
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| LAML | |||||||
| LAML | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| DLBC | |||
| GBM | |||
| KIRC | |||
| LGG | |||
| MESO | |||
| PAAD | |||
| SKCM | |||
| THYM |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| STAD | ||
| MESO | ||
| SKCM | ||
| COAD | ||
| BLCA | ||
| READ | ||
| LAML | ||
| KICH | ||
| UCEC | ||
| LIHC | ||
| LGG | ||
| OV |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000531410 | EPB41L2-228 | 2926 | - | ENSP00000434596 | 126 (aa) | - | E9PPC9 |
| ENST00000530707 | EPB41L2-225 | 565 | - | ENSP00000435556 | 118 (aa) | - | E9PJP4 |
| ENST00000526782 | EPB41L2-213 | 424 | - | - | - (aa) | - | - |
| ENST00000445890 | EPB41L2-205 | 3677 | - | ENSP00000402041 | 747 (aa) | - | O43491 |
| ENST00000456097 | EPB41L2-207 | 1138 | - | ENSP00000397580 | 380 (aa) | - | H0Y5B0 |
| ENST00000529709 | EPB41L2-222 | 585 | - | ENSP00000436871 | 179 (aa) | - | E9PQD2 |
| ENST00000628542 | EPB41L2-232 | 4247 | - | ENSP00000486691 | 935 (aa) | - | E9PHY5 |
| ENST00000639623 | EPB41L2-233 | 3395 | - | ENSP00000494672 | 824 (aa) | - | A0A2R8Y5B3 |
| ENST00000392427 | EPB41L2-204 | 3369 | - | ENSP00000376222 | 673 (aa) | - | O43491 |
| ENST00000527423 | EPB41L2-217 | 962 | - | ENSP00000437295 | 268 (aa) | - | E9PMV8 |
| ENST00000524581 | EPB41L2-208 | 3090 | - | ENSP00000437207 | 383 (aa) | - | Q6R5J7 |
| ENST00000527017 | EPB41L2-215 | 727 | - | ENSP00000432949 | 240 (aa) | - | E9PN54 |
| ENST00000534166 | EPB41L2-231 | 572 | - | - | - (aa) | - | - |
| ENST00000525271 | EPB41L2-211 | 2568 | - | ENSP00000432803 | 673 (aa) | - | O43491 |
| ENST00000528282 | EPB41L2-220 | 3663 | - | ENSP00000434308 | 747 (aa) | - | O43491 |
| ENST00000337057 | EPB41L2-201 | 4457 | XM_011535524 | ENSP00000338481 | 1005 (aa) | XP_011533826 | O43491 |
| ENST00000530148 | EPB41L2-223 | 664 | - | - | - (aa) | - | - |
| ENST00000368126 | EPB41L2-202 | 715 | - | - | - (aa) | - | - |
| ENST00000525198 | EPB41L2-210 | 981 | - | ENSP00000434998 | 224 (aa) | - | E9PMG5 |
| ENST00000530757 | EPB41L2-226 | 4360 | - | ENSP00000436349 | 201 (aa) | - | Q6ZSX4 |
| ENST00000368128 | EPB41L2-203 | 4456 | XM_017010350 | ENSP00000357110 | 1005 (aa) | XP_016865839 | O43491 |
| ENST00000525193 | EPB41L2-209 | 2121 | - | ENSP00000431988 | 706 (aa) | - | E9PII3 |
| ENST00000530481 | EPB41L2-224 | 3914 | - | ENSP00000434576 | 852 (aa) | - | O43491 |
| ENST00000531356 | EPB41L2-227 | 588 | - | ENSP00000436145 | 127 (aa) | - | E9PQN0 |
| ENST00000452150 | EPB41L2-206 | 2994 | - | - | - (aa) | - | - |
| ENST00000533912 | EPB41L2-230 | 514 | - | - | - (aa) | - | - |
| ENST00000528179 | EPB41L2-219 | 560 | - | - | - (aa) | - | - |
| ENST00000527659 | EPB41L2-218 | 2436 | - | ENSP00000431647 | 811 (aa) | - | E9PK52 |
| ENST00000526333 | EPB41L2-212 | 549 | - | - | - (aa) | - | - |
| ENST00000529208 | EPB41L2-221 | 3023 | - | ENSP00000436641 | 935 (aa) | - | E9PHY5 |
| ENST00000526983 | EPB41L2-214 | 552 | - | ENSP00000432329 | 153 (aa) | - | E9PRG1 |
| ENST00000527411 | EPB41L2-216 | 4186 | XM_011535528 | ENSP00000436348 | 935 (aa) | XP_011533830 | E9PHY5 |
| ENST00000532499 | EPB41L2-229 | 591 | - | ENSP00000432013 | 162 (aa) | - | E9PIG0 |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000079819 | Cholesterol, HDL | 3.2518174920345E-7 | 17903299 |
| ENSG00000079819 | Cholesterol, HDL | 2.17227992254415E-6 | 17903299 |
| ENSG00000079819 | Cholesterol, HDL | 5.94508334821237E-7 | 17903299 |
| ENSG00000079819 | Cholesterol, HDL | 1.79466764483281E-7 | 17903299 |
| ENSG00000079819 | CD40 Ligand | 7.92033313053052E-8 | 17903293 |
| ENSG00000079819 | Electrocardiography | 1.37426494733452E-12 | 17903302 |
| ENSG00000079819 | Electrocardiography | 2.02853586778398E-9 | 17903302 |
| ENSG00000079819 | Electrocardiography | 3.30431018060061E-8 | 17903302 |
| ENSG00000079819 | Electrocardiography | 5.25565872108497E-8 | 17903302 |
| ENSG00000079819 | Hematocrit | 4.1170000E-005 | - |
| ENSG00000079819 | Platelet Function Tests | 1.9400000E-006 | - |
| ENSG00000079819 | Platelet Function Tests | 1.7200000E-006 | - |
| ENSG00000079819 | Hydroxymethylglutaryl CoA Reductases | 2E-7 | 22331829 |
| ENSG00000079819 | Cholesterol, LDL | 2E-7 | 22331829 |
| ENSG00000079819 | Corpus Striatum | 5E-6 | 22903471 |
| ENSG00000079819 | Immunoglobulins | 2E-6 | 23382691 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000079819 | rs6921542 | 6 | 131006940 | C | Mean corpuscular volume | 27863252 | [0.018-0.034] unit decrease | 0.02573725 | EFO_0004526 |
| ENSG00000079819 | rs6908917 | 6 | 131034724 | C | IgG glycosylation | 23382691 | [0.098-0.236] unit increase | 0.1674 | EFO_0005193 |
| ENSG00000079819 | rs6941712 | 6 | 130961070 | C | Lentiform nucleus volume | 22903471 | [NR] unit decrease | 149.67 | EFO_0004913 |
| ENSG00000079819 | rs5880046 | 6 | 131005179 | GT | Heel bone mineral density | 28869591 | [0.012-0.033] unit increase | 0.0223833 | EFO_0009270 |
| ENSG00000079819 | rs5880046 | 6 | 131005179 | GT | Heel bone mineral density | 28869591 | [0.021-0.034] unit increase | 0.027655 | EFO_0009270 |
| ENSG00000079819 | rs5880046 | 6 | 131005179 | GT | Heel bone mineral density | 28869591 | [0.021-0.04] unit increase | 0.0301183 | EFO_0009270 |
| ENSG00000079819 | rs7769153 | 6 | 130935224 | ? | Response to statins (LDL cholesterol change) | 22331829 | [6.77-13.83] % increase | 10.3 | GO_0036273|EFO_0007804 |
| ENSG00000079819 | rs5880046 | 6 | 131005179 | ? | Heel bone mineral density | 30048462 | [0.023-0.032] unit increase | 0.0274138 | EFO_0009270 |
| ENSG00000079819 | rs4895901 | 6 | 130986042 | ? | Heel bone mineral density | 30048462 | [0.023-0.032] unit increase | 0.0275732 | EFO_0009270 |
| ENSG00000079819 | rs9492774 | 6 | 130981349 | C | Educational attainment (years of education) | 30038396 | [0.0051-0.0109] unit increase | 0.008 | EFO_0004784 |
| ENSG00000079819 | rs1571911 | 6 | 130872806 | C | Heel bone mineral density | 30598549 | [0.011-0.02] unit decrease | 0.0152984 | EFO_0009270 |
| ENSG00000079819 | rs4895901 | 6 | 130986042 | T | Heel bone mineral density | 30598549 | [0.027-0.035] unit increase | 0.0309682 | EFO_0009270 |
| ENSG00000079819 | rs6903705 | 6 | 131058527 | ? | Balding type 1 | 30595370 | EFO_0007825 | ||
| ENSG00000079819 | rs6903705 | 6 | 131058527 | T | Male-pattern baldness | 30573740 | [0.03-0.044] unit increase | 0.0368459 | EFO_0007825 |
| ENSG00000079819 | rs7770860 | 6 | 130865253 | T | Loneliness | 29970889 | [0.0031-0.0063] unit decrease | 0.0047 | EFO_0007865 |
| ENSG00000079819 | rs7770860 | 6 | 130865253 | T | Loneliness (MTAG) | 29970889 | [0.0087-0.0171] unit decrease | 0.012899768 | EFO_0007865 |
| ENSG00000079819 | rs9885632 | 6 | 130990769 | T | Systolic blood pressure | 30224653 | [0.16-0.26] mmHg increase | 0.2102 | EFO_0006335 |
| ENSG00000079819 | rs9885632 | 6 | 130990769 | ? | Systolic blood pressure | 30595370 | EFO_0006335 | ||
| ENSG00000079819 | rs872576 | 6 | 130846909 | ? | Neuroticism | 30595370 | EFO_0007660 | ||
| ENSG00000079819 | rs12203760 | 6 | 131028477 | ? | Mean corpuscular hemoglobin | 30595370 | EFO_0004527 | ||
| ENSG00000079819 | rs13437326 | 6 | 131050995 | ? | Heel bone mineral density | 30595370 | EFO_0009270 |
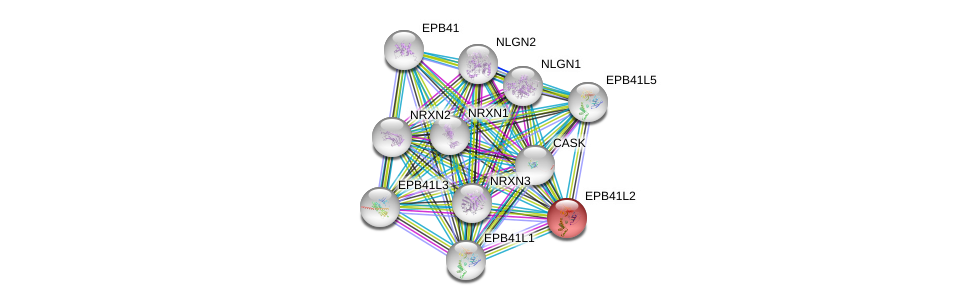
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000079819 | EPB41L2 | 99 | 94.118 | ENSMUSG00000019978 | Epb41l2 | 98 | 92.708 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0003779 | actin binding | - | IEA | Function |
| GO:0005198 | structural molecule activity | - | IEA | Function |
| GO:0005515 | protein binding | 23870127.24996901. | IPI | Function |
| GO:0005634 | nucleus | - | IDA | Component |
| GO:0005654 | nucleoplasm | - | IDA | Component |
| GO:0005829 | cytosol | - | TAS | Component |
| GO:0005886 | plasma membrane | 21873635. | IBA | Component |
| GO:0005886 | plasma membrane | - | IDA | Component |
| GO:0005925 | focal adhesion | 21423176. | HDA | Component |
| GO:0007049 | cell cycle | - | IEA | Process |
| GO:0008091 | spectrin | 9598318. | TAS | Component |
| GO:0008180 | COP9 signalosome | 18850735. | IDA | Component |
| GO:0030054 | cell junction | - | IDA | Component |
| GO:0030507 | spectrin binding | - | IEA | Function |
| GO:0030866 | cortical actin cytoskeleton organization | - | IEA | Process |
| GO:0031032 | actomyosin structure organization | 21873635. | IBA | Process |
| GO:0042731 | PH domain binding | - | IEA | Function |
| GO:0051301 | cell division | - | IEA | Process |
| GO:0070062 | extracellular exosome | 20458337. | HDA | Component |
| GO:0099738 | cell cortex region | 23870127. | IDA | Component |
| GO:1904778 | positive regulation of protein localization to cell cortex | 23870127. | IMP | Process |