
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LAML | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| DLBC | |||
| KIRC | |||
| TGCT | |||
| THCA | |||
| UCS |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| STAD | ||
| SARC | ||
| PAAD | ||
| PCPG | ||
| BLCA | ||
| CESC | ||
| LGG | ||
| LUAD |
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000360162 | ResIII | PF04851.15 | 2.1e-11 | 1 | 1 |
| ENSP00000360164 | ResIII | PF04851.15 | 2.1e-11 | 1 | 1 |
| ENSP00000360163 | ResIII | PF04851.15 | 2.1e-11 | 1 | 1 |
| ENSP00000360163 | DEAD | PF00270.29 | 3.8e-06 | 1 | 1 |
| ENSP00000360164 | DEAD | PF00270.29 | 3.8e-06 | 1 | 1 |
| ENSP00000360162 | DEAD | PF00270.29 | 3.9e-06 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000478420 | SMARCA1-204 | 561 | - | - | - (aa) | - | - |
| ENST00000371121 | SMARCA1-201 | 3564 | - | ENSP00000360162 | 1070 (aa) | - | B7ZLQ5 |
| ENST00000617310 | SMARCA1-205 | 4291 | - | - | - (aa) | - | - |
| ENST00000371123 | SMARCA1-203 | 3948 | XM_017029751 | ENSP00000360164 | 1058 (aa) | XP_016885240 | A0A0A0MRP6 |
| ENST00000371122 | SMARCA1-202 | 4099 | XM_005262461 | ENSP00000360163 | 1054 (aa) | XP_005262518 | P28370 |
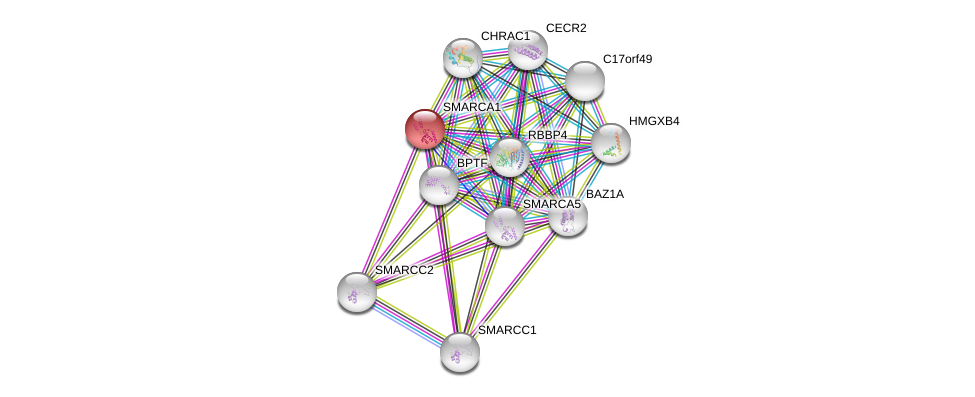
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000102038 | SMARCA1 | 92 | 83.709 | ENSAPOG00000016035 | smarca5 | 98 | 84.026 | Acanthochromis_polyacanthus |
| ENSG00000102038 | SMARCA1 | 100 | 97.009 | ENSAMEG00000015218 | SMARCA1 | 100 | 97.009 | Ailuropoda_melanoleuca |
| ENSG00000102038 | SMARCA1 | 85 | 84.053 | ENSACIG00000016982 | smarca5 | 99 | 84.152 | Amphilophus_citrinellus |
| ENSG00000102038 | SMARCA1 | 92 | 83.709 | ENSAOCG00000015578 | smarca5 | 95 | 82.762 | Amphiprion_ocellaris |
| ENSG00000102038 | SMARCA1 | 92 | 83.709 | ENSAPEG00000011117 | smarca5 | 99 | 84.080 | Amphiprion_percula |
| ENSG00000102038 | SMARCA1 | 97 | 79.550 | ENSATEG00000012894 | smarca5 | 94 | 83.714 | Anabas_testudineus |
| ENSG00000102038 | SMARCA1 | 93 | 93.279 | ENSAPLG00000013149 | SMARCA1 | 100 | 93.279 | Anas_platyrhynchos |
| ENSG00000102038 | SMARCA1 | 97 | 89.612 | ENSACAG00000011376 | SMARCA1 | 95 | 91.491 | Anolis_carolinensis |
| ENSG00000102038 | SMARCA1 | 100 | 94.802 | ENSANAG00000023098 | SMARCA1 | 100 | 94.802 | Aotus_nancymaae |
| ENSG00000102038 | SMARCA1 | 96 | 81.158 | ENSACLG00000025356 | smarca5 | 95 | 83.165 | Astatotilapia_calliptera |
| ENSG00000102038 | SMARCA1 | 88 | 88.495 | ENSAMXG00000011227 | smarca1 | 99 | 90.182 | Astyanax_mexicanus |
| ENSG00000102038 | SMARCA1 | 98 | 80.754 | ENSAMXG00000005709 | smarca5 | 94 | 84.000 | Astyanax_mexicanus |
| ENSG00000102038 | SMARCA1 | 99 | 97.450 | ENSBTAG00000002292 | SMARCA1 | 100 | 97.431 | Bos_taurus |
| ENSG00000102038 | SMARCA1 | 93 | 63.673 | WBGene00002169 | isw-1 | 97 | 63.673 | Caenorhabditis_elegans |
| ENSG00000102038 | SMARCA1 | 100 | 99.716 | ENSCJAG00000002868 | SMARCA1 | 100 | 99.716 | Callithrix_jacchus |
| ENSG00000102038 | SMARCA1 | 100 | 88.941 | ENSCAFG00000018673 | SMARCA1 | 99 | 88.824 | Canis_familiaris |
| ENSG00000102038 | SMARCA1 | 100 | 98.677 | ENSCAFG00020001751 | SMARCA1 | 100 | 98.677 | Canis_lupus_dingo |
| ENSG00000102038 | SMARCA1 | 100 | 97.549 | ENSCHIG00000009837 | SMARCA1 | 100 | 97.549 | Capra_hircus |
| ENSG00000102038 | SMARCA1 | 95 | 98.900 | ENSTSYG00000004240 | SMARCA1 | 98 | 98.269 | Carlito_syrichta |
| ENSG00000102038 | SMARCA1 | 100 | 96.015 | ENSCPOG00000013601 | SMARCA1 | 100 | 96.015 | Cavia_porcellus |
| ENSG00000102038 | SMARCA1 | 100 | 96.786 | ENSCCAG00000030817 | SMARCA1 | 100 | 96.786 | Cebus_capucinus |
| ENSG00000102038 | SMARCA1 | 100 | 100.000 | ENSCATG00000015921 | SMARCA1 | 100 | 100.000 | Cercocebus_atys |
| ENSG00000102038 | SMARCA1 | 100 | 97.070 | ENSCLAG00000002171 | SMARCA1 | 100 | 97.070 | Chinchilla_lanigera |
| ENSG00000102038 | SMARCA1 | 100 | 99.905 | ENSCSAG00000008460 | SMARCA1 | 100 | 99.905 | Chlorocebus_sabaeus |
| ENSG00000102038 | SMARCA1 | 95 | 92.707 | ENSCPBG00000001146 | SMARCA1 | 94 | 92.793 | Chrysemys_picta_bellii |
| ENSG00000102038 | SMARCA1 | 92 | 73.797 | ENSCING00000004110 | swi/snf | 97 | 73.797 | Ciona_intestinalis |
| ENSG00000102038 | SMARCA1 | 92 | 73.069 | ENSCSAVG00000004620 | - | 100 | 74.165 | Ciona_savignyi |
| ENSG00000102038 | SMARCA1 | 100 | 99.907 | ENSCANG00000007183 | SMARCA1 | 100 | 99.907 | Colobus_angolensis_palliatus |
| ENSG00000102038 | SMARCA1 | 100 | 95.940 | ENSCGRG00001010776 | Smarca1 | 98 | 96.343 | Cricetulus_griseus_chok1gshd |
| ENSG00000102038 | SMARCA1 | 95 | 95.908 | ENSCGRG00000015301 | Smarca1 | 98 | 96.382 | Cricetulus_griseus_crigri |
| ENSG00000102038 | SMARCA1 | 92 | 83.709 | ENSCSEG00000000328 | smarca5 | 95 | 83.114 | Cynoglossus_semilaevis |
| ENSG00000102038 | SMARCA1 | 93 | 83.096 | ENSCVAG00000008668 | smarca5 | 99 | 83.628 | Cyprinodon_variegatus |
| ENSG00000102038 | SMARCA1 | 93 | 85.375 | ENSDARG00000012776 | smarca1 | 97 | 85.375 | Danio_rerio |
| ENSG00000102038 | SMARCA1 | 93 | 82.727 | ENSDARG00000052348 | smarca5 | 95 | 82.727 | Danio_rerio |
| ENSG00000102038 | SMARCA1 | 98 | 96.232 | ENSDNOG00000004315 | SMARCA1 | 99 | 96.232 | Dasypus_novemcinctus |
| ENSG00000102038 | SMARCA1 | 100 | 95.351 | ENSDORG00000009270 | Smarca1 | 99 | 96.425 | Dipodomys_ordii |
| ENSG00000102038 | SMARCA1 | 93 | 72.194 | FBgn0011604 | Iswi | 98 | 72.305 | Drosophila_melanogaster |
| ENSG00000102038 | SMARCA1 | 79 | 93.750 | ENSETEG00000017426 | SMARCA1 | 86 | 93.750 | Echinops_telfairi |
| ENSG00000102038 | SMARCA1 | 93 | 80.899 | ENSEBUG00000001239 | smarca5 | 96 | 80.899 | Eptatretus_burgeri |
| ENSG00000102038 | SMARCA1 | 97 | 92.692 | ENSEASG00005008218 | SMARCA1 | 100 | 93.333 | Equus_asinus_asinus |
| ENSG00000102038 | SMARCA1 | 100 | 98.021 | ENSECAG00000012106 | SMARCA1 | 100 | 98.021 | Equus_caballus |
| ENSG00000102038 | SMARCA1 | 77 | 97.682 | ENSEEUG00000014927 | SMARCA1 | 84 | 97.682 | Erinaceus_europaeus |
| ENSG00000102038 | SMARCA1 | 94 | 86.540 | ENSELUG00000010515 | smarca1 | 98 | 86.927 | Esox_lucius |
| ENSG00000102038 | SMARCA1 | 100 | 98.677 | ENSFCAG00000018496 | SMARCA1 | 100 | 98.677 | Felis_catus |
| ENSG00000102038 | SMARCA1 | 88 | 92.324 | ENSFALG00000000209 | SMARCA1 | 98 | 93.640 | Ficedula_albicollis |
| ENSG00000102038 | SMARCA1 | 95 | 97.996 | ENSFDAG00000009818 | SMARCA1 | 98 | 97.996 | Fukomys_damarensis |
| ENSG00000102038 | SMARCA1 | 99 | 79.103 | ENSFHEG00000007687 | smarca5 | 94 | 82.828 | Fundulus_heteroclitus |
| ENSG00000102038 | SMARCA1 | 94 | 91.037 | ENSGALG00000008431 | SMARCA1 | 96 | 93.018 | Gallus_gallus |
| ENSG00000102038 | SMARCA1 | 93 | 83.503 | ENSGAFG00000017731 | smarca5 | 95 | 82.828 | Gambusia_affinis |
| ENSG00000102038 | SMARCA1 | 92 | 93.519 | ENSGAGG00000023575 | SMARCA1 | 100 | 93.519 | Gopherus_agassizii |
| ENSG00000102038 | SMARCA1 | 76 | 96.000 | ENSGGOG00000012841 | - | 98 | 96.000 | Gorilla_gorilla |
| ENSG00000102038 | SMARCA1 | 100 | 97.070 | ENSHGLG00000003080 | SMARCA1 | 100 | 97.070 | Heterocephalus_glaber_female |
| ENSG00000102038 | SMARCA1 | 94 | 97.160 | ENSHGLG00100001102 | SMARCA1 | 100 | 96.803 | Heterocephalus_glaber_male |
| ENSG00000102038 | SMARCA1 | 92 | 83.538 | ENSHCOG00000005458 | smarca5 | 95 | 82.727 | Hippocampus_comes |
| ENSG00000102038 | SMARCA1 | 95 | 85.149 | ENSIPUG00000016905 | Smarca1 | 99 | 86.925 | Ictalurus_punctatus |
| ENSG00000102038 | SMARCA1 | 97 | 80.607 | ENSIPUG00000005229 | SMARCA5 | 97 | 82.657 | Ictalurus_punctatus |
| ENSG00000102038 | SMARCA1 | 100 | 98.299 | ENSSTOG00000014524 | SMARCA1 | 100 | 98.299 | Ictidomys_tridecemlineatus |
| ENSG00000102038 | SMARCA1 | 100 | 96.143 | ENSJJAG00000002593 | Smarca1 | 100 | 96.143 | Jaculus_jaculus |
| ENSG00000102038 | SMARCA1 | 92 | 83.742 | ENSKMAG00000003777 | smarca5 | 95 | 82.929 | Kryptolebias_marmoratus |
| ENSG00000102038 | SMARCA1 | 94 | 81.637 | ENSLBEG00000018112 | smarca5 | 95 | 82.626 | Labrus_bergylta |
| ENSG00000102038 | SMARCA1 | 88 | 83.888 | ENSLBEG00000013295 | SMARCA1 | 100 | 84.829 | Labrus_bergylta |
| ENSG00000102038 | SMARCA1 | 96 | 89.250 | ENSLACG00000016697 | SMARCA1 | 98 | 90.190 | Latimeria_chalumnae |
| ENSG00000102038 | SMARCA1 | 94 | 88.855 | ENSLOCG00000014591 | smarca1 | 97 | 88.855 | Lepisosteus_oculatus |
| ENSG00000102038 | SMARCA1 | 95 | 96.720 | ENSLAFG00000000896 | SMARCA1 | 100 | 96.720 | Loxodonta_africana |
| ENSG00000102038 | SMARCA1 | 100 | 100.000 | ENSMFAG00000002117 | SMARCA1 | 100 | 100.000 | Macaca_fascicularis |
| ENSG00000102038 | SMARCA1 | 100 | 100.000 | ENSMMUG00000008818 | SMARCA1 | 100 | 100.000 | Macaca_mulatta |
| ENSG00000102038 | SMARCA1 | 100 | 100.000 | ENSMNEG00000041768 | SMARCA1 | 100 | 100.000 | Macaca_nemestrina |
| ENSG00000102038 | SMARCA1 | 100 | 99.907 | ENSMLEG00000043198 | SMARCA1 | 100 | 99.907 | Mandrillus_leucophaeus |
| ENSG00000102038 | SMARCA1 | 93 | 83.707 | ENSMAMG00000014294 | smarca5 | 96 | 82.583 | Mastacembelus_armatus |
| ENSG00000102038 | SMARCA1 | 96 | 81.158 | ENSMZEG00005009369 | smarca5 | 95 | 83.165 | Maylandia_zebra |
| ENSG00000102038 | SMARCA1 | 95 | 91.330 | ENSMGAG00000007042 | SMARCA1 | 99 | 91.494 | Meleagris_gallopavo |
| ENSG00000102038 | SMARCA1 | 100 | 96.300 | ENSMAUG00000008133 | Smarca1 | 100 | 96.300 | Mesocricetus_auratus |
| ENSG00000102038 | SMARCA1 | 100 | 98.299 | ENSMICG00000015768 | SMARCA1 | 100 | 98.299 | Microcebus_murinus |
| ENSG00000102038 | SMARCA1 | 100 | 96.110 | ENSMOCG00000009464 | Smarca1 | 100 | 96.110 | Microtus_ochrogaster |
| ENSG00000102038 | SMARCA1 | 93 | 81.231 | ENSMMOG00000005547 | smarca5 | 99 | 81.231 | Mola_mola |
| ENSG00000102038 | SMARCA1 | 98 | 89.555 | ENSMODG00000013187 | - | 99 | 89.545 | Monodelphis_domestica |
| ENSG00000102038 | SMARCA1 | 92 | 83.333 | ENSMALG00000002081 | smarca5 | 97 | 82.922 | Monopterus_albus |
| ENSG00000102038 | SMARCA1 | 100 | 95.861 | MGP_CAROLIEiJ_G0033034 | Smarca1 | 100 | 95.861 | Mus_caroli |
| ENSG00000102038 | SMARCA1 | 100 | 95.861 | ENSMUSG00000031099 | Smarca1 | 100 | 95.861 | Mus_musculus |
| ENSG00000102038 | SMARCA1 | 100 | 95.955 | MGP_PahariEiJ_G0031579 | Smarca1 | 100 | 95.955 | Mus_pahari |
| ENSG00000102038 | SMARCA1 | 100 | 95.955 | MGP_SPRETEiJ_G0034192 | Smarca1 | 100 | 95.955 | Mus_spretus |
| ENSG00000102038 | SMARCA1 | 100 | 98.224 | ENSMPUG00000017423 | SMARCA1 | 95 | 98.224 | Mustela_putorius_furo |
| ENSG00000102038 | SMARCA1 | 100 | 94.590 | ENSMLUG00000029614 | SMARCA1 | 100 | 94.030 | Myotis_lucifugus |
| ENSG00000102038 | SMARCA1 | 100 | 97.059 | ENSNGAG00000006492 | Smarca1 | 100 | 97.059 | Nannospalax_galili |
| ENSG00000102038 | SMARCA1 | 93 | 83.809 | ENSNBRG00000004463 | smarca5 | 99 | 83.131 | Neolamprologus_brichardi |
| ENSG00000102038 | SMARCA1 | 100 | 99.159 | ENSNLEG00000015179 | SMARCA1 | 100 | 99.159 | Nomascus_leucogenys |
| ENSG00000102038 | SMARCA1 | 90 | 82.038 | ENSMEUG00000008819 | SMARCA1 | 99 | 82.019 | Notamacropus_eugenii |
| ENSG00000102038 | SMARCA1 | 100 | 96.490 | ENSODEG00000012163 | SMARCA1 | 100 | 96.490 | Octodon_degus |
| ENSG00000102038 | SMARCA1 | 96 | 81.256 | ENSONIG00000009993 | smarca5 | 95 | 83.266 | Oreochromis_niloticus |
| ENSG00000102038 | SMARCA1 | 92 | 93.827 | ENSOANG00000002862 | SMARCA1 | 100 | 93.827 | Ornithorhynchus_anatinus |
| ENSG00000102038 | SMARCA1 | 100 | 96.692 | ENSOCUG00000001047 | SMARCA1 | 100 | 96.692 | Oryctolagus_cuniculus |
| ENSG00000102038 | SMARCA1 | 92 | 83.640 | ENSORLG00000021998 | smarca5 | 95 | 82.828 | Oryzias_latipes |
| ENSG00000102038 | SMARCA1 | 92 | 83.742 | ENSORLG00020017679 | smarca5 | 95 | 82.929 | Oryzias_latipes_hni |
| ENSG00000102038 | SMARCA1 | 92 | 83.640 | ENSORLG00015017210 | smarca5 | 95 | 82.727 | Oryzias_latipes_hsok |
| ENSG00000102038 | SMARCA1 | 92 | 83.640 | ENSOMEG00000000086 | smarca5 | 95 | 82.727 | Oryzias_melastigma |
| ENSG00000102038 | SMARCA1 | 100 | 98.387 | ENSOGAG00000004399 | SMARCA1 | 100 | 98.387 | Otolemur_garnettii |
| ENSG00000102038 | SMARCA1 | 95 | 97.335 | ENSOARG00000014638 | SMARCA1 | 100 | 98.878 | Ovis_aries |
| ENSG00000102038 | SMARCA1 | 100 | 100.000 | ENSPPAG00000034647 | SMARCA1 | 100 | 100.000 | Pan_paniscus |
| ENSG00000102038 | SMARCA1 | 100 | 98.677 | ENSPPRG00000008929 | SMARCA1 | 100 | 98.677 | Panthera_pardus |
| ENSG00000102038 | SMARCA1 | 95 | 97.151 | ENSPTIG00000000915 | SMARCA1 | 98 | 97.151 | Panthera_tigris_altaica |
| ENSG00000102038 | SMARCA1 | 100 | 100.000 | ENSPTRG00000049876 | SMARCA1 | 100 | 100.000 | Pan_troglodytes |
| ENSG00000102038 | SMARCA1 | 100 | 100.000 | ENSPANG00000003871 | SMARCA1 | 100 | 100.000 | Papio_anubis |
| ENSG00000102038 | SMARCA1 | 93 | 85.816 | ENSPKIG00000013411 | smarca1 | 98 | 87.124 | Paramormyrops_kingsleyae |
| ENSG00000102038 | SMARCA1 | 95 | 91.807 | ENSPSIG00000010101 | SMARCA1 | 100 | 93.210 | Pelodiscus_sinensis |
| ENSG00000102038 | SMARCA1 | 100 | 96.964 | ENSPEMG00000017503 | Smarca1 | 100 | 96.964 | Peromyscus_maniculatus_bairdii |
| ENSG00000102038 | SMARCA1 | 95 | 92.108 | ENSPCIG00000015460 | SMARCA1 | 98 | 92.192 | Phascolarctos_cinereus |
| ENSG00000102038 | SMARCA1 | 92 | 83.742 | ENSPFOG00000007649 | smarca5 | 95 | 82.828 | Poecilia_formosa |
| ENSG00000102038 | SMARCA1 | 92 | 83.742 | ENSPLAG00000003363 | smarca5 | 95 | 82.828 | Poecilia_latipinna |
| ENSG00000102038 | SMARCA1 | 92 | 83.640 | ENSPMEG00000019849 | smarca5 | 95 | 82.727 | Poecilia_mexicana |
| ENSG00000102038 | SMARCA1 | 92 | 83.640 | ENSPREG00000023250 | smarca5 | 95 | 82.727 | Poecilia_reticulata |
| ENSG00000102038 | SMARCA1 | 100 | 97.259 | ENSPPYG00000020703 | SMARCA1 | 100 | 97.259 | Pongo_abelii |
| ENSG00000102038 | SMARCA1 | 78 | 90.909 | ENSPCOG00000020722 | SMARCA1 | 94 | 93.539 | Propithecus_coquereli |
| ENSG00000102038 | SMARCA1 | 94 | 97.194 | ENSPVAG00000003805 | SMARCA1 | 94 | 97.297 | Pteropus_vampyrus |
| ENSG00000102038 | SMARCA1 | 56 | 84.384 | ENSPNYG00000012299 | smarca5 | 92 | 82.933 | Pundamilia_nyererei |
| ENSG00000102038 | SMARCA1 | 100 | 96.408 | ENSRNOG00000003762 | Smarca1 | 100 | 96.408 | Rattus_norvegicus |
| ENSG00000102038 | SMARCA1 | 100 | 99.907 | ENSRROG00000034167 | SMARCA1 | 100 | 99.907 | Rhinopithecus_roxellana |
| ENSG00000102038 | SMARCA1 | 96 | 98.258 | ENSSBOG00000020641 | SMARCA1 | 100 | 99.796 | Saimiri_boliviensis_boliviensis |
| ENSG00000102038 | SMARCA1 | 92 | 86.742 | ENSSHAG00000013518 | SMARCA1 | 99 | 86.742 | Sarcophilus_harrisii |
| ENSG00000102038 | SMARCA1 | 98 | 85.314 | ENSSFOG00015009043 | smarca1 | 98 | 87.675 | Scleropages_formosus |
| ENSG00000102038 | SMARCA1 | 95 | 82.154 | ENSSFOG00015016794 | smarca5 | 100 | 83.814 | Scleropages_formosus |
| ENSG00000102038 | SMARCA1 | 93 | 82.371 | ENSSMAG00000004801 | smarca5 | 95 | 82.371 | Scophthalmus_maximus |
| ENSG00000102038 | SMARCA1 | 93 | 83.198 | ENSSDUG00000020690 | smarca5 | 96 | 82.525 | Seriola_dumerili |
| ENSG00000102038 | SMARCA1 | 93 | 83.198 | ENSSLDG00000025190 | smarca5 | 96 | 82.525 | Seriola_lalandi_dorsalis |
| ENSG00000102038 | SMARCA1 | 87 | 90.399 | ENSSARG00000000842 | SMARCA1 | 92 | 90.399 | Sorex_araneus |
| ENSG00000102038 | SMARCA1 | 95 | 90.572 | ENSSPUG00000000590 | SMARCA1 | 94 | 92.103 | Sphenodon_punctatus |
| ENSG00000102038 | SMARCA1 | 93 | 83.299 | ENSSPAG00000002894 | smarca5 | 97 | 84.026 | Stegastes_partitus |
| ENSG00000102038 | SMARCA1 | 98 | 97.784 | ENSSSCG00000012649 | SMARCA1 | 99 | 97.784 | Sus_scrofa |
| ENSG00000102038 | SMARCA1 | 93 | 92.770 | ENSTGUG00000003899 | - | 100 | 92.770 | Taeniopygia_guttata |
| ENSG00000102038 | SMARCA1 | 93 | 83.401 | ENSTRUG00000014094 | smarca5 | 95 | 82.727 | Takifugu_rubripes |
| ENSG00000102038 | SMARCA1 | 92 | 82.582 | ENSTNIG00000017717 | smarca5 | 94 | 81.616 | Tetraodon_nigroviridis |
| ENSG00000102038 | SMARCA1 | 94 | 91.365 | ENSTBEG00000014973 | SMARCA1 | 100 | 91.365 | Tupaia_belangeri |
| ENSG00000102038 | SMARCA1 | 94 | 95.354 | ENSTTRG00000006168 | SMARCA1 | 100 | 95.354 | Tursiops_truncatus |
| ENSG00000102038 | SMARCA1 | 100 | 98.110 | ENSUAMG00000020201 | SMARCA1 | 100 | 98.110 | Ursus_americanus |
| ENSG00000102038 | SMARCA1 | 95 | 94.071 | ENSUMAG00000004073 | SMARCA1 | 97 | 98.783 | Ursus_maritimus |
| ENSG00000102038 | SMARCA1 | 79 | 99.683 | ENSVPAG00000010492 | - | 86 | 99.683 | Vicugna_pacos |
| ENSG00000102038 | SMARCA1 | 95 | 99.000 | ENSVVUG00000008878 | SMARCA1 | 99 | 99.060 | Vulpes_vulpes |
| ENSG00000102038 | SMARCA1 | 94 | 89.347 | ENSXETG00000001526 | smarca1 | 99 | 89.347 | Xenopus_tropicalis |
| ENSG00000102038 | SMARCA1 | 93 | 83.401 | ENSXCOG00000011170 | smarca5 | 98 | 82.727 | Xiphophorus_couchianus |
| ENSG00000102038 | SMARCA1 | 93 | 83.401 | ENSXMAG00000009678 | smarca5 | 97 | 84.978 | Xiphophorus_maculatus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000733 | DNA strand renaturation | - | IEA | Process |
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | - | ISA | Function |
| GO:0003677 | DNA binding | - | IEA | Function |
| GO:0004386 | helicase activity | - | IEA | Function |
| GO:0005515 | protein binding | 14609955.15640247. | IPI | Function |
| GO:0005524 | ATP binding | - | IEA | Function |
| GO:0005634 | nucleus | 14609955. | IDA | Component |
| GO:0005654 | nucleoplasm | - | IDA | Component |
| GO:0006338 | chromatin remodeling | 14609955. | IDA | Process |
| GO:0007420 | brain development | 14609955. | IMP | Process |
| GO:0008094 | DNA-dependent ATPase activity | 14609955. | IDA | Function |
| GO:0008134 | transcription factor binding | 27141965. | IPI | Function |
| GO:0016589 | NURF complex | 20850016. | IDA | Component |
| GO:0030182 | neuron differentiation | - | ISS | Process |
| GO:0031491 | nucleosome binding | - | IEA | Function |
| GO:0036310 | annealing helicase activity | 22705370. | IDA | Function |
| GO:0043044 | ATP-dependent chromatin remodeling | 15640247. | IDA | Process |
| GO:0043231 | intracellular membrane-bounded organelle | - | IDA | Component |
| GO:0045893 | positive regulation of transcription, DNA-templated | 14609955. | IMP | Process |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 14609955. | IMP | Process |
| GO:0070615 | nucleosome-dependent ATPase activity | 15640247. | IDA | Function |
| GO:0090537 | CERF complex | 15640247. | IDA | Component |