
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| READ | |||
| UCS |
| Cancer | P-value | Q-value |
|---|---|---|
| THYM | ||
| KIRC | ||
| SARC | ||
| MESO | ||
| ACC | ||
| SKCM | ||
| LUSC | ||
| KIRP | ||
| COAD | ||
| PAAD | ||
| CESC | ||
| READ | ||
| KICH | ||
| UCEC | ||
| LIHC | ||
| LGG | ||
| THCA | ||
| LUAD | ||
| UVM |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000520994 | MCM4-210 | 522 | - | - | - (aa) | - | - |
| ENST00000521261 | MCM4-212 | 1342 | - | - | - (aa) | - | - |
| ENST00000519138 | MCM4-206 | 927 | - | - | - (aa) | - | - |
| ENST00000648554 | MCM4-220 | 755 | - | ENSP00000496985 | 191 (aa) | - | - |
| ENST00000521151 | MCM4-211 | 1125 | - | - | - (aa) | - | - |
| ENST00000519170 | MCM4-207 | 734 | - | - | - (aa) | - | - |
| ENST00000523944 | MCM4-214 | 4105 | - | ENSP00000430194 | 863 (aa) | - | P33991 |
| ENST00000517709 | MCM4-202 | 842 | - | - | - (aa) | - | - |
| ENST00000524086 | MCM4-215 | 547 | - | ENSP00000427829 | 81 (aa) | - | E5RG53 |
| ENST00000648407 | MCM4-217 | 2598 | - | ENSP00000497881 | 742 (aa) | - | - |
| ENST00000262105 | MCM4-201 | 4183 | - | ENSP00000262105 | 863 (aa) | - | P33991 |
| ENST00000519470 | MCM4-208 | 498 | - | - | - (aa) | - | - |
| ENST00000518221 | MCM4-203 | 572 | - | ENSP00000430329 | 140 (aa) | - | E5RFR3 |
| ENST00000649919 | MCM4-222 | 2957 | - | ENSP00000498202 | 813 (aa) | - | UPI000387DE53 |
| ENST00000520637 | MCM4-209 | 1981 | - | ENSP00000427875 | 582 (aa) | - | E5RG31 |
| ENST00000649838 | MCM4-221 | 3157 | - | ENSP00000497648 | 904 (aa) | - | - |
| ENST00000649973 | MCM4-223 | 4062 | - | ENSP00000496964 | 863 (aa) | - | UPI000013D25C |
| ENST00000518382 | MCM4-204 | 366 | - | ENSP00000430864 | 27 (aa) | - | E5RHP5 |
| ENST00000650327 | MCM4-225 | 235 | - | - | - (aa) | - | - |
| ENST00000650216 | MCM4-224 | 2399 | - | ENSP00000497093 | 749 (aa) | - | - |
| ENST00000647877 | MCM4-216 | 1256 | - | ENSP00000497251 | 107 (aa) | - | - |
| ENST00000523853 | MCM4-213 | 354 | - | - | - (aa) | - | - |
| ENST00000648519 | MCM4-218 | 3226 | - | ENSP00000497176 | 160 (aa) | - | - |
| ENST00000648533 | MCM4-219 | 733 | - | - | - (aa) | - | - |
| ENST00000518680 | MCM4-205 | 862 | - | - | - (aa) | - | - |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000104738 | rs762679 | 8 | 47972876 | A | Red blood cell count | 27863252 | [0.022-0.042] unit decrease | 0.03194922 | EFO_0004305 |
| ENSG00000104738 | rs762679 | 8 | 47972876 | A | Mean corpuscular volume | 27863252 | [0.025-0.044] unit increase | 0.03467907 | EFO_0004526 |
| ENSG00000104738 | rs762679 | 8 | 47972876 | ? | Mean corpuscular hemoglobin | 30595370 | EFO_0004527 | ||
| ENSG00000104738 | rs762679 | 8 | 47972876 | ? | Eosinophil counts | 30595370 | EFO_0004842 |
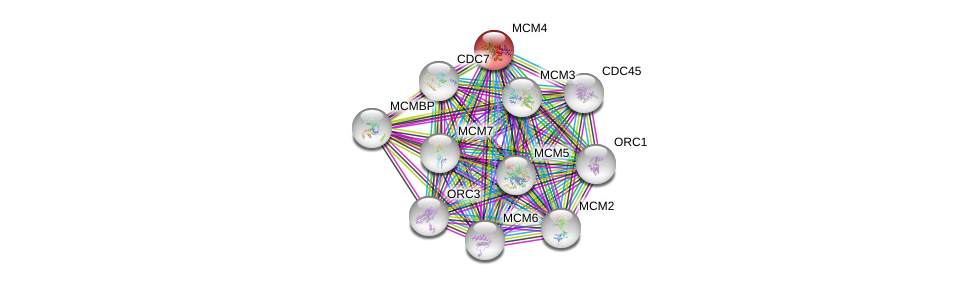
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000104738 | MCM4 | 99 | 68.220 | FBgn0015929 | dpa | 99 | 61.469 | Drosophila_melanogaster |
| ENSG00000104738 | MCM4 | 90 | 47.701 | FBgn0014861 | Mcm2 | 67 | 33.651 | Drosophila_melanogaster |
| ENSG00000104738 | MCM4 | 89 | 50.000 | ENSG00000073111 | MCM2 | 83 | 40.556 | Homo_sapiens |
| ENSG00000104738 | MCM4 | 86 | 66.667 | YPR019W | MCM4 | 80 | 47.397 | Saccharomyces_cerevisiae |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000082 | G1/S transition of mitotic cell cycle | - | TAS | Process |
| GO:0000784 | nuclear chromosome, telomeric region | 19135898. | HDA | Component |
| GO:0003697 | single-stranded DNA binding | - | IEA | Function |
| GO:0004003 | ATP-dependent DNA helicase activity | 9305914. | IDA | Function |
| GO:0005515 | protein binding | 12364596.15232106.16902406.17296731.22190034.22540012.23764002.24299456.24407287.25036637. | IPI | Function |
| GO:0005524 | ATP binding | - | IEA | Function |
| GO:0005634 | nucleus | 8265339. | NAS | Component |
| GO:0005654 | nucleoplasm | - | IDA | Component |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0006260 | DNA replication | 9465298. | NAS | Process |
| GO:0006260 | DNA replication | - | TAS | Process |
| GO:0006268 | DNA unwinding involved in DNA replication | - | IEA | Process |
| GO:0006270 | DNA replication initiation | - | IEA | Process |
| GO:0016020 | membrane | 19946888. | HDA | Component |
| GO:0042555 | MCM complex | 17296731. | IDA | Component |