
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LAML | |||||||
| LAML | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PCPG | |||||||
| PCPG | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| KIRP | |||
| PAAD |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| STAD | ||
| MESO | ||
| HNSC | ||
| BRCA | ||
| ESCA | ||
| KIRP | ||
| CESC | ||
| LAML | ||
| GBM | ||
| LUAD | ||
| UVM |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000438462 | RTN4-211 | 656 | - | ENSP00000397808 | 203 (aa) | - | H7C106 |
| ENST00000491592 | RTN4-215 | 860 | - | - | - (aa) | - | - |
| ENST00000357376 | RTN4-203 | 4110 | - | ENSP00000349944 | 986 (aa) | - | Q9NQC3 |
| ENST00000486085 | RTN4-214 | 955 | - | ENSP00000489133 | 127 (aa) | - | A0A0U1RQR6 |
| ENST00000485749 | RTN4-213 | 832 | - | - | - (aa) | - | - |
| ENST00000337526 | RTN4-202 | 4790 | - | ENSP00000337838 | 1192 (aa) | - | Q9NQC3 |
| ENST00000394609 | RTN4-205 | 1898 | - | ENSP00000378107 | 199 (aa) | - | Q9NQC3 |
| ENST00000357732 | RTN4-204 | 2390 | - | ENSP00000350365 | 392 (aa) | - | Q9NQC3 |
| ENST00000317610 | RTN4-201 | 2333 | - | ENSP00000322147 | 373 (aa) | - | Q9NQC3 |
| ENST00000402434 | RTN4-207 | 1456 | - | ENSP00000384825 | 345 (aa) | - | F8W914 |
| ENST00000405240 | RTN4-209 | 4061 | - | ENSP00000384471 | 986 (aa) | - | Q9NQC3 |
| ENST00000394611 | RTN4-206 | 4161 | - | ENSP00000378109 | 986 (aa) | - | Q9NQC3 |
| ENST00000427710 | RTN4-210 | 589 | - | ENSP00000411628 | 91 (aa) | - | C9J685 |
| ENST00000461004 | RTN4-212 | 422 | - | - | - (aa) | - | - |
| ENST00000404909 | RTN4-208 | 4102 | - | ENSP00000385650 | 986 (aa) | - | Q9NQC3 |
| Pathway ID | Pathway Name | Source |
|---|---|---|
| hsa05010 | Alzheimer disease | KEGG |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000115310 | Cholesterol, HDL | 4.33236853163432E-5 | 17903299 |
| ENSG00000115310 | Lipids | 5.81981414238621E-5 | 17903299 |
| ENSG00000115310 | Choice Behavior | 5.38e-005 | - |
| ENSG00000115310 | Antihypertensive Agents | 6.9390000E-005 | - |
| ENSG00000115310 | Antihypertensive Agents | 7.4970000E-006 | - |
| ENSG00000115310 | Cholesterol, HDL | 4.1790000E-005 | - |
| ENSG00000115310 | Cholesterol, HDL | 3.8770000E-005 | - |
| ENSG00000115310 | Cholesterol, HDL | 2.5150000E-005 | - |
| ENSG00000115310 | Cholesterol, HDL | 4.0980000E-006 | - |
| ENSG00000115310 | Triglycerides | 4.7880000E-005 | - |
| ENSG00000115310 | Platelet Function Tests | 3.6900000E-006 | - |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000115310 | rs2920861 | 2 | 55090980 | A | Self-reported math ability (MTAG) | 30038396 | [0.011-0.023] unit increase | 0.017 | EFO_0004875 |
| ENSG00000115310 | rs3806572 | 2 | 55011541 | A | Major depressive disorder (probable) | 29662059 | [0.0043-0.0097] unit decrease | 0.007 | EFO_0003761 |
| ENSG00000115310 | rs7601895 | 2 | 55054765 | ? | Body mass index | 30595370 | EFO_0004340 | ||
| ENSG00000115310 | rs12479297 | 2 | 55044445 | ? | Red cell distribution width | 30595370 | EFO_0005192 | ||
| ENSG00000115310 | rs2920899 | 2 | 55052545 | T | Systolic blood pressure | 30224653 | [0.13-0.24] mmHg increase | 0.1851 | EFO_0006335 |
| ENSG00000115310 | rs6545468 | 2 | 55050505 | ? | Mean corpuscular hemoglobin | 30595370 | EFO_0004527 |
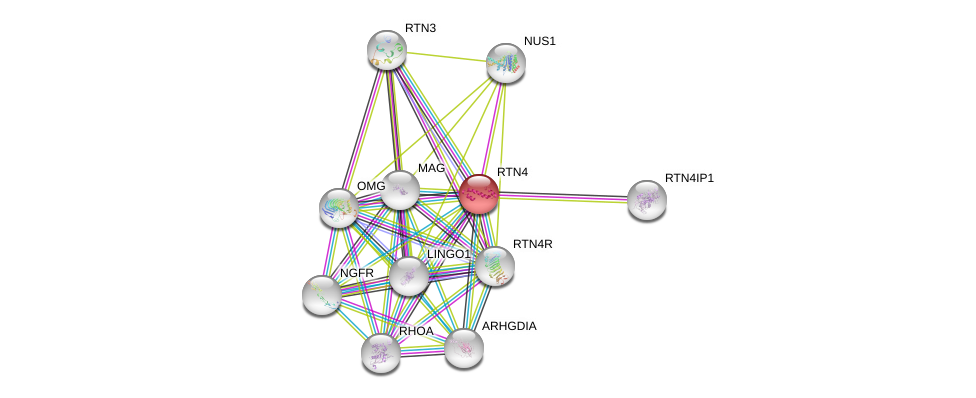
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000115310 | RTN4 | 100 | 97.487 | ENSMUSG00000020458 | Rtn4 | 100 | 97.487 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0001825 | blastocyst formation | - | IEA | Process |
| GO:0003723 | RNA binding | 22658674. | HDA | Function |
| GO:0005515 | protein binding | 11126360.16752908.19665976.21516116.25416956.26906412. | IPI | Function |
| GO:0005635 | nuclear envelope | 11126360. | IDA | Component |
| GO:0005783 | endoplasmic reticulum | 16791210. | HDA | Component |
| GO:0005783 | endoplasmic reticulum | - | IDA | Component |
| GO:0005783 | endoplasmic reticulum | 11126360. | NAS | Component |
| GO:0005789 | endoplasmic reticulum membrane | 25612671.26906412. | IDA | Component |
| GO:0005886 | plasma membrane | - | TAS | Component |
| GO:0006915 | apoptotic process | 11126360. | NAS | Process |
| GO:0007413 | axonal fasciculation | 21873635. | IBA | Process |
| GO:0007413 | axonal fasciculation | - | ISS | Process |
| GO:0010634 | positive regulation of epithelial cell migration | 27353365. | IMP | Process |
| GO:0014069 | postsynaptic density | - | IEA | Component |
| GO:0021801 | cerebral cortex radial glia guided migration | - | ISS | Process |
| GO:0030054 | cell junction | - | IEA | Component |
| GO:0030176 | integral component of endoplasmic reticulum membrane | 10667797. | IDA | Component |
| GO:0030308 | negative regulation of cell growth | 20463223. | IMP | Process |
| GO:0030517 | negative regulation of axon extension | 10667797. | IDA | Process |
| GO:0031625 | ubiquitin protein ligase binding | 27353365. | IPI | Function |
| GO:0033601 | positive regulation of mammary gland epithelial cell proliferation | 27353365. | IMP | Process |
| GO:0034165 | positive regulation of toll-like receptor 9 signaling pathway | - | ISS | Process |
| GO:0042981 | regulation of apoptotic process | 11126360. | NAS | Process |
| GO:0042995 | cell projection | - | IEA | Component |
| GO:0043025 | neuronal cell body | - | IEA | Component |
| GO:0045296 | cadherin binding | 25468996. | HDA | Function |
| GO:0050771 | negative regulation of axonogenesis | - | TAS | Process |
| GO:0050821 | protein stabilization | 27353365. | IMP | Process |
| GO:0051292 | nuclear pore complex assembly | 26906412. | IMP | Process |
| GO:0051897 | positive regulation of protein kinase B signaling | 27353365. | IMP | Process |
| GO:0060317 | cardiac epithelial to mesenchymal transition | - | IEA | Process |
| GO:0061462 | protein localization to lysosome | - | ISS | Process |
| GO:0071782 | endoplasmic reticulum tubular network | 27353365. | IDA | Component |
| GO:0071786 | endoplasmic reticulum tubular network organization | 18779370.26906412. | IMP | Process |
| GO:0071787 | endoplasmic reticulum tubular network formation | 24262037.25612671. | IDA | Process |
| GO:0090156 | cellular sphingolipid homeostasis | - | IEA | Process |
| GO:0098826 | endoplasmic reticulum tubular network membrane | 27619977. | IDA | Component |
| GO:1905552 | positive regulation of protein localization to endoplasmic reticulum | 27353365. | IDA | Process |
| GO:1905580 | positive regulation of ERBB3 signaling pathway | 27353365. | IMP | Process |
| GO:1990809 | endoplasmic reticulum tubular network membrane organization | 27619977. | IMP | Process |
| GO:2000172 | regulation of branching morphogenesis of a nerve | - | ISS | Process |