
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRP | |||||||
| LAML | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| THCA | |||||||
| THYM | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| DLBC | |||
| ESCA | |||
| KIRC | |||
| PAAD | |||
| READ | |||
| SKCM | |||
| TGCT | |||
| UCEC | |||
| UCS |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| MESO | ||
| ACC | ||
| LUSC | ||
| BRCA | ||
| ESCA | ||
| COAD | ||
| CESC | ||
| KICH | ||
| UCEC | ||
| LIHC | ||
| THCA | ||
| LUAD |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000470541 | ARHGEF2-208 | 1877 | - | ENSP00000476689 | 263 (aa) | - | V9GYF0 |
| ENST00000474428 | ARHGEF2-212 | 742 | - | - | - (aa) | - | - |
| ENST00000609126 | ARHGEF2-219 | 490 | - | - | - (aa) | - | - |
| ENST00000495070 | ARHGEF2-216 | 571 | - | ENSP00000476532 | 83 (aa) | - | V9GY94 |
| ENST00000609707 | ARHGEF2-220 | 692 | - | ENSP00000476699 | 178 (aa) | - | V9GYF5 |
| ENST00000368315 | ARHGEF2-204 | 1645 | - | ENSP00000357298 | 264 (aa) | - | Q5VY93 |
| ENST00000497907 | ARHGEF2-217 | 764 | - | ENSP00000476724 | 214 (aa) | - | V9GYG5 |
| ENST00000465079 | ARHGEF2-207 | 693 | - | - | - (aa) | - | - |
| ENST00000470874 | ARHGEF2-209 | 372 | - | ENSP00000477448 | 59 (aa) | - | V9GZ58 |
| ENST00000462460 | ARHGEF2-206 | 4438 | XM_011510136 | ENSP00000476916 | 1031 (aa) | XP_011508438 | V9GYM8 |
| ENST00000313695 | ARHGEF2-202 | 4080 | XM_005245589 | ENSP00000315325 | 958 (aa) | XP_005245646 | Q92974 |
| ENST00000608543 | ARHGEF2-218 | 820 | - | - | - (aa) | - | - |
| ENST00000423422 | ARHGEF2-205 | 420 | - | ENSP00000476518 | 7 (aa) | - | A0A1Y8EN19 |
| ENST00000470975 | ARHGEF2-210 | 638 | - | - | - (aa) | - | - |
| ENST00000361247 | ARHGEF2-203 | 4149 | XM_005245587 | ENSP00000354837 | 986 (aa) | XP_005245644 | Q92974 |
| ENST00000477754 | ARHGEF2-214 | 883 | - | - | - (aa) | - | - |
| ENST00000487755 | ARHGEF2-215 | 2176 | - | - | - (aa) | - | - |
| ENST00000313667 | ARHGEF2-201 | 2958 | XM_005245588 | ENSP00000314787 | 985 (aa) | XP_005245645 | Q92974 |
| ENST00000476273 | ARHGEF2-213 | 668 | - | - | - (aa) | - | - |
| ENST00000471589 | ARHGEF2-211 | 892 | - | ENSP00000477299 | 229 (aa) | - | V9GZ14 |
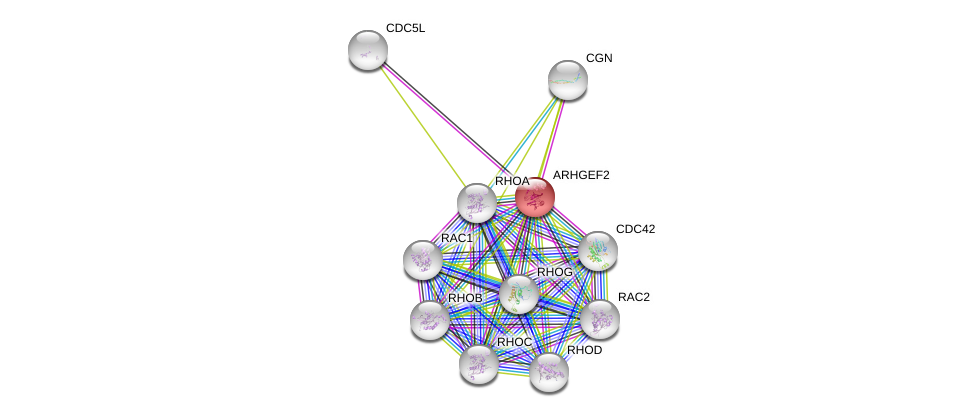
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000132 | establishment of mitotic spindle orientation | - | IEA | Process |
| GO:0000902 | cell morphogenesis | 11912491. | IMP | Process |
| GO:0002102 | podosome | - | IEA | Component |
| GO:0005089 | Rho guanyl-nucleotide exchange factor activity | 9857026. | IDA | Function |
| GO:0005515 | protein binding | 14970201.15161933.19043560.21887730.25416956.25609649. | IPI | Function |
| GO:0005737 | cytoplasm | 21887730. | IDA | Component |
| GO:0005794 | Golgi apparatus | - | IEA | Component |
| GO:0005819 | spindle | - | IEA | Component |
| GO:0005829 | cytosol | - | TAS | Component |
| GO:0005856 | cytoskeleton | 21887730. | IDA | Component |
| GO:0005874 | microtubule | 9857026. | IDA | Component |
| GO:0005923 | bicellular tight junction | - | IEA | Component |
| GO:0005925 | focal adhesion | 21423176. | HDA | Component |
| GO:0006886 | intracellular protein transport | 9857026. | NAS | Process |
| GO:0007015 | actin filament organization | 9857026. | IMP | Process |
| GO:0007026 | negative regulation of microtubule depolymerization | 11912491. | IMP | Process |
| GO:0007186 | G protein-coupled receptor signaling pathway | - | TAS | Process |
| GO:0008017 | microtubule binding | 9857026. | IDA | Function |
| GO:0008134 | transcription factor binding | - | ISS | Function |
| GO:0008270 | zinc ion binding | 11912491. | NAS | Function |
| GO:0017048 | Rho GTPase binding | 9857026. | IDA | Function |
| GO:0030676 | Rac guanyl-nucleotide exchange factor activity | 9857026. | IDA | Function |
| GO:0031410 | cytoplasmic vesicle | - | IEA | Component |
| GO:0031982 | vesicle | 21887730. | IDA | Component |
| GO:0032587 | ruffle membrane | 19043560. | IDA | Component |
| GO:0032755 | positive regulation of interleukin-6 production | 21887730. | IDA | Process |
| GO:0032760 | positive regulation of tumor necrosis factor production | 21887730. | IDA | Process |
| GO:0032991 | protein-containing complex | 21887730. | IDA | Component |
| GO:0035023 | regulation of Rho protein signal transduction | 11912491. | NAS | Process |
| GO:0035556 | intracellular signal transduction | - | IEA | Process |
| GO:0042127 | regulation of cell proliferation | 9857026. | TAS | Process |
| GO:0043025 | neuronal cell body | - | IEA | Component |
| GO:0043065 | positive regulation of apoptotic process | - | TAS | Process |
| GO:0043198 | dendritic shaft | - | IEA | Component |
| GO:0045087 | innate immune response | - | IEA | Process |
| GO:0045666 | positive regulation of neuron differentiation | 28453519. | IDA | Process |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 21887730. | IDA | Process |
| GO:0048365 | Rac GTPase binding | 9857026. | IDA | Function |
| GO:0050731 | positive regulation of peptidyl-tyrosine phosphorylation | 21887730. | IDA | Process |
| GO:0050768 | negative regulation of neurogenesis | - | IEA | Process |
| GO:0051056 | regulation of small GTPase mediated signal transduction | - | TAS | Process |
| GO:0051092 | positive regulation of NF-kappaB transcription factor activity | 19043560.21887730. | IDA | Process |
| GO:0055059 | asymmetric neuroblast division | 28453519. | IDA | Process |
| GO:0060546 | negative regulation of necroptotic process | - | ISS | Process |
| GO:0071225 | cellular response to muramyl dipeptide | 21887730. | IDA | Process |
| GO:0071356 | cellular response to tumor necrosis factor | - | ISS | Process |
| GO:0071474 | cellular hyperosmotic response | - | ISS | Process |
| GO:0071802 | negative regulation of podosome assembly | - | IEA | Process |
| GO:0098978 | glutamatergic synapse | - | IEA | Component |
| GO:0099092 | postsynaptic density, intracellular component | - | IEA | Component |
| GO:1902042 | negative regulation of extrinsic apoptotic signaling pathway via death domain receptors | - | ISS | Process |
| GO:1902219 | negative regulation of intrinsic apoptotic signaling pathway in response to osmotic stress | - | ISS | Process |
| GO:2001224 | positive regulation of neuron migration | - | ISS | Process |