
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| CHOL | |||
| LAML | |||
| PCPG | |||
| THCA | |||
| THYM | |||
| UCEC | |||
| UCS |
| Cancer | P-value | Q-value |
|---|---|---|
| STAD | ||
| HNSC | ||
| SKCM | ||
| KIRP | ||
| PAAD | ||
| LAML | ||
| LGG | ||
| CHOL | ||
| THCA | ||
| OV |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000606364 | TJP2-210 | 591 | - | ENSP00000475926 | 134 (aa) | - | U3KQJ2 |
| ENST00000636438 | TJP2-212 | 4689 | - | ENSP00000489860 | 1249 (aa) | - | A0A1B0GTW1 |
| ENST00000648153 | TJP2-217 | 573 | - | - | - (aa) | - | - |
| ENST00000649927 | TJP2-225 | 3374 | - | - | - (aa) | - | - |
| ENST00000648204 | TJP2-218 | 4725 | - | ENSP00000497941 | 1190 (aa) | - | UPI0000141800 |
| ENST00000636247 | TJP2-211 | 3725 | - | - | - (aa) | - | - |
| ENST00000648087 | TJP2-216 | 5085 | - | - | - (aa) | - | - |
| ENST00000348208 | TJP2-201 | 4055 | - | ENSP00000345893 | 1043 (aa) | - | Q9UDY2 |
| ENST00000539225 | TJP2-209 | 3838 | - | ENSP00000438262 | 1221 (aa) | - | Q9UDY2 |
| ENST00000650353 | TJP2-230 | 3282 | - | - | - (aa) | - | - |
| ENST00000649943 | TJP2-227 | 5672 | - | ENSP00000497539 | 1099 (aa) | - | - |
| ENST00000498204 | TJP2-207 | 4685 | - | - | - (aa) | - | - |
| ENST00000377259 | TJP2-203 | 588 | - | - | - (aa) | - | - |
| ENST00000535702 | TJP2-208 | 3984 | - | ENSP00000442090 | 1157 (aa) | - | Q9UDY2 |
| ENST00000643713 | TJP2-213 | 490 | - | ENSP00000494704 | 5 (aa) | - | UPI000D1943BE |
| ENST00000648460 | TJP2-220 | 611 | - | - | - (aa) | - | - |
| ENST00000413932 | TJP2-204 | 822 | - | - | - (aa) | - | - |
| ENST00000648402 | TJP2-219 | 1483 | - | ENSP00000497596 | 134 (aa) | - | UPI00038BB0BE |
| ENST00000423935 | TJP2-205 | 869 | - | ENSP00000402941 | 161 (aa) | - | B1AN86 |
| ENST00000650460 | TJP2-232 | 2851 | - | ENSP00000497787 | 621 (aa) | - | - |
| ENST00000649134 | TJP2-223 | 3964 | XM_017015328 | ENSP00000498068 | 1047 (aa) | XP_016870817 | UPI0007DC57BD |
| ENST00000650084 | TJP2-228 | 4389 | XM_005252314 | ENSP00000497861 | 1191 (aa) | XP_005252371 | - |
| ENST00000649114 | TJP2-222 | 5344 | - | ENSP00000497328 | 989 (aa) | - | - |
| ENST00000650522 | TJP2-233 | 3774 | - | - | - (aa) | - | - |
| ENST00000650378 | TJP2-231 | 629 | - | - | - (aa) | - | - |
| ENST00000649939 | TJP2-226 | 597 | - | ENSP00000498043 | 156 (aa) | - | - |
| ENST00000650333 | TJP2-229 | 3612 | - | ENSP00000496791 | 1128 (aa) | - | - |
| ENST00000649783 | TJP2-224 | 4264 | - | - | - (aa) | - | - |
| ENST00000648042 | TJP2-215 | 2771 | - | ENSP00000497059 | 652 (aa) | - | - |
| ENST00000647986 | TJP2-214 | 2868 | - | ENSP00000496877 | 851 (aa) | - | - |
| ENST00000648862 | TJP2-221 | 464 | - | - | - (aa) | - | - |
| ENST00000453658 | TJP2-206 | 4129 | XM_011519204 | ENSP00000392178 | 1020 (aa) | XP_011517506 | Q9UDY2 |
| ENST00000377245 | TJP2-202 | 4503 | XM_011519206 | ENSP00000366453 | 1190 (aa) | XP_011517508 | Q9UDY2 |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000119139 | Cholesterol | 3.51876109508958E-5 | 17903299 |
| ENSG00000119139 | Cholesterol, LDL | 7.6855409045791E-5 | 17903299 |
| ENSG00000119139 | Platelet Function Tests | 8.7621739E-007 | - |
| ENSG00000119139 | Platelet Function Tests | 5.7002085E-006 | - |
| ENSG00000119139 | Platelet Function Tests | 1.5512040E-012 | - |
| ENSG00000119139 | Child Development Disorders, Pervasive | 1.1942000E-005 | - |
| ENSG00000119139 | Child Development Disorders, Pervasive | 1.9014000E-006 | - |
| ENSG00000119139 | Glioma | 1.3870000E-005 | - |
| ENSG00000119139 | Adipose Tissue | 4E-6 | 22044751 |
| ENSG00000119139 | Seasonal Affective Disorder | 9E-6 | 25562672 |
| ENSG00000119139 | Myopia | 7E-21 | 27182965 |
| ENSG00000119139 | Education | 2E-9 | 27020472 |
| ENSG00000119139 | Refractive Errors | 2E-9 | 27020472 |
| ENSG00000119139 | Refraction, Ocular | 7E-9 | 23396134 |
| ENSG00000119139 | Education | 2E-9 | 27020472 |
| ENSG00000119139 | Refractive Errors | 2E-9 | 27020472 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000119139 | rs11145488 | 9 | 69156023 | A | Spherical equivalent (joint analysis main effects and education interaction) | 27020472 | EFO_0004784|EFO_0007814 | ||
| ENSG00000119139 | rs11145488 | 9 | 69156023 | A | Spherical equivalent (joint analysis main effects and education interaction) | 27020472 | EFO_0004784|EFO_0007814 | ||
| ENSG00000119139 | rs11145465 | 9 | 69151677 | A | Refractive error | 23396134 | [0.083-0.165] unit decrease | 0.124 | HP_0000539 |
| ENSG00000119139 | rs11145465 | 9 | 69151677 | A | Spherical equivalent | 29808027 | [0.067-0.135] unit decrease | 0.1012 | EFO_0007814 |
| ENSG00000119139 | rs11145465 | 9 | 69151677 | A | Spherical equivalent | 29808027 | [0.066-0.136] unit decrease | 0.1011 | EFO_0007814 |
| ENSG00000119139 | rs11145461 | 9 | 69151203 | T | Myopia (age of diagnosis) | 29808027 | [0.05-0.083] unit decrease | 0.0668 | EFO_0004847|HP_0000545 |
| ENSG00000119139 | rs11145465 | 9 | 69151677 | A | Spherical equivalent or myopia (age of diagnosis) | 29808027 | [NR] z score decrease | 9.546 | EFO_0004847|HP_0000545|EFO_0007814 |
| ENSG00000119139 | rs1538583 | 9 | 69176631 | ? | Glomerular filtration rate in type 2 diabetes | 29703844 | [1.70-4.19] unit increase | 2.95 | EFO_0005208|EFO_0001360 |
| ENSG00000119139 | rs2282335 | 9 | 69251016 | A | Renal sinus fat | 22044751 | [0.098-0.244] unit increase | 0.171 | EFO_0004864 |
| ENSG00000119139 | rs11145488 | 9 | 69156023 | ? | Myopia | 27182965 | [1.07-1.11] | 1.0869565 | HP_0000545 |
| ENSG00000119139 | rs62567129 | 9 | 69174188 | ? | Macular thickness | 30535121 | [0.28-0.61] unit increase | 0.4451 | EFO_0008375 |
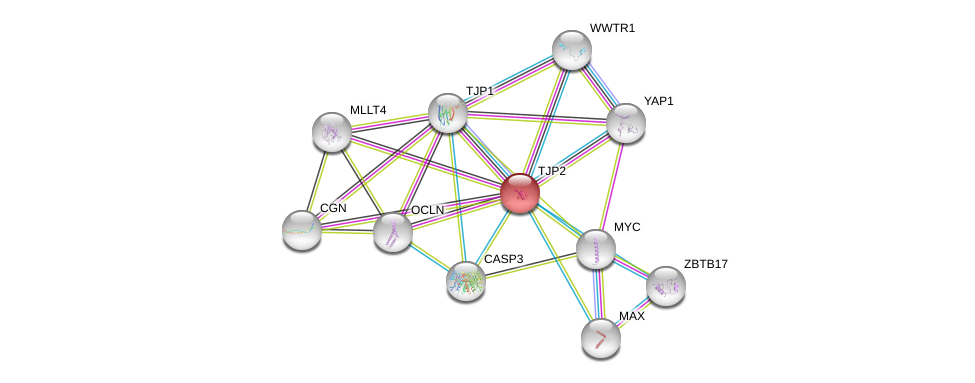
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000119139 | TJP2 | 100 | 93.284 | ENSMUSG00000024812 | Tjp2 | 100 | 85.774 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0004385 | guanylate kinase activity | 8824195. | TAS | Function |
| GO:0005515 | protein binding | 15975580.18823282.22665060.23885123. | IPI | Function |
| GO:0005654 | nucleoplasm | - | IDA | Component |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0005829 | cytosol | - | IDA | Component |
| GO:0005829 | cytosol | - | TAS | Component |
| GO:0005886 | plasma membrane | - | IDA | Component |
| GO:0005886 | plasma membrane | - | TAS | Component |
| GO:0005912 | adherens junction | - | IEA | Component |
| GO:0005923 | bicellular tight junction | 22006950.23885123. | IDA | Component |
| GO:0019904 | protein domain specific binding | 23885123. | IPI | Function |
| GO:0030054 | cell junction | - | IDA | Component |
| GO:0030674 | protein binding, bridging | 23885123. | IDA | Function |
| GO:0035329 | hippo signaling | - | TAS | Process |
| GO:0045296 | cadherin binding | 25468996. | HDA | Function |
| GO:0046037 | GMP metabolic process | - | IEA | Process |
| GO:0046710 | GDP metabolic process | - | IEA | Process |
| GO:0050892 | intestinal absorption | 23885123. | IMP | Process |
| GO:0090557 | establishment of endothelial intestinal barrier | 23885123. | IMP | Process |
| GO:0090559 | regulation of membrane permeability | 23885123. | IMP | Process |