
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LAML | |||||||
| LAML | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THYM | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| DLBC | |||
| KIRC | |||
| LGG | |||
| LIHC | |||
| PCPG | |||
| PRAD | |||
| READ | |||
| SARC | |||
| TGCT | |||
| THYM | |||
| UCEC |
| Cancer | P-value | Q-value |
|---|---|---|
| ACC | ||
| KIRP | ||
| PAAD | ||
| CESC | ||
| READ | ||
| KICH | ||
| UCEC | ||
| LIHC | ||
| LGG | ||
| THCA | ||
| LUAD | ||
| UVM |
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000355540 | U3snoRNP10 | PF12397.8 | 2e-35 | 1 | 1 |
| ENSP00000355541 | U3snoRNP10 | PF12397.8 | 2.9e-35 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000483073 | HEATR1-204 | 654 | - | - | - (aa) | - | - |
| ENST00000490339 | HEATR1-205 | 453 | - | - | - (aa) | - | - |
| ENST00000366579 | HEATR1-201 | 793 | - | ENSP00000355538 | 120 (aa) | - | Q6P664 |
| ENST00000366582 | HEATR1-203 | 8447 | - | ENSP00000355541 | 2144 (aa) | - | Q9H583 |
| ENST00000366581 | HEATR1-202 | 6538 | - | ENSP00000355540 | 2063 (aa) | - | Q5T3Q7 |
| Pathway ID | Pathway Name | Source |
|---|---|---|
| hsa03008 | Ribosome biogenesis in eukaryotes | KEGG |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000119285 | rs150174091 | 1 | 236584261 | G | Post bronchodilator FEV1/FVC ratio | 26634245 | unit increase | 0.262 | GO_0097366|EFO_0004713 |
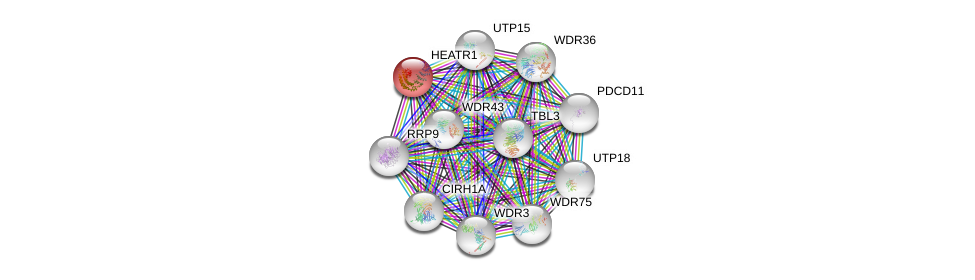
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSAPOG00000008169 | heatr1 | 96 | 56.410 | Acanthochromis_polyacanthus |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSAMEG00000001015 | HEATR1 | 100 | 88.106 | Ailuropoda_melanoleuca |
| ENSG00000119285 | HEATR1 | 100 | 71.667 | ENSACIG00000015343 | heatr1 | 96 | 61.010 | Amphilophus_citrinellus |
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSAPEG00000009996 | heatr1 | 100 | 54.148 | Amphiprion_percula |
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSATEG00000013260 | heatr1 | 96 | 59.656 | Anabas_testudineus |
| ENSG00000119285 | HEATR1 | 99 | 71.305 | ENSAPLG00000008015 | HEATR1 | 96 | 71.401 | Anas_platyrhynchos |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSANAG00000021975 | HEATR1 | 100 | 97.008 | Aotus_nancymaae |
| ENSG00000119285 | HEATR1 | 100 | 71.667 | ENSACLG00000017561 | - | 93 | 60.976 | Astatotilapia_calliptera |
| ENSG00000119285 | HEATR1 | 100 | 67.500 | ENSAMXG00000040261 | heatr1 | 96 | 60.377 | Astyanax_mexicanus |
| ENSG00000119285 | HEATR1 | 100 | 99.167 | ENSBTAG00000044100 | HEATR1 | 100 | 88.293 | Bos_taurus |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSCJAG00000017734 | HEATR1 | 100 | 96.718 | Callithrix_jacchus |
| ENSG00000119285 | HEATR1 | 100 | 97.500 | ENSCAFG00000010919 | HEATR1 | 100 | 89.739 | Canis_familiaris |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSCAFG00020026884 | HEATR1 | 100 | 91.216 | Canis_lupus_dingo |
| ENSG00000119285 | HEATR1 | 100 | 99.167 | ENSCHIG00000022619 | HEATR1 | 100 | 87.826 | Capra_hircus |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSTSYG00000000988 | HEATR1 | 100 | 92.471 | Carlito_syrichta |
| ENSG00000119285 | HEATR1 | 92 | 69.028 | ENSCAPG00000011461 | HEATR1 | 100 | 69.028 | Cavia_aperea |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSCPOG00000008331 | HEATR1 | 100 | 87.407 | Cavia_porcellus |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSCCAG00000037071 | HEATR1 | 100 | 95.637 | Cebus_capucinus |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSCATG00000021120 | HEATR1 | 100 | 97.141 | Cercocebus_atys |
| ENSG00000119285 | HEATR1 | 100 | 96.667 | ENSCLAG00000016900 | HEATR1 | 100 | 87.832 | Chinchilla_lanigera |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSCSAG00000009731 | HEATR1 | 100 | 97.249 | Chlorocebus_sabaeus |
| ENSG00000119285 | HEATR1 | 90 | 97.872 | ENSCHOG00000004046 | HEATR1 | 90 | 97.872 | Choloepus_hoffmanni |
| ENSG00000119285 | HEATR1 | 100 | 82.500 | ENSCPBG00000004198 | HEATR1 | 97 | 72.055 | Chrysemys_picta_bellii |
| ENSG00000119285 | HEATR1 | 100 | 56.198 | ENSCING00000009854 | - | 98 | 40.528 | Ciona_intestinalis |
| ENSG00000119285 | HEATR1 | 100 | 55.372 | ENSCSAVG00000000516 | - | 100 | 30.679 | Ciona_savignyi |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSCANG00000027702 | HEATR1 | 100 | 96.754 | Colobus_angolensis_palliatus |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSCGRG00001020538 | Heatr1 | 100 | 85.448 | Cricetulus_griseus_chok1gshd |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSCGRG00000016828 | Heatr1 | 100 | 85.448 | Cricetulus_griseus_crigri |
| ENSG00000119285 | HEATR1 | 100 | 71.667 | ENSCVAG00000019837 | - | 89 | 65.385 | Cyprinodon_variegatus |
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSDARG00000099742 | heatr1 | 96 | 62.287 | Danio_rerio |
| ENSG00000119285 | HEATR1 | 100 | 99.167 | ENSDNOG00000009046 | HEATR1 | 100 | 88.542 | Dasypus_novemcinctus |
| ENSG00000119285 | HEATR1 | 100 | 94.167 | ENSDORG00000004607 | Heatr1 | 98 | 86.178 | Dipodomys_ordii |
| ENSG00000119285 | HEATR1 | 99 | 52.941 | FBgn0086451 | l(2)k09022 | 74 | 34.436 | Drosophila_melanogaster |
| ENSG00000119285 | HEATR1 | 100 | 95.000 | ENSETEG00000004144 | HEATR1 | 90 | 87.755 | Echinops_telfairi |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSECAG00000021443 | HEATR1 | 100 | 91.744 | Equus_caballus |
| ENSG00000119285 | HEATR1 | 99 | 95.798 | ENSEEUG00000008946 | HEATR1 | 82 | 93.373 | Erinaceus_europaeus |
| ENSG00000119285 | HEATR1 | 100 | 72.500 | ENSELUG00000005309 | heatr1 | 97 | 60.952 | Esox_lucius |
| ENSG00000119285 | HEATR1 | 97 | 72.185 | ENSFALG00000013475 | HEATR1 | 100 | 66.496 | Ficedula_albicollis |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSFDAG00000012144 | HEATR1 | 100 | 87.925 | Fukomys_damarensis |
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSFHEG00000019723 | - | 100 | 62.654 | Fundulus_heteroclitus |
| ENSG00000119285 | HEATR1 | 100 | 69.167 | ENSGMOG00000014830 | heatr1 | 100 | 51.115 | Gadus_morhua |
| ENSG00000119285 | HEATR1 | 100 | 70.833 | ENSGAFG00000014904 | heatr1 | 96 | 55.725 | Gambusia_affinis |
| ENSG00000119285 | HEATR1 | 100 | 67.500 | ENSGACG00000010205 | heatr1 | 96 | 56.459 | Gasterosteus_aculeatus |
| ENSG00000119285 | HEATR1 | 100 | 83.333 | ENSGAGG00000018712 | HEATR1 | 100 | 68.165 | Gopherus_agassizii |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSGGOG00000006913 | HEATR1 | 100 | 99.031 | Gorilla_gorilla |
| ENSG00000119285 | HEATR1 | 100 | 71.667 | ENSHBUG00000007268 | - | 97 | 63.415 | Haplochromis_burtoni |
| ENSG00000119285 | HEATR1 | 100 | 97.500 | ENSHGLG00000016543 | HEATR1 | 100 | 88.013 | Heterocephalus_glaber_female |
| ENSG00000119285 | HEATR1 | 100 | 97.500 | ENSHGLG00100015785 | HEATR1 | 100 | 87.826 | Heterocephalus_glaber_male |
| ENSG00000119285 | HEATR1 | 100 | 70.833 | ENSIPUG00000012219 | heatr1 | 96 | 61.773 | Ictalurus_punctatus |
| ENSG00000119285 | HEATR1 | 100 | 97.500 | ENSSTOG00000007293 | HEATR1 | 100 | 88.293 | Ictidomys_tridecemlineatus |
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSLBEG00000013928 | - | 89 | 64.120 | Labrus_bergylta |
| ENSG00000119285 | HEATR1 | 100 | 78.333 | ENSLOCG00000016621 | - | 100 | 68.652 | Lepisosteus_oculatus |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSLAFG00000002968 | - | 99 | 86.916 | Loxodonta_africana |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSMFAG00000044672 | HEATR1 | 100 | 97.093 | Macaca_fascicularis |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSMMUG00000015135 | HEATR1 | 100 | 97.141 | Macaca_mulatta |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSMNEG00000035612 | HEATR1 | 100 | 97.141 | Macaca_nemestrina |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSMLEG00000035012 | HEATR1 | 100 | 97.190 | Mandrillus_leucophaeus |
| ENSG00000119285 | HEATR1 | 100 | 68.333 | ENSMAMG00000010181 | heatr1 | 97 | 59.564 | Mastacembelus_armatus |
| ENSG00000119285 | HEATR1 | 100 | 71.667 | ENSMZEG00005013121 | - | 93 | 65.232 | Maylandia_zebra |
| ENSG00000119285 | HEATR1 | 100 | 80.833 | ENSMGAG00000011761 | HEATR1 | 96 | 70.825 | Meleagris_gallopavo |
| ENSG00000119285 | HEATR1 | 100 | 95.000 | ENSMICG00000015859 | HEATR1 | 100 | 92.293 | Microcebus_murinus |
| ENSG00000119285 | HEATR1 | 100 | 86.667 | ENSMODG00000007936 | HEATR1 | 100 | 78.415 | Monodelphis_domestica |
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSMALG00000011014 | heatr1 | 95 | 52.280 | Monopterus_albus |
| ENSG00000119285 | HEATR1 | 100 | 94.167 | ENSMUSG00000050244 | Heatr1 | 96 | 88.224 | Mus_musculus |
| ENSG00000119285 | HEATR1 | 100 | 94.167 | MGP_PahariEiJ_G0019273 | Heatr1 | 96 | 88.320 | Mus_pahari |
| ENSG00000119285 | HEATR1 | 100 | 94.167 | MGP_SPRETEiJ_G0019081 | Heatr1 | 96 | 88.127 | Mus_spretus |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSMPUG00000012748 | HEATR1 | 100 | 90.159 | Mustela_putorius_furo |
| ENSG00000119285 | HEATR1 | 100 | 96.667 | ENSMLUG00000024338 | - | 100 | 86.521 | Myotis_lucifugus |
| ENSG00000119285 | HEATR1 | 92 | 86.451 | ENSMLUG00000023156 | - | 100 | 86.451 | Myotis_lucifugus |
| ENSG00000119285 | HEATR1 | 100 | 90.833 | ENSNGAG00000017650 | Heatr1 | 100 | 83.535 | Nannospalax_galili |
| ENSG00000119285 | HEATR1 | 100 | 99.167 | ENSNLEG00000003345 | HEATR1 | 100 | 99.035 | Nomascus_leucogenys |
| ENSG00000119285 | HEATR1 | 98 | 83.158 | ENSOPRG00000010081 | HEATR1 | 100 | 83.158 | Ochotona_princeps |
| ENSG00000119285 | HEATR1 | 100 | 71.667 | ENSONIG00000019095 | heatr1 | 96 | 59.886 | Oreochromis_niloticus |
| ENSG00000119285 | HEATR1 | 100 | 81.667 | ENSOANG00000006937 | - | 92 | 71.429 | Ornithorhynchus_anatinus |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSOCUG00000014007 | HEATR1 | 100 | 90.532 | Oryctolagus_cuniculus |
| ENSG00000119285 | HEATR1 | 100 | 68.333 | ENSORLG00015018281 | heatr1 | 100 | 52.214 | Oryzias_latipes_hsok |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSOGAG00000010984 | - | 99 | 88.020 | Otolemur_garnettii |
| ENSG00000119285 | HEATR1 | 100 | 99.167 | ENSOARG00000003675 | HEATR1 | 100 | 87.920 | Ovis_aries |
| ENSG00000119285 | HEATR1 | 100 | 99.710 | ENSPPAG00000036487 | HEATR1 | 100 | 99.580 | Pan_paniscus |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSPPRG00000014254 | HEATR1 | 100 | 89.675 | Panthera_pardus |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSPTIG00000017413 | HEATR1 | 100 | 91.216 | Panthera_tigris_altaica |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSPTRG00000002141 | HEATR1 | 100 | 99.534 | Pan_troglodytes |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSPANG00000020212 | HEATR1 | 100 | 97.384 | Papio_anubis |
| ENSG00000119285 | HEATR1 | 91 | 61.841 | ENSPKIG00000002326 | heatr1 | 99 | 59.927 | Paramormyrops_kingsleyae |
| ENSG00000119285 | HEATR1 | 100 | 82.500 | ENSPSIG00000010048 | HEATR1 | 100 | 66.574 | Pelodiscus_sinensis |
| ENSG00000119285 | HEATR1 | 100 | 66.116 | ENSPMAG00000006017 | - | 99 | 49.605 | Petromyzon_marinus |
| ENSG00000119285 | HEATR1 | 100 | 86.667 | ENSPCIG00000008351 | HEATR1 | 100 | 78.295 | Phascolarctos_cinereus |
| ENSG00000119285 | HEATR1 | 100 | 69.167 | ENSPFOG00000006008 | heatr1 | 97 | 58.357 | Poecilia_formosa |
| ENSG00000119285 | HEATR1 | 100 | 99.167 | ENSPPYG00000000085 | HEATR1 | 100 | 98.181 | Pongo_abelii |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSPCOG00000018534 | HEATR1 | 98 | 91.699 | Propithecus_coquereli |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSPVAG00000013860 | HEATR1 | 100 | 86.147 | Pteropus_vampyrus |
| ENSG00000119285 | HEATR1 | 100 | 71.667 | ENSPNYG00000011083 | - | 93 | 65.563 | Pundamilia_nyererei |
| ENSG00000119285 | HEATR1 | 100 | 65.000 | ENSPNAG00000025592 | heatr1 | 96 | 62.560 | Pygocentrus_nattereri |
| ENSG00000119285 | HEATR1 | 100 | 95.833 | ENSRNOG00000047594 | LOC108348069 | 96 | 89.286 | Rattus_norvegicus |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSRBIG00000039995 | HEATR1 | 100 | 96.225 | Rhinopithecus_bieti |
| ENSG00000119285 | HEATR1 | 100 | 100.000 | ENSRROG00000037217 | HEATR1 | 100 | 97.141 | Rhinopithecus_roxellana |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSSBOG00000033349 | HEATR1 | 100 | 96.042 | Saimiri_boliviensis_boliviensis |
| ENSG00000119285 | HEATR1 | 100 | 87.500 | ENSSHAG00000007902 | HEATR1 | 100 | 78.462 | Sarcophilus_harrisii |
| ENSG00000119285 | HEATR1 | 100 | 77.500 | ENSSFOG00015009818 | heatr1 | 96 | 61.494 | Scleropages_formosus |
| ENSG00000119285 | HEATR1 | 100 | 70.000 | ENSSMAG00000013148 | heatr1 | 98 | 50.000 | Scophthalmus_maximus |
| ENSG00000119285 | HEATR1 | 100 | 70.833 | ENSSDUG00000013751 | heatr1 | 96 | 59.677 | Seriola_dumerili |
| ENSG00000119285 | HEATR1 | 83 | 68.750 | ENSSLDG00000017083 | heatr1 | 99 | 68.750 | Seriola_lalandi_dorsalis |
| ENSG00000119285 | HEATR1 | 86 | 93.617 | ENSSARG00000012336 | HEATR1 | 86 | 93.617 | Sorex_araneus |
| ENSG00000119285 | HEATR1 | 100 | 97.500 | ENSSSCG00000010145 | HEATR1 | 99 | 87.595 | Sus_scrofa |
| ENSG00000119285 | HEATR1 | 100 | 81.667 | ENSTGUG00000010404 | HEATR1 | 96 | 71.785 | Taeniopygia_guttata |
| ENSG00000119285 | HEATR1 | 100 | 69.167 | ENSTNIG00000003577 | heatr1 | 96 | 57.696 | Tetraodon_nigroviridis |
| ENSG00000119285 | HEATR1 | 100 | 96.667 | ENSTBEG00000017495 | HEATR1 | 83 | 81.619 | Tupaia_belangeri |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSTTRG00000012382 | HEATR1 | 97 | 90.495 | Tursiops_truncatus |
| ENSG00000119285 | HEATR1 | 57 | 90.049 | ENSUAMG00000010978 | - | 98 | 91.023 | Ursus_americanus |
| ENSG00000119285 | HEATR1 | 100 | 97.500 | ENSUAMG00000017854 | - | 94 | 94.137 | Ursus_americanus |
| ENSG00000119285 | HEATR1 | 100 | 97.500 | ENSUMAG00000013575 | - | 94 | 94.137 | Ursus_maritimus |
| ENSG00000119285 | HEATR1 | 100 | 98.333 | ENSVVUG00000009369 | HEATR1 | 100 | 89.459 | Vulpes_vulpes |
| ENSG00000119285 | HEATR1 | 100 | 78.333 | ENSXETG00000009013 | heatr1 | 100 | 63.700 | Xenopus_tropicalis |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000462 | maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) | 21873635. | IBA | Process |
| GO:0001650 | fibrillar center | - | IDA | Component |
| GO:0003723 | RNA binding | 22658674.22681889. | HDA | Function |
| GO:0005515 | protein binding | 22190034. | IPI | Function |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0005730 | nucleolus | 17699751. | IDA | Component |
| GO:0005739 | mitochondrion | - | IDA | Component |
| GO:0006364 | rRNA processing | - | TAS | Process |
| GO:0016020 | membrane | 19946888. | HDA | Component |
| GO:0030686 | 90S preribosome | 21873635. | IBA | Component |
| GO:0032040 | small-subunit processome | 21873635. | IBA | Component |
| GO:0034455 | t-UTP complex | 21873635. | IBA | Component |
| GO:0045943 | positive regulation of transcription by RNA polymerase I | 21873635. | IBA | Process |
| GO:0045943 | positive regulation of transcription by RNA polymerase I | 17699751. | IMP | Process |
| GO:2000234 | positive regulation of rRNA processing | 17699751. | IMP | Process |