
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| LAML | |||||||
| LGG | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| BLCA | |||
| KIRC | |||
| KIRP | |||
| LGG | |||
| MESO | |||
| PAAD | |||
| SKCM | |||
| THYM | |||
| UVM |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| ACC | ||
| HNSC | ||
| SKCM | ||
| BRCA | ||
| KIRP | ||
| PAAD | ||
| BLCA | ||
| CESC | ||
| READ | ||
| UCEC | ||
| LIHC | ||
| LGG | ||
| LUAD |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000611279 | MTHFD1L-211 | 3475 | XM_005266911 | ENSP00000478253 | 979 (aa) | XP_005266968 | B7ZM99 |
| ENST00000367321 | MTHFD1L-203 | 3604 | XM_005266907 | ENSP00000356290 | 978 (aa) | XP_005266964 | Q6UB35 |
| ENST00000423867 | MTHFD1L-206 | 524 | - | ENSP00000400776 | 114 (aa) | - | Q5JYA3 |
| ENST00000618312 | MTHFD1L-212 | 3159 | XM_011535730 | ENSP00000479539 | 913 (aa) | XP_011534032 | A0A087WVM4 |
| ENST00000441122 | MTHFD1L-207 | 1134 | - | ENSP00000407070 | 108 (aa) | - | Q5JYA8 |
| ENST00000420192 | MTHFD1L-204 | 606 | - | ENSP00000395158 | 96 (aa) | - | Q4VXV2 |
| ENST00000421497 | MTHFD1L-205 | 373 | - | - | - (aa) | - | - |
| ENST00000367308 | MTHFD1L-202 | 996 | XM_024446396 | ENSP00000356277 | 332 (aa) | XP_024302164 | H0Y327 |
| ENST00000478643 | MTHFD1L-210 | 421 | - | - | - (aa) | - | - |
| ENST00000367307 | MTHFD1L-201 | 1049 | - | ENSP00000356276 | 275 (aa) | - | Q6UB35 |
| ENST00000453602 | MTHFD1L-209 | 503 | - | ENSP00000391022 | 92 (aa) | - | Q4VXM0 |
| ENST00000450635 | MTHFD1L-208 | 427 | - | ENSP00000399804 | 57 (aa) | - | Q4VXM1 |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000120254 | Respiratory Function Tests | 3.85504303519468E-5 | 17903307 |
| ENSG00000120254 | Body Mass Index | 4.14939035831008E-5 | 17903300 |
| ENSG00000120254 | Body Mass Index | 5.37691608886963E-6 | 17903300 |
| ENSG00000120254 | Body Mass Index | 4.73950542678736E-6 | 17903300 |
| ENSG00000120254 | Body Mass Index | 9.47239859660896E-8 | 17903300 |
| ENSG00000120254 | Body Weight | 3.78872399011687E-5 | 17903300 |
| ENSG00000120254 | Aorta | 8.3543782868123E-5 | 17903303 |
| ENSG00000120254 | Aorta | 8.74531513195276E-5 | 17903303 |
| ENSG00000120254 | Stroke | 3.3014086E-004 | 19369658 |
| ENSG00000120254 | Cholesterol | 2.203e-005 | - |
| ENSG00000120254 | Arteries | 1.6540000E-005 | - |
| ENSG00000120254 | Vascular Diseases | 6.1500000E-006 | - |
| ENSG00000120254 | Coronary Disease | 3E-8 | 17634449 |
| ENSG00000120254 | Schizophrenia | 1E-6 | 26198764 |
| ENSG00000120254 | Alzheimer Disease | 2E-10 | 20885792 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000120254 | rs524732 | 6 | 150993705 | A | Schizophrenia | 26198764 | [NR] | 1.06 | EFO_0000692 |
| ENSG00000120254 | rs11754661 | 6 | 150885942 | A | Alzheimer's disease (late onset) | 20885792 | [1.67-2.64] | 2.1 | EFO_0000249 |
| ENSG00000120254 | rs6922269 | 6 | 150931849 | A | Coronary heart disease | 17634449 | [1.15-1.33] | 1.23 | EFO_0001645 |
| ENSG00000120254 | rs9397365 | 6 | 150915044 | G | Peripheral arterial disease (traffic-related air pollution interaction) | 27082954 | [19.58-22.56] | 21.07 | EFO_0004265|EFO_0007908 |
| ENSG00000120254 | rs13193176 | 6 | 150945734 | ? | DNA methylation variation (age effect) | 30348214 | GO_0006306 |
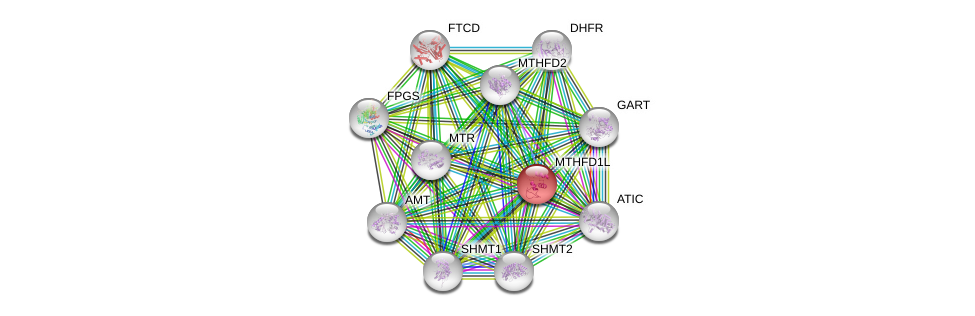
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000120254 | MTHFD1L | 97 | 96.774 | ENSMUSG00000040675 | Mthfd1l | 100 | 88.344 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0001843 | neural tube closure | - | ISS | Process |
| GO:0004329 | formate-tetrahydrofolate ligase activity | 21873635. | IBA | Function |
| GO:0004329 | formate-tetrahydrofolate ligase activity | 12937168. | IDA | Function |
| GO:0004488 | methylenetetrahydrofolate dehydrogenase (NADP+) activity | - | IEA | Function |
| GO:0005524 | ATP binding | 16171773. | IDA | Function |
| GO:0005737 | cytoplasm | 21873635. | IBA | Component |
| GO:0005739 | mitochondrion | 21873635. | IBA | Component |
| GO:0005739 | mitochondrion | 12937168. | IDA | Component |
| GO:0005759 | mitochondrial matrix | - | TAS | Component |
| GO:0006760 | folic acid-containing compound metabolic process | 12937168. | IDA | Process |
| GO:0009113 | purine nucleobase biosynthetic process | 21873635. | IBA | Process |
| GO:0009257 | 10-formyltetrahydrofolate biosynthetic process | 21873635. | IBA | Process |
| GO:0009257 | 10-formyltetrahydrofolate biosynthetic process | 12937168. | IDA | Process |
| GO:0015942 | formate metabolic process | 16171773. | IDA | Process |
| GO:0016020 | membrane | 19946888. | HDA | Component |
| GO:0035999 | tetrahydrofolate interconversion | - | IEA | Process |
| GO:0042803 | protein homodimerization activity | 16171773. | IDA | Function |
| GO:0046655 | folic acid metabolic process | - | TAS | Process |
| GO:0048702 | embryonic neurocranium morphogenesis | - | ISS | Process |
| GO:0048703 | embryonic viscerocranium morphogenesis | - | ISS | Process |
| GO:0055114 | oxidation-reduction process | - | IEA | Process |