
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| KIRP | |||
| LUSC | |||
| READ | |||
| UCS |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| MESO | ||
| ACC | ||
| HNSC | ||
| SKCM | ||
| ESCA | ||
| COAD | ||
| PAAD | ||
| LAML | ||
| UCEC | ||
| LIHC | ||
| THCA | ||
| LUAD | ||
| OV |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000252699 | ACTN4-201 | 4963 | XM_005259281 | ENSP00000252699 | 911 (aa) | XP_005259338 | O43707 |
| ENST00000497637 | ACTN4-208 | 877 | - | - | - (aa) | - | - |
| ENST00000589528 | ACTN4-211 | 441 | - | ENSP00000467190 | 105 (aa) | - | K7EP19 |
| ENST00000390009 | ACTN4-202 | 2102 | - | ENSP00000439497 | 692 (aa) | - | O43707 |
| ENST00000586538 | ACTN4-209 | 546 | - | ENSP00000465176 | 182 (aa) | - | K7EJH8 |
| ENST00000495553 | ACTN4-207 | 586 | - | - | - (aa) | - | - |
| ENST00000588618 | ACTN4-210 | 1729 | - | - | - (aa) | - | - |
| ENST00000424234 | ACTN4-203 | 1566 | - | ENSP00000411187 | 521 (aa) | - | F5GXS2 |
| ENST00000477174 | ACTN4-205 | 544 | - | - | - (aa) | - | - |
| ENST00000489451 | ACTN4-206 | 654 | - | - | - (aa) | - | - |
| ENST00000440400 | ACTN4-204 | 3180 | - | ENSP00000398393 | 342 (aa) | - | H7C144 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000130402 | rs11083475 | 19 | 38697472 | G | Heart rate | 23583979 | EFO_0004326 | ||
| ENSG00000130402 | rs973009 | 19 | 38683692 | ? | Migraine with aura | 23793025 | [1.1-1.27] | 1.18 | EFO_0003821 |
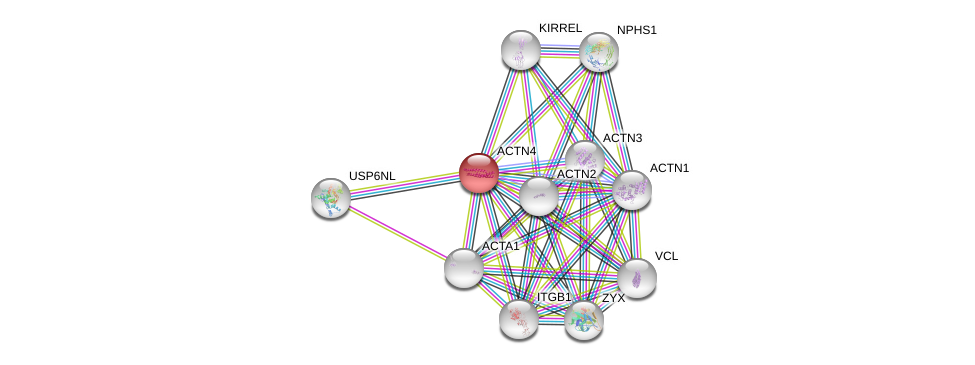
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000130402 | ACTN4 | 100 | 98.901 | ENSMUSG00000054808 | Actn4 | 100 | 100.000 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000977 | RNA polymerase II regulatory region sequence-specific DNA binding | 25411248. | IDA | Function |
| GO:0001666 | response to hypoxia | - | IEA | Process |
| GO:0001725 | stress fiber | - | IEA | Component |
| GO:0001882 | nucleoside binding | 12411747. | IDA | Function |
| GO:0002576 | platelet degranulation | - | TAS | Process |
| GO:0003713 | transcription coactivator activity | 25411248. | IMP | Function |
| GO:0003723 | RNA binding | 22658674. | HDA | Function |
| GO:0003779 | actin binding | 8104223. | TAS | Function |
| GO:0005178 | integrin binding | 8104223. | TAS | Function |
| GO:0005509 | calcium ion binding | - | IEA | Function |
| GO:0005515 | protein binding | 15619032.15841212.15988023.16189514.16204054.16944923.19447967.22351778.22662192.24802111.25241761.25411248.25416956.25910212.26496610.26871637. | IPI | Function |
| GO:0005576 | extracellular region | - | TAS | Component |
| GO:0005615 | extracellular space | 16502470. | HDA | Component |
| GO:0005634 | nucleus | 9508771.22351778.25411248. | IDA | Component |
| GO:0005737 | cytoplasm | 16791210. | HDA | Component |
| GO:0005737 | cytoplasm | 9508771.22351778.25411248. | IDA | Component |
| GO:0005829 | cytosol | - | IDA | Component |
| GO:0005903 | brush border | - | IEA | Component |
| GO:0005911 | cell-cell junction | - | IEA | Component |
| GO:0005925 | focal adhesion | 21423176. | HDA | Component |
| GO:0015031 | protein transport | - | IEA | Process |
| GO:0015629 | actin cytoskeleton | 25918384. | IDA | Component |
| GO:0016604 | nuclear body | - | IDA | Component |
| GO:0030018 | Z disc | - | IEA | Component |
| GO:0030050 | vesicle transport along actin filament | 25918384. | IMP | Process |
| GO:0030335 | positive regulation of cell migration | 25918384. | IMP | Process |
| GO:0030374 | nuclear receptor transcription coactivator activity | 22351778. | IMP | Function |
| GO:0030863 | cortical cytoskeleton | - | IEA | Component |
| GO:0031093 | platelet alpha granule lumen | - | TAS | Component |
| GO:0031143 | pseudopodium | 1629252. | TAS | Component |
| GO:0031490 | chromatin DNA binding | 25411248. | IDA | Function |
| GO:0032417 | positive regulation of sodium:proton antiporter activity | 11948184. | NAS | Process |
| GO:0032991 | protein-containing complex | 11948184. | IDA | Component |
| GO:0033209 | tumor necrosis factor-mediated signaling pathway | 25411248. | IDA | Process |
| GO:0035257 | nuclear hormone receptor binding | 22351778. | IPI | Function |
| GO:0035357 | peroxisome proliferator activated receptor signaling pathway | 22351778. | IDA | Process |
| GO:0042803 | protein homodimerization activity | 22351778. | IPI | Function |
| GO:0042803 | protein homodimerization activity | 15841212. | TAS | Function |
| GO:0042974 | retinoic acid receptor binding | 22351778. | IPI | Function |
| GO:0042981 | regulation of apoptotic process | 16807302. | NAS | Process |
| GO:0043005 | neuron projection | - | IEA | Component |
| GO:0044325 | ion channel binding | 19943616. | IPI | Function |
| GO:0047485 | protein N-terminus binding | - | IEA | Function |
| GO:0048384 | retinoic acid receptor signaling pathway | 22351778. | IDA | Process |
| GO:0048471 | perinuclear region of cytoplasm | 15619032. | IDA | Component |
| GO:0048549 | positive regulation of pinocytosis | - | IEA | Process |
| GO:0051015 | actin filament binding | 12411747. | IDA | Function |
| GO:0051015 | actin filament binding | 25918384. | IMP | Function |
| GO:0051017 | actin filament bundle assembly | - | IEA | Process |
| GO:0051271 | negative regulation of cellular component movement | - | IEA | Process |
| GO:0051272 | positive regulation of cellular component movement | 9508771. | IDA | Process |
| GO:0051272 | positive regulation of cellular component movement | 15048094. | IMP | Process |
| GO:0070062 | extracellular exosome | 19199708.20458337.21362503.23533145. | HDA | Component |
| GO:0070830 | bicellular tight junction assembly | - | IEA | Process |
| GO:1900025 | negative regulation of substrate adhesion-dependent cell spreading | 25918384. | IMP | Process |
| GO:1901224 | positive regulation of NIK/NF-kappaB signaling | 25411248. | IMP | Process |
| GO:1902396 | protein localization to bicellular tight junction | - | IEA | Process |
| GO:1903506 | regulation of nucleic acid-templated transcription | 22351778. | IMP | Process |
| GO:1903508 | positive regulation of nucleic acid-templated transcription | - | IEA | Process |
| GO:1990904 | ribonucleoprotein complex | 17289661. | IDA | Component |