
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LAML | |||||||
| LAML | |||||||
| LAML | |||||||
| LAML | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PCPG | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THYM | |||||||
| THYM | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UVM | |||||||
| UVM |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| BLCA | |||
| CHOL | |||
| GBM | |||
| LAML | |||
| PRAD | |||
| UCEC |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| STAD | ||
| MESO | ||
| SKCM | ||
| BRCA | ||
| LAML | ||
| UCEC | ||
| LGG |
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000268489 | zf-C2H2 | PF00096.26 | 4.6e-13 | 1 | 2 |
| ENSP00000268489 | zf-C2H2 | PF00096.26 | 4.6e-13 | 2 | 2 |
| ENSP00000493252 | zf-C2H2 | PF00096.26 | 4.6e-13 | 1 | 2 |
| ENSP00000493252 | zf-C2H2 | PF00096.26 | 4.6e-13 | 2 | 2 |
| ENSP00000438926 | zf-C2H2 | PF00096.26 | 2.9e-10 | 1 | 1 |
| ENSP00000268489 | zf-met | PF12874.7 | 2.4e-06 | 1 | 1 |
| ENSP00000493252 | zf-met | PF12874.7 | 2.4e-06 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000563625 | ZFHX3-205 | 455 | - | - | - (aa) | - | - |
| ENST00000397992 | ZFHX3-203 | 13841 | XM_017023251 | ENSP00000438926 | 2789 (aa) | XP_016878740 | Q15911 |
| ENST00000641018 | ZFHX3-206 | 837 | - | - | - (aa) | - | - |
| ENST00000641077 | ZFHX3-207 | 942 | - | - | - (aa) | - | - |
| ENST00000641206 | ZFHX3-208 | 17219 | - | ENSP00000493252 | 3703 (aa) | - | Q15911 |
| ENST00000358463 | ZFHX3-202 | 1308 | - | - | - (aa) | - | - |
| ENST00000268489 | ZFHX3-201 | 16064 | XM_005255957 | ENSP00000268489 | 3703 (aa) | XP_005256014 | Q15911 |
| ENST00000642085 | ZFHX3-209 | 1603 | - | - | - (aa) | - | - |
| ENST00000558842 | ZFHX3-204 | 240 | - | - | - (aa) | - | - |
| Pathway ID | Pathway Name | Source |
|---|---|---|
| hsa04550 | Signaling pathways regulating pluripotency of stem cells | KEGG |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000140836 | Cardiovascular Diseases | 3.08229721345304E-11 | 17903304 |
| ENSG00000140836 | Cardiovascular Diseases | 1.7707092227539E-9 | 17903304 |
| ENSG00000140836 | Cardiovascular Diseases | 3.1686443324061E-9 | 17903304 |
| ENSG00000140836 | Cardiovascular Diseases | 2.61163771674666E-8 | 17903304 |
| ENSG00000140836 | Cardiovascular Diseases | 2.39538039477632E-8 | 17903304 |
| ENSG00000140836 | Cardiovascular Diseases | 2.3717326436264E-7 | 17903304 |
| ENSG00000140836 | Body Mass Index | 3.0320000E-005 | - |
| ENSG00000140836 | Obesity | 2.8880000E-005 | - |
| ENSG00000140836 | Waist Circumference | 7.8720000E-006 | - |
| ENSG00000140836 | Waist Circumference | 6.2680000E-005 | - |
| ENSG00000140836 | Platelet Function Tests | 8.0100000E-006 | - |
| ENSG00000140836 | Platelet Function Tests | 1.7762800E-005 | - |
| ENSG00000140836 | Platelet Function Tests | 2.0018300E-005 | - |
| ENSG00000140836 | Vitamin B 6 | 7.6570000E-005 | - |
| ENSG00000140836 | Plaque, Atherosclerotic | 1.8810000E-005 | 21909108 |
| ENSG00000140836 | Atrial Fibrillation | 1E-10 | 19597491 |
| ENSG00000140836 | Atrial Fibrillation | 5E-10 | 27790247 |
| ENSG00000140836 | Coronary Disease | 5E-10 | 27790247 |
| ENSG00000140836 | Diabetes Mellitus | 5E-10 | 27790247 |
| ENSG00000140836 | Heart Failure | 5E-10 | 27790247 |
| ENSG00000140836 | Mortality | 5E-10 | 27790247 |
| ENSG00000140836 | Neoplasms | 5E-10 | 27790247 |
| ENSG00000140836 | Stroke | 5E-10 | 27790247 |
| ENSG00000140836 | Glucocorticoids | 1E-6 | 26265699 |
| ENSG00000140836 | Osteonecrosis | 1E-6 | 26265699 |
| ENSG00000140836 | Atrial Fibrillation | 2E-15 | 19597492 |
| ENSG00000140836 | Cholesterol, LDL | 5E-6 | 21347282 |
| ENSG00000140836 | Stroke | 2E-8 | 23041239 |
| ENSG00000140836 | Hypospadias | 1E-18 | 25108383 |
| ENSG00000140836 | Atrial Fibrillation | 3E-11 | 27790247 |
| ENSG00000140836 | Blood Pressure | 3E-11 | 27790247 |
| ENSG00000140836 | Cholesterol | 3E-11 | 27790247 |
| ENSG00000140836 | Coronary Disease | 3E-11 | 27790247 |
| ENSG00000140836 | Diabetes Mellitus | 3E-11 | 27790247 |
| ENSG00000140836 | Electrocardiography | 3E-11 | 27790247 |
| ENSG00000140836 | Glucose | 3E-11 | 27790247 |
| ENSG00000140836 | Heart Failure | 3E-11 | 27790247 |
| ENSG00000140836 | Hematocrit | 3E-11 | 27790247 |
| ENSG00000140836 | Cholesterol, HDL | 3E-11 | 27790247 |
| ENSG00000140836 | Mortality | 3E-11 | 27790247 |
| ENSG00000140836 | Neoplasms | 3E-11 | 27790247 |
| ENSG00000140836 | Triglycerides | 3E-11 | 27790247 |
| ENSG00000140836 | Body Mass Index | 3E-11 | 27790247 |
| ENSG00000140836 | Stroke | 3E-11 | 27790247 |
| ENSG00000140836 | Mucocutaneous Lymph Node Syndrome | 2E-6 | 19132087 |
| ENSG00000140836 | Embolism | 2E-10 | 26708676 |
| ENSG00000140836 | Stroke | 2E-10 | 26708676 |
| ENSG00000140836 | Schizophrenia | 6E-6 | 26198764 |
| ENSG00000140836 | Atrial Fibrillation | 3E-16 | 22544366 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000140836 | rs1480570 | 16 | 73642843 | A | Subjective well-being | 27089181 | [0.0082-0.019] unit increase | 0.0136 | EFO_0007869 |
| ENSG00000140836 | rs1858800 | 16 | 72990377 | T | Hypospadias | 25108383 | [NR] | 1.36 | EFO_0004209 |
| ENSG00000140836 | rs143661751 | 16 | 73688392 | G | Post bronchodilator FEV1/FVC ratio | 26634245 | unit increase | 0.464 | GO_0097366|EFO_0004713 |
| ENSG00000140836 | rs427576 | 16 | 73795371 | C | Thiazide-induced adverse metabolic effects in hypertensive patients | 23400010 | [1.5-3.74] mg/dL decrease | 2.62 | EFO_0005202|EFO_0004465 |
| ENSG00000140836 | rs7193343 | 16 | 72995261 | T | Ischemic stroke (cardioembolic) | 26708676 | [1.11-1.23] | 1.17 | HP_0002140|EFO_1001493 |
| ENSG00000140836 | rs16971384 | 16 | 72897186 | A | LDL cholesterol | 21347282 | [0.041-0.102] unit decrease | 0.0715 | EFO_0004611 |
| ENSG00000140836 | rs2229288 | 16 | 72794405 | C | Glucocorticoid-induced osteonecrosis | 26265699 | GO_0051384|EFO_0004259 | ||
| ENSG00000140836 | rs16971465 | 16 | 72983162 | C | Schizophrenia | 26198764 | [NR] | 1.08 | EFO_0000692 |
| ENSG00000140836 | rs879324 | 16 | 73034779 | A | Stroke (ischemic) | 23041239 | [1.15-1.35] | 1.25 | EFO_0000712 |
| ENSG00000140836 | rs764255 | 16 | 73679784 | T | Word reading | 23738518 | [0.048-0.106] unit decrease | 0.077 | EFO_0005300 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Atrial fibrillation | 22544366 | [1.17-1.30] | 1.24 | EFO_0000275 |
| ENSG00000140836 | rs7191888 | 16 | 73547159 | ? | Multiple sclerosis (severity) | 19010793 | [NR] | EFO_0003885 | |
| ENSG00000140836 | rs7199343 | 16 | 72975125 | T | Kawasaki disease | 19132087 | [1.33-1.92] | 1.56 | EFO_0004246 |
| ENSG00000140836 | rs7193343 | 16 | 72995261 | T | Atrial fibrillation | 19597491 | [1.14-1.29] | 1.21 | EFO_0000275 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Atrial fibrillation | 19597492 | 1.25 | EFO_0000275 | |
| ENSG00000140836 | rs147089336 | 16 | 73318730 | A | QT interval | 29213071 | [5.48-13.68] ms increase | 9.58 | EFO_0004682 |
| ENSG00000140836 | rs4788694 | 16 | 73036184 | G | Body mass index | 28892062 | [0.013-0.029] kg/m2 decrease | 0.021 | EFO_0004340 |
| ENSG00000140836 | rs756717 | 16 | 72962263 | A | Body mass index | 28892062 | [0.0091-0.0209] kg/m2 decrease | 0.015 | EFO_0004340 |
| ENSG00000140836 | rs4404097 | 16 | 72998133 | A | Atrial fibrillation | 29290336 | [1.12-1.24] | 1.18 | EFO_0000275 |
| ENSG00000140836 | rs1364064 | 16 | 73428587 | ? | Colonoscopy-negative controls vs population controls | 29228715 | [NR] | 1.393 | EFO_0008460 |
| ENSG00000140836 | rs2359171 | 16 | 73019123 | A | Atrial fibrillation | 30061737 | [1.17-1.21] | 1.19 | EFO_0000275 |
| ENSG00000140836 | rs417278 | 16 | 73796577 | T | Self-reported math ability | 30038396 | [0.007-0.0148] unit decrease | 0.0109 | EFO_0004875 |
| ENSG00000140836 | rs12932445 | 16 | 73035989 | ? | Stroke | 29531354 | EFO_0000712 | ||
| ENSG00000140836 | rs12932445 | 16 | 73035989 | ? | Ischemic stroke | 29531354 | HP_0002140 | ||
| ENSG00000140836 | rs12932445 | 16 | 73035989 | ? | Ischemic stroke (cardioembolic) | 29531354 | EFO_1001976 | ||
| ENSG00000140836 | rs2063506 | 16 | 73759653 | G | Height | 29782485 | EFO_0004339 | ||
| ENSG00000140836 | rs8054028 | 16 | 73126071 | ? | Midgestational circulating levels of PBDEs (fetal genetic effect) | 28235828 | [0.25-0.53] unit decrease | 0.39 | EFO_0007961|EFO_0007964|EFO_0007959|EFO_0007962 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Atrial fibrillation | 28416818 | [1.15-1.23] | 1.19 | EFO_0000275 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Atrial fibrillation | 28416818 | [1.17-1.37] | 1.2 | EFO_0000275 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Atrial fibrillation | 28416818 | [1.20-1.35] | 1.27 | EFO_0000275 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Early onset atrial fibrillation | 28460022 | [1.83-2.36] | 2.08 | EFO_0000275 |
| ENSG00000140836 | rs4499262 | 16 | 73025260 | A | Incident atrial fibrillation | 28416818 | 1.09-1.19 | 1.14 | EFO_0000275 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Prevalent atrial fibrillation | 28416818 | 1.19-1.31 | 1.25 | EFO_0000275 |
| ENSG00000140836 | rs75232769 | 16 | 72812192 | A | Facial morphology (factor 19) | 28441456 | [0.53-1.27] unit decrease | 0.8967 | EFO_0007841 |
| ENSG00000140836 | rs7190256 | 16 | 72963084 | ? | Age-related diseases and mortality | 27790247 | EFO_0000311|EFO_0003144|EFO_0000400|EFO_0000712|EFO_0001645|EFO_0000275|EFO_0004352 | ||
| ENSG00000140836 | rs2359171 | 16 | 73019123 | A | Atrial fibrillation | 29892015 | [1.19-1.23] | 1.21 | EFO_0000275 |
| ENSG00000140836 | rs2359171 | 16 | 73019123 | A | Atrial fibrillation | 29892015 | [1.17-1.22] | 1.2 | EFO_0000275 |
| ENSG00000140836 | rs12446956 | 16 | 73467637 | C | Major depressive disorder | 21042317 | [NR] | 1.22 | EFO_0003761 |
| ENSG00000140836 | rs9934948 | 16 | 73405456 | C | Breast cancer (survival) | 22232737 | [1.16-1.44] | 1.29 | EFO_0000714|EFO_0000305 |
| ENSG00000140836 | rs7189864 | 16 | 73600037 | ? | Photic sneeze reflex | 27182965 | [1.046-1.094] | 1.069 | EFO_0007887 |
| ENSG00000140836 | rs2106261 | 16 | 73017721 | T | Atrial fibrillation | 28416822 | [1.267-1.387] | 1.326 | EFO_0000275 |
| ENSG00000140836 | rs4888280 | 16 | 73431477 | A | Behavioural changes in frontotemporal lobe dementia | 29724592 | [1.71-2.29] | 2 | Orphanet_282|GO_0007610 |
| ENSG00000140836 | rs4888921 | 16 | 73866095 | ? | Reaction time | 29844566 | [0.0047-0.0116] unit increase | 0.0081513 | EFO_0008393 |
| ENSG00000140836 | rs756717 | 16 | 72962263 | G | Body mass index | 30108127 | [NR] unit increase | 0.015 | EFO_0004340 |
| ENSG00000140836 | rs876727 | 16 | 73033862 | T | Atrial fibrillation | 30061737 | [1.03-1.07] | 1.05 | EFO_0000275 |
| ENSG00000140836 | rs7197197 | 16 | 72877507 | ? | Heel bone mineral density | 30048462 | [0.0097-0.0181] unit decrease | 0.0139025 | EFO_0009270 |
| ENSG00000140836 | rs374035142 | 16 | 73883400 | ? | Heel bone mineral density | 30048462 | [0.0097-0.018] unit increase | 0.0138308 | EFO_0009270 |
| ENSG00000140836 | rs7198843 | 16 | 72877840 | T | Heel bone mineral density | 30598549 | [0.011-0.018] unit decrease | 0.0144254 | EFO_0009270 |
| ENSG00000140836 | rs756717 | 16 | 72962263 | ? | Body mass index | 30595370 | EFO_0004340 | ||
| ENSG00000140836 | rs117934006 | 16 | 73392991 | ? | Body mass index | 30595370 | EFO_0004340 | ||
| ENSG00000140836 | rs825680 | 16 | 73572664 | ? | Body mass index | 30595370 | EFO_0004340 | ||
| ENSG00000140836 | rs12932445 | 16 | 73035989 | ? | Stroke | 29531354 | EFO_0000712 | ||
| ENSG00000140836 | rs12932445 | 16 | 73035989 | ? | Ischemic stroke (cardioembolic) | 29531354 | EFO_1001976 | ||
| ENSG00000140836 | rs12930834 | 16 | 72917728 | A | Smoking status (ever vs never smokers) | 30643258 | [0.0091-0.0183] unit increase | 0.013715122 | EFO_0004318 |
| ENSG00000140836 | rs16972552 | 16 | 73776555 | C | Smoking status (ever vs never smokers) | 30643258 | [0.011-0.024] unit decrease | 0.017533675 | EFO_0004318 |
| ENSG00000140836 | rs6499595 | 16 | 72900544 | C | Number of sexual partners | 30643258 | [0.0085-0.0179] unit decrease | 0.013198892 | EFO_0007877 |
| ENSG00000140836 | rs62055084 | 16 | 73063946 | ? | Systolic blood pressure | 30595370 | EFO_0006335 | ||
| ENSG00000140836 | rs825702 | 16 | 73566673 | ? | Systolic blood pressure | 30595370 | EFO_0006335 | ||
| ENSG00000140836 | rs12922127 | 16 | 72925068 | ? | Lung function (FVC) | 30595370 | EFO_0004312 | ||
| ENSG00000140836 | rs4788676 | 16 | 72916569 | ? | Smoking status | 30595370 | EFO_0006527 | ||
| ENSG00000140836 | rs1104608 | 16 | 73878689 | C | Alcohol consumption (drinks per week) (MTAG) | 30643251 | [0.0068-0.0122] unit decrease | 0.00948981 | EFO_0007878 |
| ENSG00000140836 | rs739414 | 16 | 73064057 | T | Pulse pressure | 30578418 | [0.084-0.171] mmHg increase | 0.1276 | EFO_0005763 |
| ENSG00000140836 | rs6499595 | 16 | 72900544 | C | Risk-taking tendency (4-domain principal component model) | 30643258 | [0.0093-0.0196] unit decrease | 0.014426594 | EFO_0008579 |
| ENSG00000140836 | rs4788488 | 16 | 72926384 | ? | Lung function (FEV1/FVC) | 30595370 | EFO_0004713 | ||
| ENSG00000140836 | rs62041356 | 16 | 73676251 | C | Well-being spectrum (multivariate analysis) | 30643256 | [0.005-0.0104] unit increase | 0.007699552 | EFO_0007869 |
| ENSG00000140836 | rs7198843 | 16 | 72877840 | ? | Heel bone mineral density | 30595370 | EFO_0009270 | ||
| ENSG00000140836 | rs4788676 | 16 | 72916569 | C | Smoking initiation (ever regular vs never regular) (MTAG) | 30643251 | [0.0048-0.0098] unit decrease | 0.00731008 | EFO_0006527 |
| ENSG00000140836 | rs4129177 | 16 | 73243690 | C | Smoking initiation (ever regular vs never regular) (MTAG) | 30643251 | [0.0039-0.0083] unit increase | 0.00609175 | EFO_0006527 |
| ENSG00000140836 | rs4788676 | 16 | 72916569 | C | Smoking initiation (ever regular vs never regular) | 30643251 | [0.012-0.024] unit decrease | 0.017745035 | EFO_0006527 |
| ENSG00000140836 | rs1104608 | 16 | 73878689 | C | Alcohol consumption (drinks per week) | 30643251 | [0.0081-0.0139] unit decrease | 0.010974988 | EFO_0007878 |
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000140836 | ZFHX3 | 100 | 93.738 | ENSAMEG00000002197 | ZFHX3 | 100 | 94.249 | Ailuropoda_melanoleuca |
| ENSG00000140836 | ZFHX3 | 100 | 66.289 | ENSATEG00000004640 | zfhx3 | 100 | 62.487 | Anabas_testudineus |
| ENSG00000140836 | ZFHX3 | 84 | 88.186 | ENSAPLG00000002327 | ZFHX3 | 99 | 86.268 | Anas_platyrhynchos |
| ENSG00000140836 | ZFHX3 | 100 | 97.929 | ENSANAG00000033325 | ZFHX3 | 100 | 97.849 | Aotus_nancymaae |
| ENSG00000140836 | ZFHX3 | 69 | 64.677 | ENSACLG00000001914 | zfhx3 | 100 | 62.676 | Astatotilapia_calliptera |
| ENSG00000140836 | ZFHX3 | 100 | 66.233 | ENSAMXG00000004340 | zfhx3 | 100 | 63.033 | Astyanax_mexicanus |
| ENSG00000140836 | ZFHX3 | 100 | 93.455 | ENSBTAG00000014636 | ZFHX3 | 100 | 93.965 | Bos_taurus |
| ENSG00000140836 | ZFHX3 | 100 | 98.038 | ENSCJAG00000043080 | ZFHX3 | 100 | 98.010 | Callithrix_jacchus |
| ENSG00000140836 | ZFHX3 | 100 | 96.592 | ENSCAFG00000020243 | ZFHX3 | 100 | 96.592 | Canis_familiaris |
| ENSG00000140836 | ZFHX3 | 100 | 96.906 | ENSCAFG00020020336 | ZFHX3 | 100 | 96.906 | Canis_lupus_dingo |
| ENSG00000140836 | ZFHX3 | 100 | 93.672 | ENSCHIG00000018446 | ZFHX3 | 100 | 94.050 | Capra_hircus |
| ENSG00000140836 | ZFHX3 | 100 | 97.031 | ENSTSYG00000029930 | ZFHX3 | 100 | 96.765 | Carlito_syrichta |
| ENSG00000140836 | ZFHX3 | 95 | 100.000 | ENSCAPG00000010889 | ZFHX3 | 99 | 94.915 | Cavia_aperea |
| ENSG00000140836 | ZFHX3 | 100 | 95.881 | ENSCPOG00000009111 | ZFHX3 | 100 | 94.042 | Cavia_porcellus |
| ENSG00000140836 | ZFHX3 | 100 | 97.735 | ENSCCAG00000026346 | ZFHX3 | 100 | 97.735 | Cebus_capucinus |
| ENSG00000140836 | ZFHX3 | 100 | 98.435 | ENSCATG00000022545 | ZFHX3 | 100 | 98.435 | Cercocebus_atys |
| ENSG00000140836 | ZFHX3 | 100 | 94.552 | ENSCLAG00000007000 | ZFHX3 | 100 | 95.535 | Chinchilla_lanigera |
| ENSG00000140836 | ZFHX3 | 100 | 98.545 | ENSCSAG00000004171 | ZFHX3 | 100 | 98.545 | Chlorocebus_sabaeus |
| ENSG00000140836 | ZFHX3 | 100 | 98.920 | ENSCANG00000034216 | ZFHX3 | 100 | 98.920 | Colobus_angolensis_palliatus |
| ENSG00000140836 | ZFHX3 | 100 | 93.957 | ENSCGRG00001012831 | Zfhx3 | 100 | 94.335 | Cricetulus_griseus_chok1gshd |
| ENSG00000140836 | ZFHX3 | 100 | 93.797 | ENSCGRG00000001001 | Zfhx3 | 100 | 93.470 | Cricetulus_griseus_crigri |
| ENSG00000140836 | ZFHX3 | 100 | 65.074 | ENSCSEG00000001762 | zfhx3 | 100 | 61.357 | Cynoglossus_semilaevis |
| ENSG00000140836 | ZFHX3 | 100 | 64.949 | ENSDARG00000103057 | zfhx3 | 100 | 61.878 | Danio_rerio |
| ENSG00000140836 | ZFHX3 | 100 | 94.712 | ENSDNOG00000046047 | ZFHX3 | 100 | 94.217 | Dasypus_novemcinctus |
| ENSG00000140836 | ZFHX3 | 100 | 95.038 | ENSEASG00005021387 | ZFHX3 | 100 | 96.407 | Equus_asinus_asinus |
| ENSG00000140836 | ZFHX3 | 100 | 95.036 | ENSECAG00000022984 | ZFHX3 | 100 | 96.432 | Equus_caballus |
| ENSG00000140836 | ZFHX3 | 94 | 95.134 | ENSEEUG00000008705 | ZFHX3 | 92 | 94.680 | Erinaceus_europaeus |
| ENSG00000140836 | ZFHX3 | 100 | 66.815 | ENSELUG00000014311 | zfhx3 | 100 | 63.171 | Esox_lucius |
| ENSG00000140836 | ZFHX3 | 100 | 96.314 | ENSFCAG00000023839 | ZFHX3 | 100 | 96.314 | Felis_catus |
| ENSG00000140836 | ZFHX3 | 97 | 87.340 | ENSFALG00000002706 | ZFHX3 | 98 | 84.342 | Ficedula_albicollis |
| ENSG00000140836 | ZFHX3 | 100 | 93.720 | ENSFDAG00000015753 | ZFHX3 | 100 | 94.847 | Fukomys_damarensis |
| ENSG00000140836 | ZFHX3 | 100 | 65.324 | ENSFHEG00000013474 | zfhx3 | 97 | 76.560 | Fundulus_heteroclitus |
| ENSG00000140836 | ZFHX3 | 81 | 70.468 | ENSGMOG00000002909 | zfhx3 | 100 | 63.338 | Gadus_morhua |
| ENSG00000140836 | ZFHX3 | 100 | 85.300 | ENSGALG00000000713 | ZFHX3 | 100 | 85.917 | Gallus_gallus |
| ENSG00000140836 | ZFHX3 | 100 | 65.954 | ENSGAFG00000017278 | zfhx3 | 100 | 61.874 | Gambusia_affinis |
| ENSG00000140836 | ZFHX3 | 100 | 65.269 | ENSGACG00000015779 | zfhx3 | 100 | 62.477 | Gasterosteus_aculeatus |
| ENSG00000140836 | ZFHX3 | 100 | 86.314 | ENSGAGG00000002102 | ZFHX3 | 100 | 86.156 | Gopherus_agassizii |
| ENSG00000140836 | ZFHX3 | 99 | 99.268 | ENSGGOG00000012083 | ZFHX3 | 100 | 99.260 | Gorilla_gorilla |
| ENSG00000140836 | ZFHX3 | 69 | 64.639 | ENSHBUG00000013200 | zfhx3 | 100 | 62.676 | Haplochromis_burtoni |
| ENSG00000140836 | ZFHX3 | 100 | 95.391 | ENSHGLG00000012541 | ZFHX3 | 100 | 95.391 | Heterocephalus_glaber_female |
| ENSG00000140836 | ZFHX3 | 100 | 94.987 | ENSHGLG00100000797 | ZFHX3 | 100 | 94.960 | Heterocephalus_glaber_male |
| ENSG00000140836 | ZFHX3 | 81 | 68.960 | ENSHCOG00000003135 | zfhx3 | 100 | 61.060 | Hippocampus_comes |
| ENSG00000140836 | ZFHX3 | 81 | 69.949 | ENSIPUG00000006119 | zfhx3 | 100 | 62.809 | Ictalurus_punctatus |
| ENSG00000140836 | ZFHX3 | 100 | 96.130 | ENSSTOG00000027206 | ZFHX3 | 100 | 96.130 | Ictidomys_tridecemlineatus |
| ENSG00000140836 | ZFHX3 | 100 | 66.483 | ENSKMAG00000006781 | zfhx3 | 100 | 62.383 | Kryptolebias_marmoratus |
| ENSG00000140836 | ZFHX3 | 100 | 68.637 | ENSLOCG00000004206 | zfhx3 | 100 | 64.948 | Lepisosteus_oculatus |
| ENSG00000140836 | ZFHX3 | 100 | 96.009 | ENSLAFG00000017476 | ZFHX3 | 100 | 94.699 | Loxodonta_africana |
| ENSG00000140836 | ZFHX3 | 100 | 98.734 | ENSMFAG00000034225 | ZFHX3 | 100 | 98.734 | Macaca_fascicularis |
| ENSG00000140836 | ZFHX3 | 100 | 98.653 | ENSMMUG00000021041 | ZFHX3 | 100 | 98.330 | Macaca_mulatta |
| ENSG00000140836 | ZFHX3 | 100 | 98.653 | ENSMNEG00000030137 | ZFHX3 | 100 | 98.653 | Macaca_nemestrina |
| ENSG00000140836 | ZFHX3 | 100 | 98.812 | ENSMLEG00000042563 | ZFHX3 | 100 | 98.812 | Mandrillus_leucophaeus |
| ENSG00000140836 | ZFHX3 | 100 | 65.576 | ENSMAMG00000021509 | zfhx3 | 100 | 62.687 | Mastacembelus_armatus |
| ENSG00000140836 | ZFHX3 | 69 | 64.578 | ENSMZEG00005014216 | zfhx3 | 100 | 62.626 | Maylandia_zebra |
| ENSG00000140836 | ZFHX3 | 78 | 89.478 | ENSMGAG00000008764 | ZFHX3 | 97 | 89.226 | Meleagris_gallopavo |
| ENSG00000140836 | ZFHX3 | 100 | 93.152 | ENSMAUG00000000602 | Zfhx3 | 100 | 93.502 | Mesocricetus_auratus |
| ENSG00000140836 | ZFHX3 | 100 | 95.967 | ENSMICG00000003537 | ZFHX3 | 100 | 95.939 | Microcebus_murinus |
| ENSG00000140836 | ZFHX3 | 100 | 93.387 | ENSMOCG00000017998 | Zfhx3 | 100 | 93.925 | Microtus_ochrogaster |
| ENSG00000140836 | ZFHX3 | 100 | 66.518 | ENSMMOG00000016551 | zfhx3 | 100 | 62.503 | Mola_mola |
| ENSG00000140836 | ZFHX3 | 100 | 66.540 | ENSMALG00000021055 | zfhx3 | 100 | 62.974 | Monopterus_albus |
| ENSG00000140836 | ZFHX3 | 100 | 92.460 | ENSMUSG00000038872 | Zfhx3 | 100 | 93.289 | Mus_musculus |
| ENSG00000140836 | ZFHX3 | 100 | 92.584 | MGP_PahariEiJ_G0023139 | Zfhx3 | 100 | 92.905 | Mus_pahari |
| ENSG00000140836 | ZFHX3 | 100 | 92.406 | MGP_SPRETEiJ_G0032657 | Zfhx3 | 100 | 93.342 | Mus_spretus |
| ENSG00000140836 | ZFHX3 | 100 | 92.374 | ENSMPUG00000007747 | ZFHX3 | 100 | 92.374 | Mustela_putorius_furo |
| ENSG00000140836 | ZFHX3 | 100 | 95.202 | ENSMLUG00000016100 | ZFHX3 | 100 | 95.171 | Myotis_lucifugus |
| ENSG00000140836 | ZFHX3 | 100 | 91.876 | ENSNGAG00000001724 | Zfhx3 | 100 | 92.362 | Nannospalax_galili |
| ENSG00000140836 | ZFHX3 | 69 | 64.593 | ENSNBRG00000010822 | zfhx3 | 100 | 62.824 | Neolamprologus_brichardi |
| ENSG00000140836 | ZFHX3 | 88 | 97.436 | ENSNLEG00000032567 | ZFHX3 | 99 | 97.436 | Nomascus_leucogenys |
| ENSG00000140836 | ZFHX3 | 100 | 92.530 | ENSODEG00000014257 | ZFHX3 | 100 | 92.238 | Octodon_degus |
| ENSG00000140836 | ZFHX3 | 57 | 79.137 | ENSONIG00000005914 | zfhx3 | 95 | 77.199 | Oreochromis_niloticus |
| ENSG00000140836 | ZFHX3 | 86 | 91.147 | ENSOANG00000005084 | ZFHX3 | 100 | 90.780 | Ornithorhynchus_anatinus |
| ENSG00000140836 | ZFHX3 | 100 | 94.957 | ENSOCUG00000017910 | - | 99 | 94.198 | Oryctolagus_cuniculus |
| ENSG00000140836 | ZFHX3 | 81 | 68.988 | ENSORLG00000007874 | zfhx3 | 100 | 61.723 | Oryzias_latipes |
| ENSG00000140836 | ZFHX3 | 100 | 65.331 | ENSORLG00020009729 | zfhx3 | 100 | 61.803 | Oryzias_latipes_hni |
| ENSG00000140836 | ZFHX3 | 81 | 68.918 | ENSORLG00015007912 | zfhx3 | 100 | 61.546 | Oryzias_latipes_hsok |
| ENSG00000140836 | ZFHX3 | 81 | 69.667 | ENSOMEG00000001800 | zfhx3 | 100 | 61.861 | Oryzias_melastigma |
| ENSG00000140836 | ZFHX3 | 100 | 95.899 | ENSPPRG00000005184 | ZFHX3 | 100 | 95.899 | Panthera_pardus |
| ENSG00000140836 | ZFHX3 | 100 | 99.217 | ENSPTRG00000008340 | ZFHX3 | 100 | 99.217 | Pan_troglodytes |
| ENSG00000140836 | ZFHX3 | 100 | 98.626 | ENSPANG00000010456 | ZFHX3 | 100 | 98.626 | Papio_anubis |
| ENSG00000140836 | ZFHX3 | 99 | 64.690 | ENSPKIG00000001525 | - | 83 | 65.114 | Paramormyrops_kingsleyae |
| ENSG00000140836 | ZFHX3 | 96 | 67.964 | ENSPKIG00000009598 | zfhx3 | 98 | 63.415 | Paramormyrops_kingsleyae |
| ENSG00000140836 | ZFHX3 | 81 | 70.667 | ENSPMGG00000006062 | zfhx3 | 98 | 70.866 | Periophthalmus_magnuspinnatus |
| ENSG00000140836 | ZFHX3 | 100 | 94.232 | ENSPEMG00000010630 | Zfhx3 | 100 | 94.771 | Peromyscus_maniculatus_bairdii |
| ENSG00000140836 | ZFHX3 | 100 | 65.311 | ENSPFOG00000001702 | zfhx3 | 100 | 61.858 | Poecilia_formosa |
| ENSG00000140836 | ZFHX3 | 100 | 65.931 | ENSPLAG00000018955 | zfhx3 | 100 | 62.069 | Poecilia_latipinna |
| ENSG00000140836 | ZFHX3 | 100 | 65.299 | ENSPMEG00000022333 | zfhx3 | 100 | 61.905 | Poecilia_mexicana |
| ENSG00000140836 | ZFHX3 | 100 | 98.570 | ENSPPYG00000007513 | ZFHX3 | 100 | 98.709 | Pongo_abelii |
| ENSG00000140836 | ZFHX3 | 100 | 93.209 | ENSPCAG00000010600 | ZFHX3 | 99 | 93.736 | Procavia_capensis |
| ENSG00000140836 | ZFHX3 | 100 | 96.505 | ENSPCOG00000025382 | ZFHX3 | 100 | 96.477 | Propithecus_coquereli |
| ENSG00000140836 | ZFHX3 | 96 | 95.925 | ENSPVAG00000006664 | ZFHX3 | 96 | 96.145 | Pteropus_vampyrus |
| ENSG00000140836 | ZFHX3 | 69 | 64.110 | ENSPNYG00000013409 | zfhx3 | 100 | 62.431 | Pundamilia_nyererei |
| ENSG00000140836 | ZFHX3 | 100 | 93.647 | ENSRNOG00000014452 | Zfhx3 | 100 | 94.051 | Rattus_norvegicus |
| ENSG00000140836 | ZFHX3 | 100 | 97.813 | ENSRBIG00000031579 | ZFHX3 | 100 | 97.813 | Rhinopithecus_bieti |
| ENSG00000140836 | ZFHX3 | 100 | 98.761 | ENSRROG00000039904 | ZFHX3 | 100 | 98.761 | Rhinopithecus_roxellana |
| ENSG00000140836 | ZFHX3 | 92 | 97.857 | ENSSBOG00000034332 | ZFHX3 | 96 | 97.857 | Saimiri_boliviensis_boliviensis |
| ENSG00000140836 | ZFHX3 | 100 | 65.410 | ENSSFOG00015019511 | zfhx3 | 99 | 63.100 | Scleropages_formosus |
| ENSG00000140836 | ZFHX3 | 100 | 66.337 | ENSSFOG00015014986 | zfhx3 | 99 | 71.795 | Scleropages_formosus |
| ENSG00000140836 | ZFHX3 | 100 | 66.974 | ENSSMAG00000000110 | zfhx3 | 100 | 62.829 | Scophthalmus_maximus |
| ENSG00000140836 | ZFHX3 | 100 | 66.380 | ENSSPAG00000002113 | zfhx3 | 100 | 63.190 | Stegastes_partitus |
| ENSG00000140836 | ZFHX3 | 100 | 96.161 | ENSSSCG00000002752 | ZFHX3 | 100 | 95.824 | Sus_scrofa |
| ENSG00000140836 | ZFHX3 | 85 | 85.348 | ENSTGUG00000008190 | ZFHX3 | 86 | 85.448 | Taeniopygia_guttata |
| ENSG00000140836 | ZFHX3 | 100 | 96.594 | ENSVVUG00000017344 | ZFHX3 | 100 | 96.594 | Vulpes_vulpes |
| ENSG00000140836 | ZFHX3 | 100 | 65.636 | ENSXMAG00000027288 | zfhx3 | 100 | 62.085 | Xiphophorus_maculatus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000122 | negative regulation of transcription by RNA polymerase II | 21873635. | IBA | Process |
| GO:0000122 | negative regulation of transcription by RNA polymerase II | 11314020. | IDA | Process |
| GO:0000122 | negative regulation of transcription by RNA polymerase II | 10318867. | IGI | Process |
| GO:0000978 | RNA polymerase II proximal promoter sequence-specific DNA binding | 21873635. | IBA | Function |
| GO:0000978 | RNA polymerase II proximal promoter sequence-specific DNA binding | 7507206. | IDA | Function |
| GO:0000978 | RNA polymerase II proximal promoter sequence-specific DNA binding | - | ISS | Function |
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | - | ISA | Function |
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | 19274049. | ISM | Function |
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | 19274049. | NAS | Function |
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | 1719379. | TAS | Function |
| GO:0001227 | DNA-binding transcription repressor activity, RNA polymerase II-specific | - | IC | Function |
| GO:0003700 | DNA-binding transcription factor activity | 1719379. | NAS | Function |
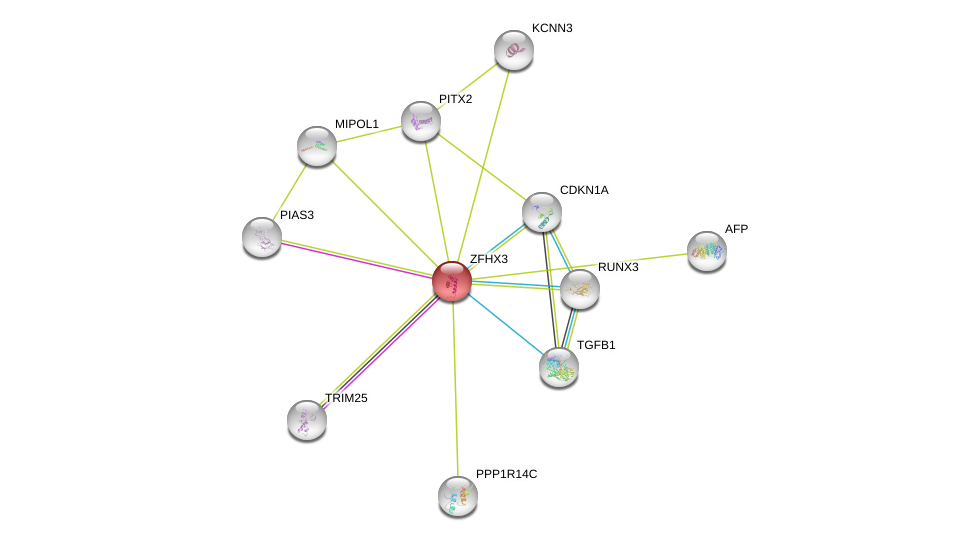
| GO:0005515 | protein binding | 20599712.22452784. | IPI | Function |
| GO:0005634 | nucleus | 21873635. | IBA | Component |
| GO:0005634 | nucleus | 20599712.24651376. | IDA | Component |
| GO:0005634 | nucleus | 1719379. | TAS | Component |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0005667 | transcription factor complex | 10318867. | IDA | Component |
| GO:0005737 | cytoplasm | 20599712. | IDA | Component |
| GO:0006355 | regulation of transcription, DNA-templated | 1719379. | TAS | Process |
| GO:0006366 | transcription by RNA polymerase II | 1719379. | TAS | Process |
| GO:0007050 | cell cycle arrest | - | IEA | Process |
| GO:0007420 | brain development | 21873635. | IBA | Process |
| GO:0007517 | muscle organ development | - | IEA | Process |
| GO:0008270 | zinc ion binding | - | IEA | Function |
| GO:0016604 | nuclear body | 24651376. | IDA | Component |
| GO:0019899 | enzyme binding | 14715251. | IPI | Function |
| GO:0032922 | circadian regulation of gene expression | - | ISS | Process |
| GO:0044212 | transcription regulatory region DNA binding | 21873635. | IBA | Function |
| GO:0045664 | regulation of neuron differentiation | 21873635. | IBA | Process |
| GO:0045785 | positive regulation of cell adhesion | - | ISS | Process |
| GO:0045893 | positive regulation of transcription, DNA-templated | 21873635. | IBA | Process |
| GO:0045893 | positive regulation of transcription, DNA-templated | 20599712. | IDA | Process |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | - | ISS | Process |
| GO:0071559 | response to transforming growth factor beta | 20599712. | IDA | Process |
| GO:1904059 | regulation of locomotor rhythm | - | ISS | Process |