
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| CHOL | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LAML | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| THYM | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UVM |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| CHOL | |||
| HNSC | |||
| LUAD | |||
| PAAD | |||
| SARC | |||
| SKCM | |||
| TGCT | |||
| THYM | |||
| UVM |
| Cancer | P-value | Q-value |
|---|---|---|
| SARC | ||
| MESO | ||
| SKCM | ||
| BRCA | ||
| KIRP | ||
| COAD | ||
| BLCA | ||
| READ | ||
| LAML | ||
| KICH | ||
| LUAD | ||
| UVM |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000485215 | PTPRG-206 | 724 | - | - | - (aa) | - | - |
| ENST00000495879 | PTPRG-207 | 3011 | - | - | - (aa) | - | - |
| ENST00000295874 | PTPRG-201 | 4650 | XM_005265353 | ENSP00000295874 | 1416 (aa) | XP_005265410 | P23470 |
| ENST00000468576 | PTPRG-202 | 854 | - | - | - (aa) | - | - |
| ENST00000475012 | PTPRG-204 | 2635 | - | - | - (aa) | - | - |
| ENST00000475527 | PTPRG-205 | 2694 | - | - | - (aa) | - | - |
| ENST00000474889 | PTPRG-203 | 9021 | XM_017006961 | ENSP00000418112 | 1445 (aa) | XP_016862450 | P23470 |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000144724 | Lipids | 5.32831414289751E-6 | 17903299 |
| ENSG00000144724 | Hip | 1.2101855243664E-5 | 17903296 |
| ENSG00000144724 | Diabetes Mellitus, Type 2 | 7.185084E-5 | 17463248 |
| ENSG00000144724 | Body Mass Index | 9.638e-005 | 19060910 |
| ENSG00000144724 | C-Reactive Protein | 2.522e-005 | 19060910 |
| ENSG00000144724 | Platelet Count | 9.881e-005 | - |
| ENSG00000144724 | Triglycerides | 9.325e-005 | - |
| ENSG00000144724 | Personality | 8.812e-005 | - |
| ENSG00000144724 | Waist Circumference | 9.8070000E-005 | - |
| ENSG00000144724 | Waist Circumference | 3.4690000E-006 | - |
| ENSG00000144724 | Arteries | 3.0990000E-005 | - |
| ENSG00000144724 | Blood Glucose | 9.5690000E-005 | - |
| ENSG00000144724 | Cell Adhesion Molecules | 3.8120000E-005 | - |
| ENSG00000144724 | Platelet Function Tests | 1.4338700E-005 | - |
| ENSG00000144724 | Platelet Function Tests | 1.5991000E-005 | - |
| ENSG00000144724 | Platelet Function Tests | 4.8800000E-006 | - |
| ENSG00000144724 | Platelet Function Tests | 1.3316800E-005 | - |
| ENSG00000144724 | Platelet Function Tests | 1.1550200E-005 | - |
| ENSG00000144724 | Platelet Function Tests | 2.3210200E-005 | - |
| ENSG00000144724 | Platelet Function Tests | 2.5084200E-005 | - |
| ENSG00000144724 | Platelet Function Tests | 2.2060100E-005 | - |
| ENSG00000144724 | Fluorescence | 8.2610000E-006 | 24934506 |
| ENSG00000144724 | Electrocardiography | 8E-7 | 20031603 |
| ENSG00000144724 | Alzheimer Disease | 4E-8 | 26830138 |
| ENSG00000144724 | Age of Onset | 4E-8 | 26830138 |
| ENSG00000144724 | Stroke | 7E-7 | 26089329 |
| ENSG00000144724 | Stroke | 6E-7 | 26089329 |
| ENSG00000144724 | Schizophrenia | 2E-6 | 21926974 |
| ENSG00000144724 | Homovanillic Acid | 5E-6 | 23319000 |
| ENSG00000144724 | Hydroxyindoleacetic Acid | 5E-6 | 23319000 |
| ENSG00000144724 | Stroke | 6E-7 | 26089329 |
| ENSG00000144724 | Bacteremia | 1E-7 | 27236921 |
| ENSG00000144724 | Stroke | 7E-7 | 26089329 |
| ENSG00000144724 | Attention Deficit Disorder with Hyperactivity | 8E-7 | 27890468 |
| ENSG00000144724 | Bipolar Disorder | 8E-7 | 27890468 |
| ENSG00000144724 | Fuchs' Endothelial Dystrophy | 1E-6 | 20825314 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000144724 | rs7633054 | 3 | 62153280 | ? | Bacteremia | 27236921 | [NR] | 1.36 | EFO_0003033 |
| ENSG00000144724 | rs13061878 | 3 | 61634560 | ? | Bipolar disorder or attention deficit hyperactivity disorder | 27890468 | EFO_0003888|EFO_0000289 | ||
| ENSG00000144724 | rs7609954 | 3 | 61650482 | T | Alzheimer disease and age of onset | 26830138 | unit increase | 5.492 | EFO_0000249|EFO_0004847 |
| ENSG00000144724 | rs704341 | 3 | 61963062 | A | Stroke | 26089329 | [1.40-2.14] | 1.73 | EFO_0000712 |
| ENSG00000144724 | rs704341 | 3 | 61963062 | A | Stroke | 26089329 | [0.33-0.77] unit increase | 0.55 | EFO_0000712 |
| ENSG00000144724 | rs704341 | 3 | 61963062 | A | Ischemic stroke | 26089329 | [1.45-2.36] | 1.85 | HP_0002140 |
| ENSG00000144724 | rs704341 | 3 | 61963062 | A | Ischemic stroke | 26089329 | [0.38-0.86] unit increase | 0.62 | HP_0002140 |
| ENSG00000144724 | rs652889 | 3 | 61808380 | A | QT interval | 20031603 | [0.09-0.21] unit decrease | 0.15 | EFO_0004682 |
| ENSG00000144724 | rs35593266 | 3 | 62126467 | A | Metabolite levels (HVA/5-HIAA ratio) | 23319000 | unit increase | 0.2196 | EFO_0005131|EFO_0005132 |
| ENSG00000144724 | rs40493 | 3 | 61989275 | C | Major depressive disorder | 29317602 | [0.071-0.189] unit increase | 0.13 | EFO_0003761 |
| ENSG00000144724 | rs4688651 | 3 | 61651395 | A | Osteoarthritis (self-reported) | 29559693 | [1.14-1.1] | 1.0981276 | EFO_0002506 |
| ENSG00000144724 | rs11130874 | 3 | 62079095 | ? | Schizophrenia | 21926974 | [1.06-1.14] | 1.1 | EFO_0000692 |
| ENSG00000144724 | rs10490775 | 3 | 62051050 | A | Fuchs's corneal dystrophy | 20825314 | [1.64-3.22] | 2.3 | Orphanet_98974 |
| ENSG00000144724 | rs660323 | 3 | 61776956 | ? | Peripheral arterial disease (traffic-related air pollution interaction) | 27082954 | [4.72-6.44] | 5.58 | EFO_0004265|EFO_0007908 |
| ENSG00000144724 | rs6445258 | 3 | 62126524 | ? | Body mass index | 30595370 | EFO_0004340 | ||
| ENSG00000144724 | rs7621604 | 3 | 61572044 | ? | Waist-hip ratio | 30595370 | EFO_0004343 |
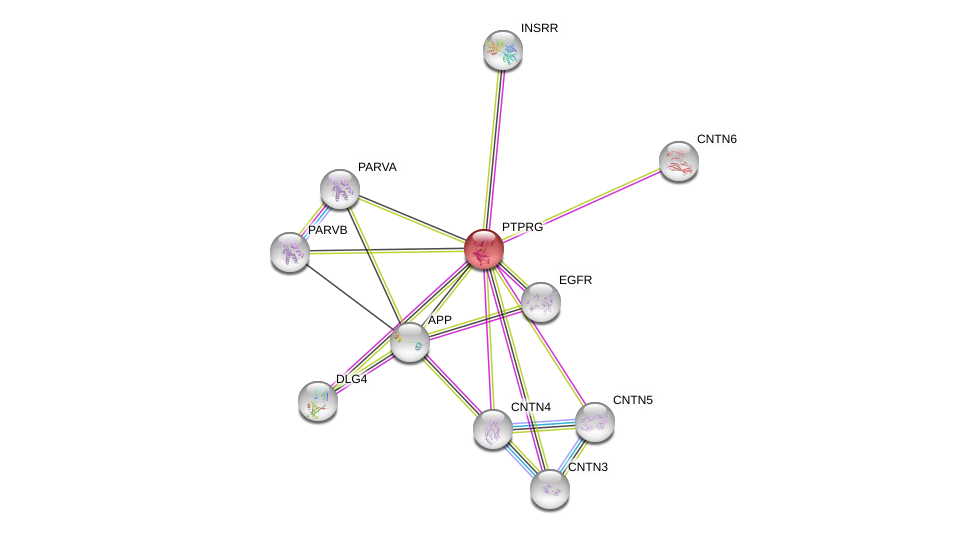
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0004725 | protein tyrosine phosphatase activity | 19167335. | IDA | Function |
| GO:0005001 | transmembrane receptor protein tyrosine phosphatase activity | 8382771. | TAS | Function |
| GO:0005515 | protein binding | 19167335.21112398.25970784. | IPI | Function |
| GO:0005887 | integral component of plasma membrane | 8382771. | TAS | Component |
| GO:0007169 | transmembrane receptor protein tyrosine kinase signaling pathway | 8382771. | TAS | Process |
| GO:0007420 | brain development | - | IEA | Process |
| GO:0010633 | negative regulation of epithelial cell migration | 21724833. | IMP | Process |
| GO:0010977 | negative regulation of neuron projection development | - | IEA | Process |
| GO:0035335 | peptidyl-tyrosine dephosphorylation | - | IEA | Process |
| GO:0042802 | identical protein binding | 19167335. | IPI | Function |
| GO:0070062 | extracellular exosome | 23533145. | HDA | Component |
| GO:1903385 | regulation of homophilic cell adhesion | 21724833. | IMP | Process |