
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| KIRC | |||||||
| LAML | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| CESC | |||
| COAD | |||
| KIRC | |||
| LGG | |||
| MESO | |||
| THCA |
| Cancer | P-value | Q-value |
|---|---|---|
| THYM | ||
| STAD | ||
| SARC | ||
| ACC | ||
| SKCM | ||
| BRCA | ||
| TGCT | ||
| BLCA | ||
| LAML | ||
| LGG | ||
| UVM |
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000282026 | MMR_HSR1 | PF01926.23 | 0.00013 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000282026 | ARL11-201 | 3760 | XM_005266253 | ENSP00000282026 | 196 (aa) | XP_005266310 | Q969Q4 |
| ENST00000490932 | ARL11-202 | 217 | - | - | - (aa) | - | - |
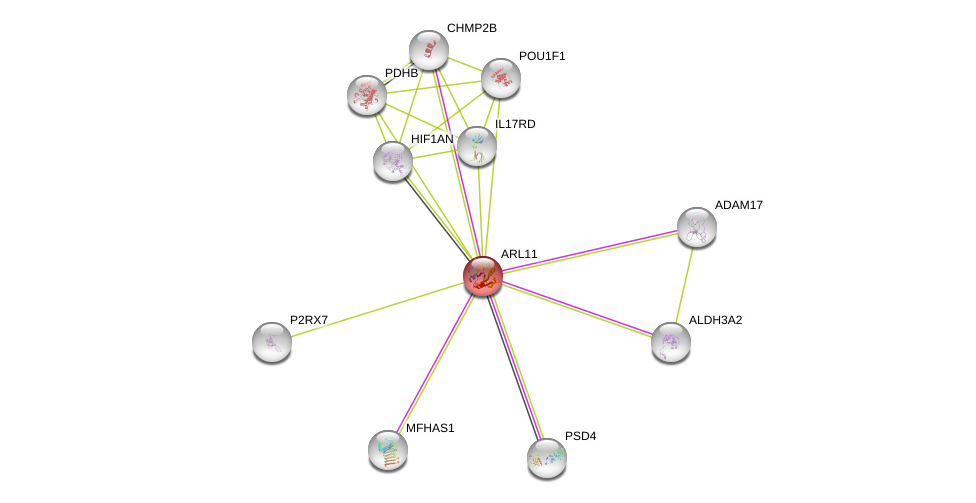
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000152213 | ARL11 | 96 | 85.185 | ENSAMEG00000002767 | ARL11 | 100 | 85.185 | Ailuropoda_melanoleuca |
| ENSG00000152213 | ARL11 | 100 | 89.796 | ENSCJAG00000022614 | ARL11 | 100 | 89.796 | Callithrix_jacchus |
| ENSG00000152213 | ARL11 | 97 | 74.211 | ENSCAPG00000006154 | ARL11 | 96 | 74.211 | Cavia_aperea |
| ENSG00000152213 | ARL11 | 97 | 74.211 | ENSCPOG00000040608 | ARL11 | 96 | 74.211 | Cavia_porcellus |
| ENSG00000152213 | ARL11 | 100 | 95.408 | ENSCATG00000011750 | ARL11 | 100 | 95.408 | Cercocebus_atys |
| ENSG00000152213 | ARL11 | 95 | 77.419 | ENSCLAG00000005195 | ARL11 | 94 | 77.419 | Chinchilla_lanigera |
| ENSG00000152213 | ARL11 | 100 | 94.898 | ENSCSAG00000018612 | ARL11 | 100 | 94.898 | Chlorocebus_sabaeus |
| ENSG00000152213 | ARL11 | 92 | 61.290 | ENSCPBG00000008579 | ARL11 | 93 | 61.290 | Chrysemys_picta_bellii |
| ENSG00000152213 | ARL11 | 100 | 95.408 | ENSCANG00000018107 | ARL11 | 100 | 95.408 | Colobus_angolensis_palliatus |
| ENSG00000152213 | ARL11 | 91 | 85.393 | ENSCGRG00001010023 | Arl11 | 100 | 85.393 | Cricetulus_griseus_chok1gshd |
| ENSG00000152213 | ARL11 | 91 | 85.393 | ENSCGRG00000006897 | Arl11 | 100 | 85.393 | Cricetulus_griseus_crigri |
| ENSG00000152213 | ARL11 | 100 | 80.203 | ENSDNOG00000009737 | ARL11 | 100 | 80.203 | Dasypus_novemcinctus |
| ENSG00000152213 | ARL11 | 90 | 86.364 | ENSDORG00000023352 | Arl11 | 95 | 86.364 | Dipodomys_ordii |
| ENSG00000152213 | ARL11 | 90 | 88.636 | ENSEASG00005017293 | ARL11 | 97 | 88.636 | Equus_asinus_asinus |
| ENSG00000152213 | ARL11 | 90 | 88.636 | ENSECAG00000004611 | ARL11 | 97 | 88.636 | Equus_caballus |
| ENSG00000152213 | ARL11 | 89 | 83.429 | ENSEEUG00000009809 | ARL11 | 92 | 83.429 | Erinaceus_europaeus |
| ENSG00000152213 | ARL11 | 89 | 83.429 | ENSFDAG00000000040 | ARL11 | 99 | 83.429 | Fukomys_damarensis |
| ENSG00000152213 | ARL11 | 91 | 62.162 | ENSGAGG00000019477 | ARL11 | 97 | 62.162 | Gopherus_agassizii |
| ENSG00000152213 | ARL11 | 100 | 98.980 | ENSGGOG00000004442 | ARL11 | 100 | 98.980 | Gorilla_gorilla |
| ENSG00000152213 | ARL11 | 92 | 79.558 | ENSHGLG00000006725 | ARL11 | 99 | 79.558 | Heterocephalus_glaber_female |
| ENSG00000152213 | ARL11 | 92 | 79.558 | ENSHGLG00100009774 | ARL11 | 99 | 79.558 | Heterocephalus_glaber_male |
| ENSG00000152213 | ARL11 | 90 | 81.356 | ENSJJAG00000001803 | Arl11 | 95 | 81.356 | Jaculus_jaculus |
| ENSG00000152213 | ARL11 | 86 | 54.706 | ENSLACG00000011405 | ARL11 | 89 | 54.706 | Latimeria_chalumnae |
| ENSG00000152213 | ARL11 | 90 | 86.364 | ENSLAFG00000001838 | ARL11 | 100 | 86.364 | Loxodonta_africana |
| ENSG00000152213 | ARL11 | 100 | 94.388 | ENSMMUG00000011766 | ARL11 | 100 | 94.388 | Macaca_mulatta |
| ENSG00000152213 | ARL11 | 100 | 95.408 | ENSMLEG00000013105 | ARL11 | 100 | 95.408 | Mandrillus_leucophaeus |
| ENSG00000152213 | ARL11 | 91 | 80.337 | ENSMICG00000006637 | ARL11 | 97 | 80.337 | Microcebus_murinus |
| ENSG00000152213 | ARL11 | 89 | 85.143 | ENSMOCG00000006454 | Arl11 | 99 | 85.143 | Microtus_ochrogaster |
| ENSG00000152213 | ARL11 | 98 | 66.495 | ENSMODG00000024105 | ARL11 | 100 | 66.495 | Monodelphis_domestica |
| ENSG00000152213 | ARL11 | 90 | 86.932 | MGP_CAROLIEiJ_G0019382 | Arl11 | 100 | 86.932 | Mus_caroli |
| ENSG00000152213 | ARL11 | 90 | 86.364 | ENSMUSG00000043157 | Arl11 | 100 | 86.364 | Mus_musculus |
| ENSG00000152213 | ARL11 | 90 | 85.227 | MGP_PahariEiJ_G0030400 | Arl11 | 100 | 85.227 | Mus_pahari |
| ENSG00000152213 | ARL11 | 90 | 84.659 | MGP_SPRETEiJ_G0020274 | Arl11 | 100 | 84.659 | Mus_spretus |
| ENSG00000152213 | ARL11 | 92 | 83.978 | ENSMPUG00000018376 | ARL11 | 96 | 83.978 | Mustela_putorius_furo |
| ENSG00000152213 | ARL11 | 90 | 83.616 | ENSMLUG00000029560 | ARL11 | 97 | 83.616 | Myotis_lucifugus |
| ENSG00000152213 | ARL11 | 90 | 88.068 | ENSNGAG00000004637 | Arl11 | 100 | 88.068 | Nannospalax_galili |
| ENSG00000152213 | ARL11 | 100 | 98.980 | ENSNLEG00000031734 | ARL11 | 100 | 98.980 | Nomascus_leucogenys |
| ENSG00000152213 | ARL11 | 90 | 69.663 | ENSOANG00000015544 | ARL11 | 97 | 69.663 | Ornithorhynchus_anatinus |
| ENSG00000152213 | ARL11 | 90 | 83.523 | ENSOCUG00000003013 | ARL11 | 98 | 83.523 | Oryctolagus_cuniculus |
| ENSG00000152213 | ARL11 | 90 | 84.181 | ENSOGAG00000005346 | ARL11 | 100 | 84.181 | Otolemur_garnettii |
| ENSG00000152213 | ARL11 | 90 | 79.096 | ENSOARG00000005963 | ARL11 | 98 | 79.096 | Ovis_aries |
| ENSG00000152213 | ARL11 | 100 | 98.980 | ENSPPAG00000033238 | ARL11 | 100 | 98.980 | Pan_paniscus |
| ENSG00000152213 | ARL11 | 100 | 98.980 | ENSPTRG00000005876 | ARL11 | 100 | 98.980 | Pan_troglodytes |
| ENSG00000152213 | ARL11 | 100 | 95.408 | ENSPANG00000006280 | ARL11 | 100 | 95.408 | Papio_anubis |
| ENSG00000152213 | ARL11 | 92 | 60.000 | ENSPSIG00000001265 | ARL11 | 100 | 60.000 | Pelodiscus_sinensis |
| ENSG00000152213 | ARL11 | 86 | 69.412 | ENSPCIG00000002831 | ARL11 | 95 | 69.412 | Phascolarctos_cinereus |
| ENSG00000152213 | ARL11 | 89 | 84.000 | ENSRNOG00000014653 | Arl11 | 100 | 84.000 | Rattus_norvegicus |
| ENSG00000152213 | ARL11 | 100 | 95.408 | ENSRBIG00000024949 | ARL11 | 100 | 95.408 | Rhinopithecus_bieti |
| ENSG00000152213 | ARL11 | 100 | 95.408 | ENSRROG00000000591 | ARL11 | 100 | 95.408 | Rhinopithecus_roxellana |
| ENSG00000152213 | ARL11 | 98 | 64.433 | ENSSHAG00000004853 | ARL11 | 100 | 64.433 | Sarcophilus_harrisii |
| ENSG00000152213 | ARL11 | 92 | 56.216 | ENSSPUG00000006852 | ARL11 | 98 | 56.216 | Sphenodon_punctatus |
| ENSG00000152213 | ARL11 | 91 | 79.444 | ENSSSCG00000036810 | ARL11 | 91 | 79.444 | Sus_scrofa |
| ENSG00000152213 | ARL11 | 92 | 85.635 | ENSUAMG00000009531 | ARL11 | 99 | 85.635 | Ursus_americanus |
| ENSG00000152213 | ARL11 | 92 | 85.635 | ENSUMAG00000018435 | ARL11 | 99 | 85.635 | Ursus_maritimus |
| ENSG00000152213 | ARL11 | 89 | 58.286 | ENSXETG00000015673 | arl11 | 99 | 58.286 | Xenopus_tropicalis |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0002244 | hematopoietic progenitor cell differentiation | - | IEA | Process |
| GO:0005515 | protein binding | 16189514.19060904. | IPI | Function |
| GO:0005525 | GTP binding | 21873635. | IBA | Function |
| GO:0005737 | cytoplasm | 21873635. | IBA | Component |
| GO:0005886 | plasma membrane | 21873635. | IBA | Component |
| GO:0006886 | intracellular protein transport | 21873635. | IBA | Process |
| GO:0016192 | vesicle-mediated transport | 21873635. | IBA | Process |