
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| ACC | |||
| DLBC | |||
| THCA | |||
| UCS | |||
| UVM |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| MESO | ||
| KIRP | ||
| PAAD | ||
| READ | ||
| LAML | ||
| KICH | ||
| LIHC | ||
| LGG | ||
| THCA | ||
| UVM | ||
| OV |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000430627 | CDK12-201 | 5918 | - | ENSP00000407720 | 1481 (aa) | - | Q9NYV4 |
| ENST00000581963 | CDK12-207 | 436 | - | - | - (aa) | - | - |
| ENST00000584336 | CDK12-208 | 1963 | - | - | - (aa) | - | - |
| ENST00000581593 | CDK12-206 | 559 | - | - | - (aa) | - | - |
| ENST00000559545 | CDK12-204 | 586 | - | - | - (aa) | - | - |
| ENST00000559663 | CDK12-205 | 871 | - | ENSP00000453329 | 159 (aa) | - | H0YLT2 |
| ENST00000447079 | CDK12-202 | 8336 | XM_005257456 | ENSP00000398880 | 1490 (aa) | XP_005257513 | Q9NYV4 |
| ENST00000558240 | CDK12-203 | 555 | - | - | - (aa) | - | - |
| ENST00000585161 | CDK12-210 | 2036 | - | - | - (aa) | - | - |
| ENST00000584632 | CDK12-209 | 4165 | XM_005257458 | ENSP00000464641 | 1201 (aa) | XP_005257515 | J3QSD7 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000167258 | rs11078903 | 17 | 39475671 | A | Glomerular filtration rate | 27588450 | [0.32-0.81] unit decrease | 0.564 | EFO_0005208 |
| ENSG00000167258 | rs7219014 | 17 | 39468537 | A | Urinary metabolites | 26352407 | [NR] unit decrease | 0.156 | EFO_0005116 |
| ENSG00000167258 | rs12451586 | 17 | 39477582 | A | Glomerular filtration rate (creatinine) | 28452372 | [0.007-0.0114] unit decrease | 0.0092 | EFO_0005208|EFO_0004518 |
| ENSG00000167258 | rs11650776 | 17 | 39485149 | A | Lung function (FEV1) | 28166213 | [0.017-0.037] unit increase | 0.027 | EFO_0004314 |
| ENSG00000167258 | rs12449852 | 17 | 39475835 | ? | Red cell distribution width | 30595370 | EFO_0005192 | ||
| ENSG00000167258 | rs4795384 | 17 | 39560518 | G | Estimated glomerular filtration rate | 30604766 | [0.2-0.59] ml/min/1.73m2 decrease | 0.395 | EFO_0005208 |
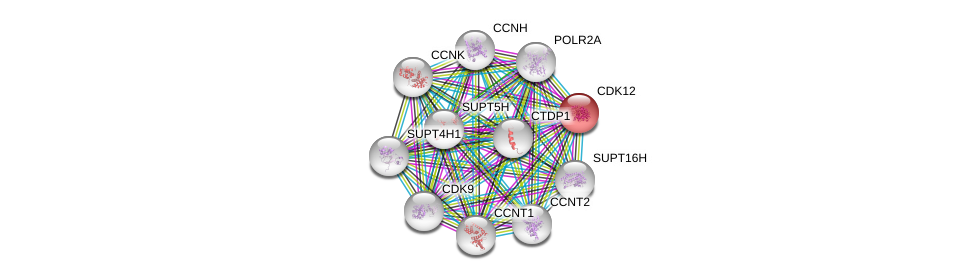
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000167258 | CDK12 | 100 | 90.201 | ENSMUSG00000003119 | Cdk12 | 100 | 90.268 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000307 | cyclin-dependent protein kinase holoenzyme complex | 21873635. | IBA | Component |
| GO:0000790 | nuclear chromatin | 21873635. | IBA | Component |
| GO:0001650 | fibrillar center | - | IDA | Component |
| GO:0002944 | cyclin K-CDK12 complex | 22012619. | IPI | Component |
| GO:0004672 | protein kinase activity | 11683387. | IDA | Function |
| GO:0004693 | cyclin-dependent protein serine/threonine kinase activity | 21873635. | IBA | Function |
| GO:0005515 | protein binding | 12841360. | IPI | Function |
| GO:0005524 | ATP binding | - | IEA | Function |
| GO:0005634 | nucleus | 21873635. | IBA | Component |
| GO:0005634 | nucleus | - | IDA | Component |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0005694 | chromosome | 21873635. | IBA | Component |
| GO:0006368 | transcription elongation from RNA polymerase II promoter | 21873635. | IBA | Process |
| GO:0006397 | mRNA processing | - | IEA | Process |
| GO:0006468 | protein phosphorylation | 21873635. | IBA | Process |
| GO:0008024 | cyclin/CDK positive transcription elongation factor complex | 21873635. | IBA | Component |
| GO:0008134 | transcription factor binding | 21873635. | IBA | Function |
| GO:0008353 | RNA polymerase II CTD heptapeptide repeat kinase activity | 21873635. | IBA | Function |
| GO:0008353 | RNA polymerase II CTD heptapeptide repeat kinase activity | 20952539. | IMP | Function |
| GO:0008380 | RNA splicing | - | ISS | Process |
| GO:0016607 | nuclear speck | 11683387. | IDA | Component |
| GO:0019901 | protein kinase binding | - | IEA | Function |
| GO:0019908 | nuclear cyclin-dependent protein kinase holoenzyme complex | - | ISS | Component |
| GO:0030332 | cyclin binding | 21873635. | IBA | Function |
| GO:0030332 | cyclin binding | 22012619. | IPI | Function |
| GO:0032968 | positive regulation of transcription elongation from RNA polymerase II promoter | 21873635. | IBA | Process |
| GO:0043405 | regulation of MAP kinase activity | 19651820. | IMP | Process |
| GO:0043484 | regulation of RNA splicing | - | IEA | Process |
| GO:0044212 | transcription regulatory region DNA binding | 21873635. | IBA | Function |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 21873635. | IBA | Process |
| GO:0046777 | protein autophosphorylation | 11683387. | IDA | Process |
| GO:0051726 | regulation of cell cycle | - | IEA | Process |
| GO:0070816 | phosphorylation of RNA polymerase II C-terminal domain | 21873635. | IBA | Process |
| GO:0070816 | phosphorylation of RNA polymerase II C-terminal domain | 20952539. | IMP | Process |
| GO:2000737 | negative regulation of stem cell differentiation | - | IEA | Process |