
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THYM | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UVM |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| DLBC | |||
| KIRC | |||
| LGG | |||
| SARC | |||
| SKCM | |||
| TGCT | |||
| UVM |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| MESO | ||
| HNSC | ||
| LUSC | ||
| TGCT | ||
| COAD | ||
| PAAD | ||
| PCPG | ||
| CESC | ||
| LAML | ||
| GBM | ||
| LIHC | ||
| LUAD | ||
| OV |
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000323856 | S10_plectin | PF03501.15 | 7.7e-35 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000398774 | PLEC-207 | 14646 | XM_005250984 | ENSP00000381756 | 4515 (aa) | XP_005251041 | Q15149 |
| ENST00000528131 | PLEC-214 | 564 | - | ENSP00000436702 | 174 (aa) | - | E9PIA2 |
| ENST00000345136 | PLEC-202 | 14803 | XM_005250980 | ENSP00000344848 | 4547 (aa) | XP_005251037 | Q15149 |
| ENST00000436759 | PLEC-208 | 14787 | XM_006716588 | ENSP00000388180 | 4574 (aa) | XP_006716651 | Q15149 |
| ENST00000356346 | PLEC-205 | 14683 | XM_005250981 | ENSP00000348702 | 4533 (aa) | XP_005251038 | Q15149 |
| ENST00000526416 | PLEC-209 | 583 | - | ENSP00000433557 | 190 (aa) | - | E9PKG0 |
| ENST00000357649 | PLEC-206 | 14689 | XM_005250978 | ENSP00000350277 | 4551 (aa) | XP_005251035 | Q15149 |
| ENST00000527816 | PLEC-212 | 583 | - | ENSP00000434490 | 83 (aa) | - | E9PQ28 |
| ENST00000528025 | PLEC-213 | 2115 | - | ENSP00000437303 | 703 (aa) | - | E9PMV1 |
| ENST00000532346 | PLEC-215 | 316 | - | - | - (aa) | - | - |
| ENST00000354958 | PLEC-204 | 14751 | XM_005250982 | ENSP00000347044 | 4525 (aa) | XP_005251039 | Q15149 |
| ENST00000527303 | PLEC-211 | 11406 | - | ENSP00000433982 | 3447 (aa) | - | H0YDN1 |
| ENST00000322810 | PLEC-201 | 15249 | XM_005250976 | ENSP00000323856 | 4684 (aa) | XP_005251033 | Q15149 |
| ENST00000527096 | PLEC-210 | 13713 | - | ENSP00000434583 | 4570 (aa) | - | Q15149 |
| ENST00000354589 | PLEC-203 | 14736 | XM_005250979 | ENSP00000346602 | 4547 (aa) | XP_005251036 | Q15149 |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000178209 | Bronchodilator Agents | 4E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 4E-6 | 26634245 |
| ENSG00000178209 | Fibrinogen | 6E-10 | 26561523 |
| ENSG00000178209 | Cholesterol | 9E-10 | 20686565 |
| ENSG00000178209 | Bronchodilator Agents | 4E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 4E-6 | 26634245 |
| ENSG00000178209 | Fibrinogen | 1E-9 | 23969696 |
| ENSG00000178209 | Bronchodilator Agents | 3E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 3E-6 | 26634245 |
| ENSG00000178209 | Bronchodilator Agents | 3E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 3E-6 | 26634245 |
| ENSG00000178209 | Bronchodilator Agents | 5E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 5E-6 | 26634245 |
| ENSG00000178209 | Bronchodilator Agents | 5E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 5E-6 | 26634245 |
| ENSG00000178209 | Platelet Count | 5E-10 | 22139419 |
| ENSG00000178209 | Cholesterol, LDL | 7E-12 | 24097068 |
| ENSG00000178209 | Bronchodilator Agents | 1E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 1E-6 | 26634245 |
| ENSG00000178209 | Cholesterol, LDL | 4E-13 | 20686565 |
| ENSG00000178209 | Body Height | 1E-9 | 25282103 |
| ENSG00000178209 | Bronchodilator Agents | 3E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 3E-6 | 26634245 |
| ENSG00000178209 | Fibrinogen | 2E-9 | 28107422 |
| ENSG00000178209 | Cholesterol | 6E-9 | 24097068 |
| ENSG00000178209 | Bronchodilator Agents | 5E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 5E-6 | 26634245 |
| ENSG00000178209 | Bronchodilator Agents | 4E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 4E-6 | 26634245 |
| ENSG00000178209 | Bronchodilator Agents | 4E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 4E-6 | 26634245 |
| ENSG00000178209 | Bronchodilator Agents | 4E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 4E-6 | 26634245 |
| ENSG00000178209 | Bronchodilator Agents | 5E-6 | 26634245 |
| ENSG00000178209 | Forced Expiratory Volume | 5E-6 | 26634245 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000178209 | rs7464572 | 8 | 143946999 | C | Fibrinogen | 23969696 | [0.005-0.009] unit decrease | 0.007 | EFO_0004623 |
| ENSG00000178209 | rs11136341 | 8 | 143969375 | G | LDL cholesterol | 24097068 | [NR] unit increase | 0.045 | EFO_0004611 |
| ENSG00000178209 | rs11780978 | 8 | 143960684 | A | Fibrinogen levels | 26561523 | NR unit increase | 0.0059 | EFO_0004623 |
| ENSG00000178209 | rs6995402 | 8 | 143931393 | C | Platelet count | 22139419 | [1.58-3.03] 10^9/l increase | 2.304 | EFO_0004309 |
| ENSG00000178209 | rs7003580 | 8 | 143933366 | C | Anti-saccade response | 29064472 | EFO_0006874 | ||
| ENSG00000178209 | rs11780978 | 8 | 143960684 | A | Osteoarthritis of the hip (hospital diagnosed) | 29559693 | [1.0834-1.1708] | 1.1263 | EFO_1000786 |
| ENSG00000178209 | rs7833924 | 8 | 143921861 | G | Platelet count | 27863252 | [0.037-0.051] unit increase | 0.04389853 | EFO_0004309 |
| ENSG00000178209 | rs11136335 | 8 | 143929609 | G | Mosquito bite size | 28199695 | [0.015-0.036] unit decrease | 0.0259095 | EFO_0008378 |
| ENSG00000178209 | rs56117011 | 8 | 143925474 | A | Post bronchodilator FEV1 | 26634245 | NR unit decrease | 0.045 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs35916068 | 8 | 143925516 | A | Post bronchodilator FEV1 | 26634245 | NR unit decrease | 0.045 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs11778026 | 8 | 143922240 | T | Post bronchodilator FEV1 | 26634245 | NR unit decrease | 0.045 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs7155 | 8 | 143915294 | A | Post bronchodilator FEV1 | 26634245 | NR unit decrease | 0.043 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs7002002 | 8 | 143923759 | A | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.044 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs7016416 | 8 | 143923488 | T | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.044 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs1140522 | 8 | 143924001 | T | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.044 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs6984820 | 8 | 143919156 | T | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.044 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs6558407 | 8 | 143921326 | T | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.045 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs11777402 | 8 | 143921568 | A | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.045 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs11786903 | 8 | 143922430 | A | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.045 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs55646585 | 8 | 143925453 | T | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.045 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs1065837 | 8 | 143916167 | A | Post bronchodilator FEV1 | 26634245 | NR unit increase | 0.047 | EFO_0004314|GO_0097366 |
| ENSG00000178209 | rs11136341 | 8 | 143969375 | G | LDL cholesterol | 20686565 | [0.99-1.81] mg/dL increase | 1.4 | EFO_0004611 |
| ENSG00000178209 | rs7464572 | 8 | 143946999 | ? | Fibrinogen levels | 28107422 | unit increase | 0.0066 | EFO_0004623 |
| ENSG00000178209 | rs11783655 | 8 | 143963405 | A | Height | 25282103 | [0.012-0.024] unit decrease | 0.018 | EFO_0004339 |
| ENSG00000178209 | rs7832643 | 8 | 143948489 | T | LDL cholesterol levels | 28334899 | [0.026-0.041] unit increase (EA Beta value) | 0.0339 | EFO_0004611 |
| ENSG00000178209 | rs7832643 | 8 | 143948489 | T | Total cholesterol levels | 28334899 | [0.022-0.036] unit increase (EA Beta values) | 0.0289 | EFO_0004574 |
| ENSG00000178209 | rs11783655 | 8 | 143963405 | T | Low density lipoprotein cholesterol levels | 29507422 | unit decrease | 0.027 | EFO_0004611 |
| ENSG00000178209 | rs11136341 | 8 | 143969375 | A | Low density lipoprotein cholesterol levels | 29507422 | unit decrease | 0.03 | EFO_0004611 |
| ENSG00000178209 | rs11136341 | 8 | 143969375 | A | Low density lipoprotein cholesterol levels | 29507422 | unit decrease | 0.03 | EFO_0004611 |
| ENSG00000178209 | rs11136341 | 8 | 143969375 | A | Total cholesterol levels | 29507422 | unit decrease | 0.027 | EFO_0004574 |
| ENSG00000178209 | rs11136341 | 8 | 143969375 | A | Total cholesterol levels | 29507422 | unit decrease | 0.026 | EFO_0004574 |
| ENSG00000178209 | rs11780978 | 8 | 143960684 | A | Osteoarthritis (hip) | 30374069 | [NR] | 1.05646 | EFO_1000786 |
| ENSG00000178209 | rs73715570 | 8 | 143951130 | ? | Systolic blood pressure | 30595370 | EFO_0006335 | ||
| ENSG00000178209 | rs7819099 | 8 | 143918694 | ? | Red blood cell count | 30595370 | EFO_0004305 | ||
| ENSG00000178209 | rs11136336 | 8 | 143933019 | ? | Fat-free mass | 30593698 | [0.075-0.164] unit decrease | 0.11946 | EFO_0004995 |
| ENSG00000178209 | rs11136336 | 8 | 143933019 | ? | Fat-free mass | 30593698 | [0.073-0.169] unit decrease | 0.12116 | EFO_0004995 |
| ENSG00000178209 | rs117961539 | 8 | 143915298 | ? | Eosinophil counts | 30595370 | EFO_0004842 |
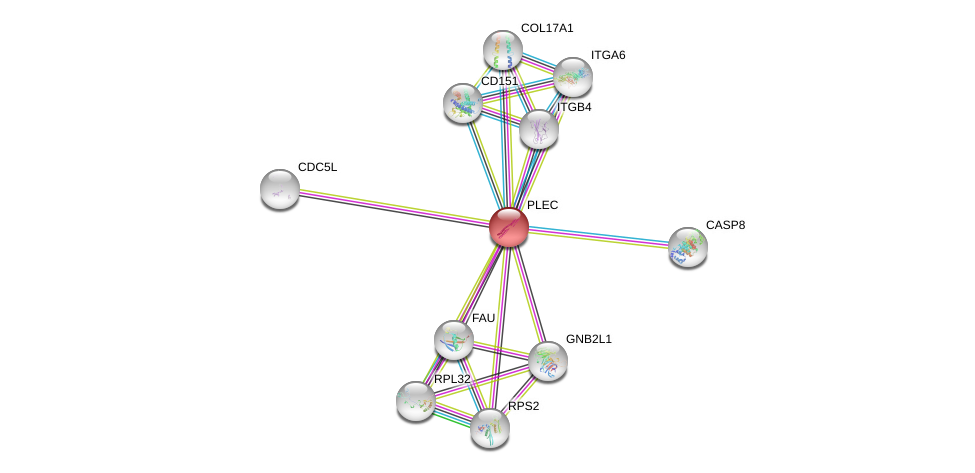
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSAMEG00000006191 | PLEC | 100 | 90.669 | Ailuropoda_melanoleuca |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSANAG00000032431 | PLEC | 100 | 96.714 | Aotus_nancymaae |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSBTAG00000011922 | PLEC | 100 | 92.493 | Bos_taurus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCJAG00000021472 | PLEC | 100 | 96.991 | Callithrix_jacchus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCAFG00000001433 | PLEC | 100 | 92.501 | Canis_familiaris |
| ENSG00000178209 | PLEC | 88 | 92.675 | ENSCHIG00000022260 | PLEC | 99 | 92.675 | Capra_hircus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSTSYG00000033419 | PLEC | 100 | 94.903 | Carlito_syrichta |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCAPG00000013570 | PLEC | 100 | 90.947 | Cavia_aperea |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCPOG00000007957 | PLEC | 100 | 93.389 | Cavia_porcellus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCCAG00000031237 | PLEC | 100 | 97.204 | Cebus_capucinus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCATG00000009349 | PLEC | 100 | 98.527 | Cercocebus_atys |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCLAG00000012830 | PLEC | 100 | 93.730 | Chinchilla_lanigera |
| ENSG00000178209 | PLEC | 100 | 98.795 | ENSCPBG00000021974 | PLEC | 99 | 72.814 | Chrysemys_picta_bellii |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCGRG00001019864 | Plec | 100 | 93.546 | Cricetulus_griseus_chok1gshd |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSCGRG00000002714 | Plec | 100 | 92.903 | Cricetulus_griseus_crigri |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSDNOG00000031742 | PLEC | 99 | 89.268 | Dasypus_novemcinctus |
| ENSG00000178209 | PLEC | 84 | 94.253 | ENSETEG00000015535 | - | 62 | 91.826 | Echinops_telfairi |
| ENSG00000178209 | PLEC | 78 | 100.000 | ENSEEUG00000004554 | - | 67 | 97.095 | Erinaceus_europaeus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSFCAG00000042897 | PLEC | 100 | 92.856 | Felis_catus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSFDAG00000011856 | PLEC | 100 | 93.261 | Fukomys_damarensis |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSGGOG00000012217 | PLEC | 100 | 97.213 | Gorilla_gorilla |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSHGLG00000012646 | PLEC | 100 | 93.154 | Heterocephalus_glaber_female |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSHGLG00100011759 | PLEC | 100 | 82.572 | Heterocephalus_glaber_male |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSSTOG00000023061 | PLEC | 100 | 92.603 | Ictidomys_tridecemlineatus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSJJAG00000012390 | Plec | 100 | 93.372 | Jaculus_jaculus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMFAG00000032066 | PLEC | 100 | 98.527 | Macaca_fascicularis |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMMUG00000000388 | PLEC | 100 | 95.014 | Macaca_mulatta |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMNEG00000011406 | PLEC | 100 | 98.484 | Macaca_nemestrina |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMLEG00000033296 | PLEC | 100 | 97.916 | Mandrillus_leucophaeus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMAUG00000001116 | Plec | 100 | 93.525 | Mesocricetus_auratus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMICG00000016160 | PLEC | 100 | 94.307 | Microcebus_murinus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMOCG00000000674 | Plec | 100 | 93.582 | Microtus_ochrogaster |
| ENSG00000178209 | PLEC | 100 | 100.000 | MGP_CAROLIEiJ_G0019913 | Plec | 100 | 93.561 | Mus_caroli |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMUSG00000022565 | Plec | 100 | 93.518 | Mus_musculus |
| ENSG00000178209 | PLEC | 100 | 100.000 | MGP_PahariEiJ_G0019923 | Plec | 100 | 93.412 | Mus_pahari |
| ENSG00000178209 | PLEC | 100 | 100.000 | MGP_SPRETEiJ_G0020816 | Plec | 100 | 93.539 | Mus_spretus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMPUG00000007329 | PLEC | 100 | 90.808 | Mustela_putorius_furo |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSNGAG00000008931 | Plec | 100 | 93.710 | Nannospalax_galili |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSMEUG00000004499 | - | 70 | 92.743 | Notamacropus_eugenii |
| ENSG00000178209 | PLEC | 100 | 98.795 | ENSOPRG00000015206 | PLEC | 69 | 92.237 | Ochotona_princeps |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSODEG00000014671 | PLEC | 100 | 93.375 | Octodon_degus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSOCUG00000023075 | - | 100 | 92.241 | Oryctolagus_cuniculus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSOARG00000015846 | - | 100 | 80.114 | Ovis_aries |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSPPAG00000042112 | PLEC | 100 | 91.084 | Pan_paniscus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSPTRG00000020672 | PLEC | 100 | 99.210 | Pan_troglodytes |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSPANG00000023403 | - | 100 | 98.228 | Papio_anubis |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSPEMG00000011922 | Plec | 100 | 93.826 | Peromyscus_maniculatus_bairdii |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSPCIG00000014981 | PLEC | 100 | 82.485 | Phascolarctos_cinereus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSPCOG00000023279 | PLEC | 100 | 94.476 | Propithecus_coquereli |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSPVAG00000009376 | PLEC | 91 | 93.131 | Pteropus_vampyrus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSRNOG00000023781 | Plec | 100 | 93.605 | Rattus_norvegicus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSRBIG00000041068 | PLEC | 75 | 95.337 | Rhinopithecus_bieti |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSRROG00000015881 | PLEC | 100 | 98.249 | Rhinopithecus_roxellana |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSSBOG00000025259 | PLEC | 100 | 94.556 | Saimiri_boliviensis_boliviensis |
| ENSG00000178209 | PLEC | 99 | 98.780 | ENSSHAG00000009020 | PLEC | 99 | 78.770 | Sarcophilus_harrisii |
| ENSG00000178209 | PLEC | 100 | 95.181 | ENSTTRG00000010427 | PLEC | 95 | 91.172 | Tursiops_truncatus |
| ENSG00000178209 | PLEC | 100 | 100.000 | ENSVVUG00000010214 | PLEC | 100 | 92.288 | Vulpes_vulpes |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0003723 | RNA binding | 22658674. | HDA | Function |
| GO:0003779 | actin binding | - | IEA | Function |
| GO:0005198 | structural molecule activity | 21873635. | IBA | Function |
| GO:0005200 | structural constituent of cytoskeleton | 21873635. | IBA | Function |
| GO:0005515 | protein binding | 12482924.18827015.19242489.19932097.22240165. | IPI | Function |
| GO:0005737 | cytoplasm | 21873635. | IBA | Component |
| GO:0005829 | cytosol | - | IDA | Component |
| GO:0005829 | cytosol | - | TAS | Component |
| GO:0005882 | intermediate filament | 21873635. | IBA | Component |
| GO:0005886 | plasma membrane | 8633055. | NAS | Component |
| GO:0005903 | brush border | - | IEA | Component |
| GO:0005925 | focal adhesion | 21423176. | HDA | Component |
| GO:0005925 | focal adhesion | 21873635. | IBA | Component |
| GO:0005925 | focal adhesion | - | IDA | Component |
| GO:0008307 | structural constituent of muscle | 21873635. | IBA | Function |
| GO:0016020 | membrane | 21873635. | IBA | Component |
| GO:0016528 | sarcoplasm | 21223964. | ISS | Component |
| GO:0030056 | hemidesmosome | 21873635. | IBA | Component |
| GO:0030056 | hemidesmosome | 12482924. | IDA | Component |
| GO:0030506 | ankyrin binding | 21873635. | IBA | Function |
| GO:0030506 | ankyrin binding | 21223964. | IPI | Function |
| GO:0031581 | hemidesmosome assembly | 21873635. | IBA | Process |
| GO:0031581 | hemidesmosome assembly | 12482924. | IDA | Process |
| GO:0031581 | hemidesmosome assembly | - | TAS | Process |
| GO:0042060 | wound healing | 21873635. | IBA | Process |
| GO:0042383 | sarcolemma | 21873635. | IBA | Component |
| GO:0042383 | sarcolemma | 21109228. | IDA | Component |
| GO:0043034 | costamere | 21223964. | TAS | Component |
| GO:0045104 | intermediate filament cytoskeleton organization | 21873635. | IBA | Process |
| GO:0045111 | intermediate filament cytoskeleton | - | IDA | Component |
| GO:0045296 | cadherin binding | 25468996. | HDA | Function |
| GO:0048471 | perinuclear region of cytoplasm | 21873635. | IBA | Component |
| GO:0070062 | extracellular exosome | 19199708. | HDA | Component |