
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000548318 | PPP1R12A-209 | 582 | - | ENSP00000449843 | 97 (aa) | - | F8VW28 |
| ENST00000261207 | PPP1R12A-201 | 5582 | - | ENSP00000261207 | 1030 (aa) | - | O14974 |
| ENST00000650220 | PPP1R12A-223 | 1143 | - | ENSP00000497229 | 381 (aa) | - | - |
| ENST00000551781 | PPP1R12A-219 | 629 | - | - | - (aa) | - | - |
| ENST00000547131 | PPP1R12A-206 | 897 | - | ENSP00000450061 | 299 (aa) | - | H0YIS4 |
| ENST00000546369 | PPP1R12A-204 | 2977 | - | ENSP00000449514 | 943 (aa) | - | O14974 |
| ENST00000550351 | PPP1R12A-215 | 738 | - | - | - (aa) | - | - |
| ENST00000550510 | PPP1R12A-216 | 631 | - | ENSP00000447338 | 210 (aa) | - | H0YHL8 |
| ENST00000550001 | PPP1R12A-211 | 631 | - | - | - (aa) | - | - |
| ENST00000548908 | PPP1R12A-210 | 3064 | - | - | - (aa) | - | - |
| ENST00000551191 | PPP1R12A-218 | 602 | - | - | - (aa) | - | - |
| ENST00000550007 | PPP1R12A-212 | 443 | - | - | - (aa) | - | - |
| ENST00000437004 | PPP1R12A-202 | 4639 | XM_017019330 | ENSP00000416769 | 995 (aa) | XP_016874819 | O14974 |
| ENST00000546762 | PPP1R12A-205 | 1257 | - | ENSP00000450059 | 234 (aa) | - | H0YIS3 |
| ENST00000550903 | PPP1R12A-217 | 959 | - | ENSP00000449647 | 161 (aa) | - | H0YIL7 |
| ENST00000553081 | PPP1R12A-221 | 1101 | - | ENSP00000447144 | 367 (aa) | - | H0YHI8 |
| ENST00000450142 | PPP1R12A-203 | 5721 | XM_005268887 | ENSP00000389168 | 1030 (aa) | XP_005268944 | O14974 |
| ENST00000550107 | PPP1R12A-213 | 2925 | XM_011538379 | ENSP00000446855 | 974 (aa) | XP_011536681 | O14974 |
| ENST00000634739 | PPP1R12A-222 | 560 | - | ENSP00000489242 | 100 (aa) | - | A0A0U1RQZ1 |
| ENST00000547330 | PPP1R12A-208 | 2275 | - | ENSP00000446816 | 692 (aa) | - | F8VZN8 |
| ENST00000547253 | PPP1R12A-207 | 676 | - | - | - (aa) | - | - |
| ENST00000550299 | PPP1R12A-214 | 683 | - | ENSP00000449666 | 188 (aa) | - | H0YIM2 |
| ENST00000552892 | PPP1R12A-220 | 2277 | - | - | - (aa) | - | - |
| Pathway ID | Pathway Name | Source |
|---|---|---|
| hsa04022 | cGMP-PKG signaling pathway | KEGG |
| hsa04024 | cAMP signaling pathway | KEGG |
| hsa04270 | Vascular smooth muscle contraction | KEGG |
| hsa04510 | Focal adhesion | KEGG |
| hsa04611 | Platelet activation | KEGG |
| hsa04810 | Regulation of actin cytoskeleton | KEGG |
| hsa04921 | Oxytocin signaling pathway | KEGG |
| hsa05205 | Proteoglycans in cancer | KEGG |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000058272 | rs113146373 | 12 | 79784781 | ? | Velopharyngeal dysfunction | 29855589 | [NR] unit decrease | 0.1339413 | EFO_0009336 |
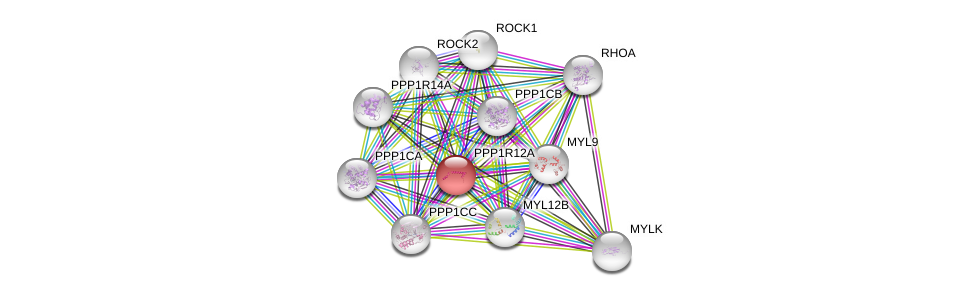
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000058272 | PPP1R12A | 100 | 98.148 | ENSMUSG00000019907 | Ppp1r12a | 100 | 92.435 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000086 | G2/M transition of mitotic cell cycle | - | TAS | Process |
| GO:0000278 | mitotic cell cycle | 18477460. | IMP | Process |
| GO:0000776 | kinetochore | 18477460. | IDA | Component |
| GO:0004857 | enzyme inhibitor activity | 21873635. | IBA | Function |
| GO:0004857 | enzyme inhibitor activity | 19245366. | IDA | Function |
| GO:0005515 | protein binding | 11067852.15292222.16417406.18073109.20195357.25609649. | IPI | Function |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0005737 | cytoplasm | 21873635. | IBA | Component |
| GO:0005813 | centrosome | 18477460. | IDA | Component |
| GO:0005829 | cytosol | - | IDA | Component |
| GO:0005829 | cytosol | - | TAS | Component |
| GO:0005925 | focal adhesion | 21423176. | HDA | Component |
| GO:0006470 | protein dephosphorylation | 18477460. | IMP | Process |
| GO:0007098 | centrosome cycle | 18477460. | IMP | Process |
| GO:0007165 | signal transduction | - | IEA | Process |
| GO:0015629 | actin cytoskeleton | - | IDA | Component |
| GO:0019208 | phosphatase regulator activity | 21873635. | IBA | Function |
| GO:0019208 | phosphatase regulator activity | 20354225. | IDA | Function |
| GO:0019208 | phosphatase regulator activity | 18477460. | IMP | Function |
| GO:0019901 | protein kinase binding | 18477460. | IPI | Function |
| GO:0030018 | Z disc | 21873635. | IBA | Component |
| GO:0030018 | Z disc | - | ISS | Component |
| GO:0030155 | regulation of cell adhesion | 20354225. | IDA | Process |
| GO:0031672 | A band | 21873635. | IBA | Component |
| GO:0031672 | A band | - | ISS | Component |
| GO:0035507 | regulation of myosin-light-chain-phosphatase activity | 20354225. | IDA | Process |
| GO:0035508 | positive regulation of myosin-light-chain-phosphatase activity | 21873635. | IBA | Process |
| GO:0035508 | positive regulation of myosin-light-chain-phosphatase activity | 25816133. | IMP | Process |
| GO:0035690 | cellular response to drug | - | IEA | Process |
| GO:0043086 | negative regulation of catalytic activity | 19245366. | IDA | Process |
| GO:0043292 | contractile fiber | 20634291. | IDA | Component |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 19245366. | IDA | Process |
| GO:0046822 | regulation of nucleocytoplasmic transport | - | IEA | Process |
| GO:0071889 | 14-3-3 protein binding | 20354225. | IDA | Function |
| GO:0072357 | PTW/PP1 phosphatase complex | 20354225. | IDA | Component |
| GO:1903140 | regulation of establishment of endothelial barrier | 25816133. | IMP | Process |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| ACC | |||
| ESCA | |||
| HNSC | |||
| LUAD | |||
| PAAD | |||
| PRAD | |||
| READ | |||
| SKCM |
| Cancer | P-value | Q-value |
|---|---|---|
| THYM | ||
| KIRC | ||
| STAD | ||
| SKCM | ||
| KIRP | ||
| PCPG | ||
| KICH | ||
| GBM | ||
| LIHC | ||
| LGG |