
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000262975 | ZMYND8-201 | 4139 | XM_017027775 | ENSP00000262975 | 1168 (aa) | XP_016883264 | Q9ULU4 |
| ENST00000352431 | ZMYND8-203 | 3832 | XM_017027760 | ENSP00000335537 | 1160 (aa) | XP_016883249 | Q9ULU4 |
| ENST00000396281 | ZMYND8-207 | 5511 | XM_011528749 | ENSP00000379577 | 1186 (aa) | XP_011527051 | Q9ULU4 |
| ENST00000441977 | ZMYND8-209 | 175 | - | ENSP00000393806 | 24 (aa) | - | Q5TH07 |
| ENST00000540497 | ZMYND8-218 | 3405 | - | ENSP00000443086 | 1134 (aa) | - | Q9ULU4 |
| ENST00000446894 | ZMYND8-210 | 341 | - | ENSP00000394379 | 42 (aa) | - | Q5TH08 |
| ENST00000360911 | ZMYND8-205 | 4991 | XM_017027765 | ENSP00000354166 | 1135 (aa) | XP_016883254 | Q9ULU4 |
| ENST00000435836 | ZMYND8-208 | 670 | - | ENSP00000413727 | 175 (aa) | - | Q5TH12 |
| ENST00000355972 | ZMYND8-204 | 5542 | XM_011528753 | ENSP00000348246 | 1214 (aa) | XP_011527055 | Q9ULU4 |
| ENST00000611941 | ZMYND8-219 | 5090 | XM_017027779 | ENSP00000482048 | 1087 (aa) | XP_016883268 | A0A087WYS3 |
| ENST00000471951 | ZMYND8-216 | 4053 | XM_005260362 | ENSP00000420095 | 1234 (aa) | XP_005260419 | Q9ULU4 |
| ENST00000311275 | ZMYND8-202 | 5362 | XM_005260366 | ENSP00000312237 | 1186 (aa) | XP_005260423 | Q9ULU4 |
| ENST00000458360 | ZMYND8-212 | 3729 | XM_017027780 | ENSP00000392964 | 1054 (aa) | XP_016883269 | Q9ULU4 |
| ENST00000372023 | ZMYND8-206 | 5144 | - | ENSP00000361093 | 1105 (aa) | - | Q9ULU4 |
| ENST00000461685 | ZMYND8-213 | 3567 | - | ENSP00000418210 | 1188 (aa) | - | Q9ULU4 |
| ENST00000468376 | ZMYND8-215 | 4064 | - | - | - (aa) | - | - |
| ENST00000536340 | ZMYND8-217 | 5273 | XM_005260356 | ENSP00000439800 | 1241 (aa) | XP_005260413 | Q9ULU4 |
| ENST00000617418 | ZMYND8-220 | 3411 | - | ENSP00000479806 | 1136 (aa) | - | A0A087WVZ6 |
| ENST00000467200 | ZMYND8-214 | 3634 | XM_017027774 | ENSP00000418495 | 1095 (aa) | XP_016883263 | H7C4X9 |
| ENST00000619049 | ZMYND8-221 | 4027 | - | ENSP00000479197 | 767 (aa) | - | A0A087WV57 |
| ENST00000446994 | ZMYND8-211 | 5471 | XM_005260358 | ENSP00000396725 | 1214 (aa) | XP_005260415 | Q9ULU4 |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000101040 | Asthma | 9.434312E-06 | 11022011 |
| ENSG00000101040 | Coronary Disease | 1.2510000E-005 | - |
| ENSG00000101040 | Platelet Function Tests | 4.3000000E-007 | - |
| ENSG00000101040 | Platelet Function Tests | 4.2900000E-006 | - |
| ENSG00000101040 | Platelet Function Tests | 1.6007200E-005 | - |
| ENSG00000101040 | Platelet Function Tests | 1.7432400E-005 | - |
| ENSG00000101040 | Child Development Disorders, Pervasive | 4.0000000E-005 | - |
| ENSG00000101040 | Osteoarthritis | 2E-10 | 23989986 |
| ENSG00000101040 | Migraine Disorders | 4E-8 | 27182965 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000101040 | rs17726337 | 20 | 47315915 | C | Mean platelet volume | 27863252 | [0.069-0.107] unit decrease | 0.08812654 | EFO_0004584 |
| ENSG00000101040 | rs6063085 | 20 | 47211814 | A | Depressive symptoms (MTAG) | 29292387 | [0.0085-0.0171] unit increase | 0.0128 | EFO_0007006 |
| ENSG00000101040 | rs6063085 | 20 | 47211814 | A | Subjective well-being (MTAG) | 29292387 | [0.0088-0.0162] unit decrease | 0.0125 | EFO_0007869 |
| ENSG00000101040 | rs910187 | 20 | 47212407 | ? | Migraine | 27182965 | [1.029-1.061] | 1.045 | EFO_0003821 |
| ENSG00000101040 | rs57808107 | 20 | 47232164 | ? | Plasma factor VII activating protease levels | 30070759 | [60.14-142.86] unit increase | 101.5 | EFO_0009368 |
| ENSG00000101040 | rs910187 | 20 | 47212407 | A | Neuroticism | 30643256 | [0.0067-0.0128] unit decrease | 0.009757282 | EFO_0007660 |
| ENSG00000101040 | rs910187 | 20 | 47212407 | A | Depressive symptoms | 30643256 | [0.0043-0.0082] unit decrease | 0.006215197 | EFO_0007006 |
| ENSG00000101040 | rs910187 | 20 | 47212407 | ? | Neuroticism | 30595370 | EFO_0007660 | ||
| ENSG00000101040 | rs910187 | 20 | 47212407 | A | Well-being spectrum (multivariate analysis) | 30643256 | [0.0045-0.0082] unit decrease | 0.006336388 | EFO_0007869 |
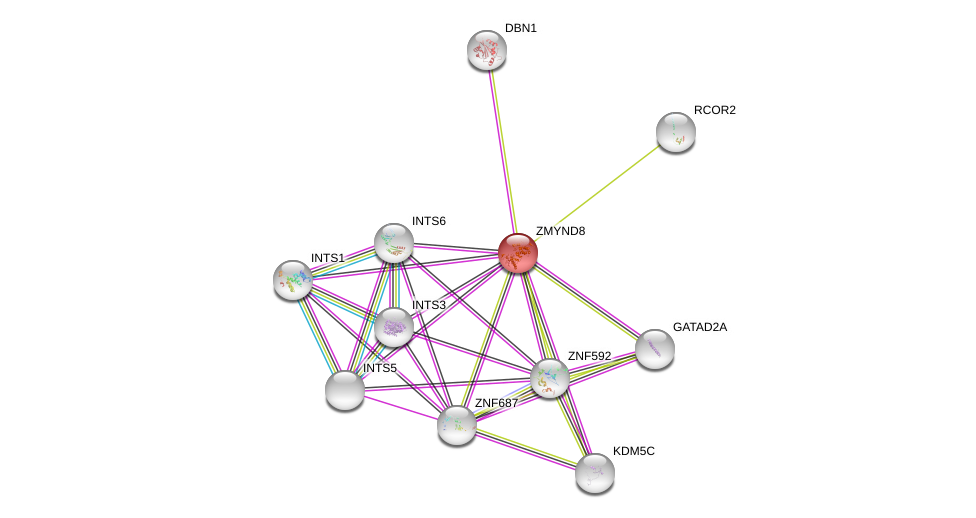
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000101040 | ZMYND8 | 100 | 96.000 | ENSMUSG00000039671 | Zmynd8 | 99 | 92.569 | Mus_musculus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0003714 | transcription corepressor activity | 27477906. | IMP | Function |
| GO:0003714 | transcription corepressor activity | - | ISS | Function |
| GO:0005515 | protein binding | 15095401.16147992.28966017. | IPI | Function |
| GO:0005634 | nucleus | 27477906.28966017. | IDA | Component |
| GO:0005634 | nucleus | - | ISS | Component |
| GO:0005737 | cytoplasm | 28966017. | IMP | Component |
| GO:0006355 | regulation of transcription, DNA-templated | - | IEA | Process |
| GO:0008270 | zinc ion binding | 28966017. | IDA | Function |
| GO:0019904 | protein domain specific binding | 28966017. | IDA | Function |
| GO:0030336 | negative regulation of cell migration | 27477906. | IMP | Process |
| GO:0035064 | methylated histone binding | 27477906. | IDA | Function |
| GO:0043197 | dendritic spine | - | IEA | Component |
| GO:0043198 | dendritic shaft | - | IEA | Component |
| GO:0047485 | protein N-terminus binding | - | IEA | Function |
| GO:0051491 | positive regulation of filopodium assembly | - | IEA | Process |
| GO:0060999 | positive regulation of dendritic spine development | - | IEA | Process |
| GO:0070491 | repressing transcription factor binding | - | ISS | Function |
| GO:0070577 | lysine-acetylated histone binding | 27477906. | IDA | Function |
| GO:0098815 | modulation of excitatory postsynaptic potential | - | IEA | Process |
| GO:1902897 | regulation of postsynaptic density protein 95 clustering | - | IEA | Process |
| GO:1902952 | positive regulation of dendritic spine maintenance | - | IEA | Process |
| GO:1903507 | negative regulation of nucleic acid-templated transcription | - | IEA | Process |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| LAML | |||||||
| LAML | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PCPG | |||||||
| PCPG | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| TGCT | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| LAML | |||
| LUAD | |||
| PRAD | |||
| UCEC |
| Cancer | P-value | Q-value |
|---|---|---|
| THYM | ||
| KIRC | ||
| MESO | ||
| ACC | ||
| UCS | ||
| BRCA | ||
| ESCA | ||
| BLCA | ||
| LIHC | ||
| DLBC | ||
| LGG | ||
| UVM |