
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000358478 | ResIII | PF04851.15 | 1.2e-09 | 1 | 1 |
| PID | Title | Method | Time | Author | Doi |
|---|---|---|---|---|---|
| 30528433 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000469638 | TTF2-204 | 775 | - | - | - (aa) | - | - |
| ENST00000480701 | TTF2-206 | 983 | - | - | - (aa) | - | - |
| ENST00000492682 | TTF2-207 | 803 | - | - | - (aa) | - | - |
| ENST00000427271 | TTF2-202 | 639 | - | ENSP00000408111 | 143 (aa) | - | X6RI15 |
| ENST00000369466 | TTF2-201 | 9462 | XM_005271277 | ENSP00000358478 | 1162 (aa) | XP_005271334 | Q9UNY4 |
| ENST00000470935 | TTF2-205 | 849 | - | - | - (aa) | - | - |
| ENST00000463696 | TTF2-203 | 662 | - | - | - (aa) | - | - |
| Pathway ID | Pathway Name | Source |
|---|---|---|
| hsa04918 | Thyroid hormone synthesis | KEGG |
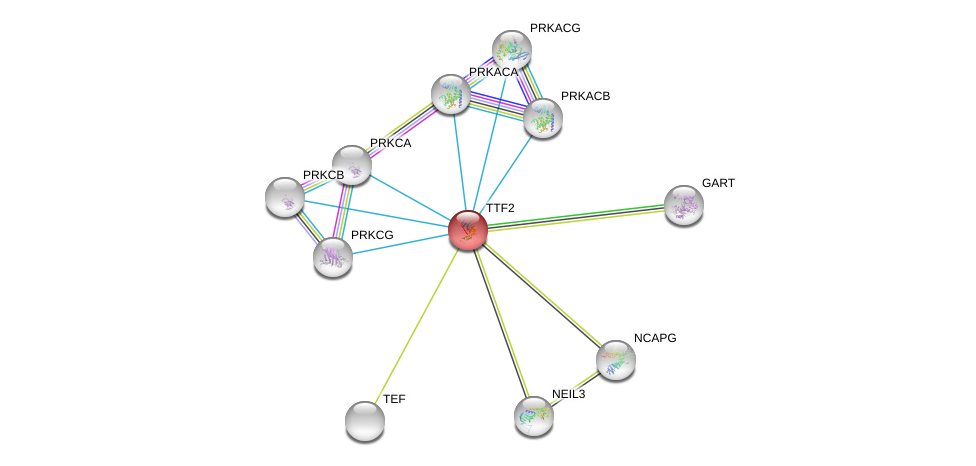
| Ensembl ID | Gene Symbol | Coverage | Identiy | Paralog | Gene Symbol | Coverage | Identiy |
|---|---|---|---|---|---|---|---|
| ENSG00000116830 | TTF2 | 85 | 35.246 | ENSG00000173575 | CHD2 | 85 | 38.542 |
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000116830 | TTF2 | 100 | 80.556 | ENSAPLG00000010324 | - | 100 | 53.742 | Anas_platyrhynchos |
| ENSG00000116830 | TTF2 | 100 | 99.301 | ENSANAG00000020654 | TTF2 | 100 | 91.316 | Aotus_nancymaae |
| ENSG00000116830 | TTF2 | 100 | 90.909 | ENSBTAG00000015392 | TTF2 | 100 | 76.778 | Bos_taurus |
| ENSG00000116830 | TTF2 | 100 | 91.608 | ENSCHIG00000020785 | TTF2 | 98 | 75.571 | Capra_hircus |
| ENSG00000116830 | TTF2 | 100 | 99.301 | ENSCCAG00000032675 | TTF2 | 100 | 91.144 | Cebus_capucinus |
| ENSG00000116830 | TTF2 | 71 | 65.686 | ENSCSAVG00000002857 | - | 100 | 37.453 | Ciona_savignyi |
| ENSG00000116830 | TTF2 | 100 | 100.000 | ENSCANG00000032079 | TTF2 | 100 | 95.790 | Colobus_angolensis_palliatus |
| ENSG00000116830 | TTF2 | 100 | 77.622 | ENSDORG00000013781 | Ttf2 | 100 | 64.333 | Dipodomys_ordii |
| ENSG00000116830 | TTF2 | 100 | 52.083 | FBgn0002542 | lds | 77 | 37.382 | Drosophila_melanogaster |
| ENSG00000116830 | TTF2 | 100 | 94.406 | ENSECAG00000012474 | TTF2 | 100 | 83.616 | Equus_caballus |
| ENSG00000116830 | TTF2 | 100 | 88.811 | ENSFCAG00000001981 | TTF2 | 100 | 72.161 | Felis_catus |
| ENSG00000116830 | TTF2 | 85 | 48.378 | ENSGALG00000015249 | - | 99 | 47.256 | Gallus_gallus |
| ENSG00000116830 | TTF2 | 100 | 72.222 | ENSGAFG00000004358 | TTF2 | 99 | 47.049 | Gambusia_affinis |
| ENSG00000116830 | TTF2 | 100 | 99.301 | ENSGGOG00000015790 | TTF2 | 100 | 98.623 | Gorilla_gorilla |
| ENSG00000116830 | TTF2 | 100 | 92.308 | ENSJJAG00000015225 | Ttf2 | 100 | 72.151 | Jaculus_jaculus |
| ENSG00000116830 | TTF2 | 100 | 93.299 | ENSMNEG00000042285 | TTF2 | 100 | 93.299 | Macaca_nemestrina |
| ENSG00000116830 | TTF2 | 100 | 100.000 | ENSMLEG00000041549 | TTF2 | 100 | 95.533 | Mandrillus_leucophaeus |
| ENSG00000116830 | TTF2 | 100 | 79.861 | ENSMGAG00000014354 | TTF2 | 100 | 53.529 | Meleagris_gallopavo |
| ENSG00000116830 | TTF2 | 100 | 93.007 | ENSMOCG00000008415 | Ttf2 | 99 | 69.257 | Microtus_ochrogaster |
| ENSG00000116830 | TTF2 | 99 | 85.315 | ENSMODG00000005145 | TTF2 | 98 | 62.066 | Monodelphis_domestica |
| ENSG00000116830 | TTF2 | 100 | 72.222 | ENSMALG00000017262 | TTF2 | 98 | 54.796 | Monopterus_albus |
| ENSG00000116830 | TTF2 | 100 | 92.308 | MGP_CAROLIEiJ_G0025427 | Ttf2 | 100 | 70.377 | Mus_caroli |
| ENSG00000116830 | TTF2 | 100 | 92.308 | ENSMUSG00000033222 | Ttf2 | 100 | 70.240 | Mus_musculus |
| ENSG00000116830 | TTF2 | 100 | 93.706 | MGP_PahariEiJ_G0026871 | Ttf2 | 100 | 69.710 | Mus_pahari |
| ENSG00000116830 | TTF2 | 100 | 91.608 | MGP_SPRETEiJ_G0026377 | Ttf2 | 100 | 70.497 | Mus_spretus |
| ENSG00000116830 | TTF2 | 100 | 93.706 | ENSMLUG00000013908 | TTF2 | 100 | 79.299 | Myotis_lucifugus |
| ENSG00000116830 | TTF2 | 100 | 95.105 | ENSNGAG00000018882 | Ttf2 | 100 | 75.578 | Nannospalax_galili |
| ENSG00000116830 | TTF2 | 67 | 76.289 | ENSNBRG00000011914 | TTF2 | 86 | 55.128 | Neolamprologus_brichardi |
| ENSG00000116830 | TTF2 | 100 | 100.000 | ENSNLEG00000005209 | TTF2 | 100 | 96.644 | Nomascus_leucogenys |
| ENSG00000116830 | TTF2 | 100 | 95.804 | ENSOCUG00000000613 | TTF2 | 100 | 76.455 | Oryctolagus_cuniculus |
| ENSG00000116830 | TTF2 | 100 | 90.909 | ENSOGAG00000009039 | TTF2 | 100 | 78.186 | Otolemur_garnettii |
| ENSG00000116830 | TTF2 | 100 | 91.608 | ENSOARG00000020266 | TTF2 | 100 | 75.533 | Ovis_aries |
| ENSG00000116830 | TTF2 | 100 | 100.000 | ENSPPAG00000027542 | TTF2 | 100 | 99.225 | Pan_paniscus |
| ENSG00000116830 | TTF2 | 100 | 99.301 | ENSPTRG00000001162 | TTF2 | 100 | 99.139 | Pan_troglodytes |
| ENSG00000116830 | TTF2 | 100 | 79.167 | ENSPSIG00000005266 | TTF2 | 99 | 65.272 | Pelodiscus_sinensis |
| ENSG00000116830 | TTF2 | 85 | 58.644 | ENSPCIG00000003483 | TTF2 | 90 | 58.153 | Phascolarctos_cinereus |
| ENSG00000116830 | TTF2 | 100 | 95.009 | ENSPPYG00000000976 | TTF2 | 100 | 95.009 | Pongo_abelii |
| ENSG00000116830 | TTF2 | 100 | 93.706 | ENSPCOG00000000551 | TTF2 | 100 | 84.147 | Propithecus_coquereli |
| ENSG00000116830 | TTF2 | 100 | 95.105 | ENSPVAG00000014881 | TTF2 | 100 | 77.015 | Pteropus_vampyrus |
| ENSG00000116830 | TTF2 | 100 | 100.000 | ENSRBIG00000042651 | TTF2 | 100 | 94.872 | Rhinopithecus_bieti |
| ENSG00000116830 | TTF2 | 100 | 100.000 | ENSRROG00000013287 | TTF2 | 100 | 95.615 | Rhinopithecus_roxellana |
| ENSG00000116830 | TTF2 | 100 | 99.301 | ENSSBOG00000022555 | TTF2 | 100 | 89.252 | Saimiri_boliviensis_boliviensis |
| ENSG00000116830 | TTF2 | 100 | 81.944 | ENSSHAG00000018195 | TTF2 | 100 | 60.928 | Sarcophilus_harrisii |
| ENSG00000116830 | TTF2 | 100 | 74.306 | ENSSMAG00000007532 | TTF2 | 72 | 58.263 | Scophthalmus_maximus |
| ENSG00000116830 | TTF2 | 100 | 72.917 | ENSSDUG00000013617 | TTF2 | 99 | 47.720 | Seriola_dumerili |
| ENSG00000116830 | TTF2 | 100 | 92.308 | ENSSARG00000007562 | TTF2 | 100 | 64.175 | Sorex_araneus |
| ENSG00000116830 | TTF2 | 100 | 91.608 | ENSSSCG00000006733 | TTF2 | 100 | 75.257 | Sus_scrofa |
| ENSG00000116830 | TTF2 | 61 | 52.782 | ENSTRUG00000015592 | - | 66 | 52.782 | Takifugu_rubripes |
| ENSG00000116830 | TTF2 | 100 | 72.603 | ENSTNIG00000015679 | - | 85 | 55.726 | Tetraodon_nigroviridis |
| ENSG00000116830 | TTF2 | 100 | 74.825 | ENSTTRG00000012884 | TTF2 | 100 | 74.379 | Tursiops_truncatus |
| ENSG00000116830 | TTF2 | 91 | 69.418 | ENSVPAG00000008276 | TTF2 | 97 | 69.418 | Vicugna_pacos |
| ENSG00000116830 | TTF2 | 74 | 45.791 | ENSXETG00000022003 | - | 100 | 45.791 | Xenopus_tropicalis |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0003677 | DNA binding | - | IEA | Function |
| GO:0004386 | helicase activity | - | IEA | Function |
| GO:0005515 | protein binding | 12927788.17577209. | IPI | Function |
| GO:0005524 | ATP binding | - | IEA | Function |
| GO:0005681 | spliceosomal complex | - | IEA | Component |
| GO:0005829 | cytosol | - | IDA | Component |
| GO:0006353 | DNA-templated transcription, termination | 9748214. | TAS | Process |
| GO:0006369 | termination of RNA polymerase II transcription | 9748214. | TAS | Process |
| GO:0006397 | mRNA processing | - | IEA | Process |
| GO:0008023 | transcription elongation factor complex | 9748214. | TAS | Component |
| GO:0008094 | DNA-dependent ATPase activity | 9748214. | TAS | Function |
| GO:0008270 | zinc ion binding | - | IEA | Function |
| GO:0008380 | RNA splicing | - | IEA | Process |
| PID | Title | Article | Time | Author | Doi |
|---|---|---|---|---|---|
| 26356687 |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| CESC | |||
| COAD | |||
| DLBC | |||
| HNSC | |||
| LUAD | |||
| LUSC | |||
| READ | |||
| SKCM | |||
| STAD | |||
| TGCT | |||
| UVM |
| Cancer | P-value | Q-value |
|---|---|---|
| STAD | ||
| SARC | ||
| MESO | ||
| ACC | ||
| UCS | ||
| PRAD | ||
| LUSC | ||
| KIRP | ||
| COAD | ||
| READ | ||
| KICH | ||
| UCEC | ||
| LIHC | ||
| LUAD |