
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000393257 | RNB | PF00773.19 | 1.8e-49 | 1 | 1 |
| ENSP00000417401 | RNB | PF00773.19 | 2.8e-49 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000427522 | HELZ2-202 | 7827 | - | ENSP00000393257 | 2080 (aa) | - | Q9BYK8 |
| ENST00000467148 | HELZ2-204 | 8064 | XM_024452006 | ENSP00000417401 | 2649 (aa) | XP_024307774 | Q9BYK8 |
| ENST00000370082 | HELZ2-201 | 1827 | - | - | - (aa) | - | - |
| ENST00000479540 | HELZ2-206 | 3079 | - | - | - (aa) | - | - |
| ENST00000478861 | HELZ2-205 | 833 | - | - | - (aa) | - | - |
| ENST00000454223 | HELZ2-203 | 435 | - | - | - (aa) | - | - |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000130589 | Platelet Function Tests | 1.5003400E-005 | - |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000130589 | rs73622826 | 20 | 63571210 | ? | Plasma factor VII activating protease levels | 30070759 | [22.55-56.65] unit increase | 39.6 | EFO_0009368 |
| ENSG00000130589 | rs3810483 | 20 | 63562677 | ? | Red cell distribution width | 30595370 | EFO_0005192 |
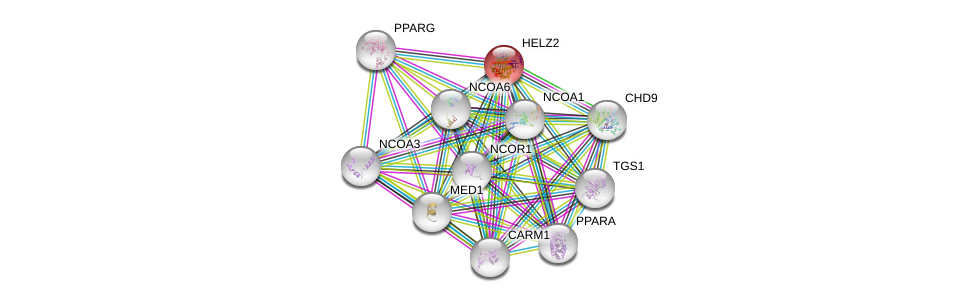
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000130589 | HELZ2 | 99 | 72.751 | ENSAMEG00000001622 | HELZ2 | 92 | 72.556 | Ailuropoda_melanoleuca |
| ENSG00000130589 | HELZ2 | 95 | 57.106 | ENSAPLG00000010386 | HELZ2 | 99 | 52.070 | Anas_platyrhynchos |
| ENSG00000130589 | HELZ2 | 95 | 57.474 | ENSACAG00000011519 | HELZ2 | 91 | 53.244 | Anolis_carolinensis |
| ENSG00000130589 | HELZ2 | 100 | 87.608 | ENSANAG00000019546 | HELZ2 | 100 | 87.721 | Aotus_nancymaae |
| ENSG00000130589 | HELZ2 | 94 | 47.396 | ENSAMXG00000017465 | helz2 | 90 | 41.170 | Astyanax_mexicanus |
| ENSG00000130589 | HELZ2 | 99 | 71.780 | ENSCAFG00000012968 | HELZ2 | 91 | 71.196 | Canis_familiaris |
| ENSG00000130589 | HELZ2 | 97 | 76.873 | ENSTSYG00000027453 | HELZ2 | 100 | 76.873 | Carlito_syrichta |
| ENSG00000130589 | HELZ2 | 99 | 71.997 | ENSCAPG00000010249 | HELZ2 | 91 | 71.884 | Cavia_aperea |
| ENSG00000130589 | HELZ2 | 99 | 71.514 | ENSCPOG00000006905 | HELZ2 | 91 | 71.402 | Cavia_porcellus |
| ENSG00000130589 | HELZ2 | 100 | 87.104 | ENSCCAG00000027744 | HELZ2 | 100 | 87.255 | Cebus_capucinus |
| ENSG00000130589 | HELZ2 | 100 | 93.663 | ENSCATG00000014259 | HELZ2 | 100 | 92.166 | Cercocebus_atys |
| ENSG00000130589 | HELZ2 | 99 | 72.642 | ENSCLAG00000006292 | HELZ2 | 91 | 72.428 | Chinchilla_lanigera |
| ENSG00000130589 | HELZ2 | 100 | 94.035 | ENSCSAG00000016417 | HELZ2 | 94 | 94.035 | Chlorocebus_sabaeus |
| ENSG00000130589 | HELZ2 | 96 | 62.016 | ENSCPBG00000014633 | HELZ2 | 91 | 55.072 | Chrysemys_picta_bellii |
| ENSG00000130589 | HELZ2 | 100 | 94.073 | ENSCANG00000033242 | HELZ2 | 100 | 94.073 | Colobus_angolensis_palliatus |
| ENSG00000130589 | HELZ2 | 100 | 70.672 | ENSCGRG00001016744 | Helz2 | 91 | 71.348 | Cricetulus_griseus_chok1gshd |
| ENSG00000130589 | HELZ2 | 100 | 71.338 | ENSCGRG00000012155 | Helz2 | 92 | 71.189 | Cricetulus_griseus_crigri |
| ENSG00000130589 | HELZ2 | 88 | 35.264 | ENSDARG00000012446 | zgc:113057 | 97 | 35.264 | Danio_rerio |
| ENSG00000130589 | HELZ2 | 96 | 47.423 | ENSDARG00000016527 | helz2 | 94 | 41.658 | Danio_rerio |
| ENSG00000130589 | HELZ2 | 92 | 46.803 | ENSDARG00000012600 | si:dkey-97a13.6 | 96 | 46.803 | Danio_rerio |
| ENSG00000130589 | HELZ2 | 99 | 66.970 | ENSDNOG00000017809 | HELZ2 | 98 | 66.640 | Dasypus_novemcinctus |
| ENSG00000130589 | HELZ2 | 100 | 70.832 | ENSDORG00000005596 | Helz2 | 92 | 70.907 | Dipodomys_ordii |
| ENSG00000130589 | HELZ2 | 73 | 75.124 | ENSETEG00000009947 | - | 62 | 76.289 | Echinops_telfairi |
| ENSG00000130589 | HELZ2 | 99 | 73.873 | ENSEASG00005023168 | HELZ2 | 91 | 73.688 | Equus_asinus_asinus |
| ENSG00000130589 | HELZ2 | 99 | 74.103 | ENSECAG00000013636 | HELZ2 | 91 | 76.761 | Equus_caballus |
| ENSG00000130589 | HELZ2 | 78 | 77.778 | ENSEEUG00000004620 | HELZ2 | 82 | 77.778 | Erinaceus_europaeus |
| ENSG00000130589 | HELZ2 | 92 | 47.967 | ENSELUG00000013322 | helz2 | 90 | 41.885 | Esox_lucius |
| ENSG00000130589 | HELZ2 | 95 | 57.623 | ENSFALG00000005852 | HELZ2 | 91 | 53.161 | Ficedula_albicollis |
| ENSG00000130589 | HELZ2 | 99 | 69.343 | ENSFDAG00000013078 | HELZ2 | 92 | 69.291 | Fukomys_damarensis |
| ENSG00000130589 | HELZ2 | 96 | 56.311 | ENSGALG00000006138 | HELZ2 | 91 | 52.573 | Gallus_gallus |
| ENSG00000130589 | HELZ2 | 95 | 61.240 | ENSGAGG00000019429 | HELZ2 | 91 | 54.865 | Gopherus_agassizii |
| ENSG00000130589 | HELZ2 | 100 | 98.304 | ENSGGOG00000008640 | HELZ2 | 100 | 98.304 | Gorilla_gorilla |
| ENSG00000130589 | HELZ2 | 99 | 71.711 | ENSHGLG00000013895 | HELZ2 | 92 | 71.487 | Heterocephalus_glaber_female |
| ENSG00000130589 | HELZ2 | 99 | 69.812 | ENSHGLG00100002953 | HELZ2 | 92 | 69.217 | Heterocephalus_glaber_male |
| ENSG00000130589 | HELZ2 | 73 | 34.375 | ENSIPUG00000017627 | zgc:113057 | 99 | 34.375 | Ictalurus_punctatus |
| ENSG00000130589 | HELZ2 | 100 | 72.320 | ENSSTOG00000023572 | HELZ2 | 92 | 72.307 | Ictidomys_tridecemlineatus |
| ENSG00000130589 | HELZ2 | 100 | 70.124 | ENSJJAG00000021775 | Helz2 | 91 | 70.734 | Jaculus_jaculus |
| ENSG00000130589 | HELZ2 | 95 | 54.220 | ENSLACG00000008155 | HELZ2 | 91 | 47.023 | Latimeria_chalumnae |
| ENSG00000130589 | HELZ2 | 95 | 54.337 | ENSLOCG00000001839 | si:dkey-97a13.6 | 91 | 48.258 | Lepisosteus_oculatus |
| ENSG00000130589 | HELZ2 | 95 | 51.256 | ENSLOCG00000001770 | helz2 | 91 | 47.459 | Lepisosteus_oculatus |
| ENSG00000130589 | HELZ2 | 100 | 93.847 | ENSMFAG00000002329 | HELZ2 | 100 | 93.847 | Macaca_fascicularis |
| ENSG00000130589 | HELZ2 | 100 | 93.658 | ENSMMUG00000006070 | HELZ2 | 100 | 93.361 | Macaca_mulatta |
| ENSG00000130589 | HELZ2 | 100 | 93.960 | ENSMNEG00000044829 | HELZ2 | 94 | 93.960 | Macaca_nemestrina |
| ENSG00000130589 | HELZ2 | 97 | 94.385 | ENSMLEG00000034372 | HELZ2 | 98 | 94.385 | Mandrillus_leucophaeus |
| ENSG00000130589 | HELZ2 | 95 | 57.215 | ENSMGAG00000006941 | HELZ2 | 91 | 53.080 | Meleagris_gallopavo |
| ENSG00000130589 | HELZ2 | 100 | 71.402 | ENSMAUG00000000857 | Helz2 | 92 | 71.252 | Mesocricetus_auratus |
| ENSG00000130589 | HELZ2 | 100 | 70.071 | ENSMICG00000027046 | HELZ2 | 100 | 70.145 | Microcebus_murinus |
| ENSG00000130589 | HELZ2 | 100 | 69.941 | ENSMOCG00000016283 | Helz2 | 92 | 69.831 | Microtus_ochrogaster |
| ENSG00000130589 | HELZ2 | 95 | 65.891 | ENSMODG00000016966 | - | 91 | 59.529 | Monodelphis_domestica |
| ENSG00000130589 | HELZ2 | 100 | 69.010 | MGP_CAROLIEiJ_G0024801 | Helz2 | 92 | 68.601 | Mus_caroli |
| ENSG00000130589 | HELZ2 | 100 | 68.666 | ENSMUSG00000027580 | Helz2 | 92 | 68.492 | Mus_musculus |
| ENSG00000130589 | HELZ2 | 100 | 68.718 | MGP_PahariEiJ_G0026249 | Helz2 | 92 | 68.614 | Mus_pahari |
| ENSG00000130589 | HELZ2 | 100 | 68.437 | MGP_SPRETEiJ_G0025727 | Helz2 | 92 | 68.226 | Mus_spretus |
| ENSG00000130589 | HELZ2 | 99 | 70.940 | ENSMPUG00000008361 | HELZ2 | 92 | 70.914 | Mustela_putorius_furo |
| ENSG00000130589 | HELZ2 | 99 | 72.956 | ENSMLUG00000014588 | HELZ2 | 92 | 73.097 | Myotis_lucifugus |
| ENSG00000130589 | HELZ2 | 100 | 71.144 | ENSNGAG00000013840 | Helz2 | 92 | 70.792 | Nannospalax_galili |
| ENSG00000130589 | HELZ2 | 100 | 93.318 | ENSNLEG00000010083 | - | 100 | 93.318 | Nomascus_leucogenys |
| ENSG00000130589 | HELZ2 | 97 | 68.293 | ENSMEUG00000006147 | HELZ2 | 97 | 68.293 | Notamacropus_eugenii |
| ENSG00000130589 | HELZ2 | 99 | 70.004 | ENSODEG00000007200 | HELZ2 | 92 | 69.821 | Octodon_degus |
| ENSG00000130589 | HELZ2 | 94 | 67.273 | ENSOANG00000004941 | - | 99 | 66.667 | Ornithorhynchus_anatinus |
| ENSG00000130589 | HELZ2 | 100 | 72.191 | ENSOGAG00000031068 | HELZ2 | 91 | 72.228 | Otolemur_garnettii |
| ENSG00000130589 | HELZ2 | 100 | 99.018 | ENSPPAG00000037593 | HELZ2 | 100 | 99.018 | Pan_paniscus |
| ENSG00000130589 | HELZ2 | 99 | 73.652 | ENSPPRG00000012585 | HELZ2 | 99 | 73.180 | Panthera_pardus |
| ENSG00000130589 | HELZ2 | 99 | 98.476 | ENSPTRG00000013743 | HELZ2 | 98 | 98.476 | Pan_troglodytes |
| ENSG00000130589 | HELZ2 | 100 | 94.073 | ENSPANG00000020634 | HELZ2 | 100 | 92.612 | Papio_anubis |
| ENSG00000130589 | HELZ2 | 94 | 50.129 | ENSPKIG00000005935 | helz2 | 95 | 44.225 | Paramormyrops_kingsleyae |
| ENSG00000130589 | HELZ2 | 95 | 60.569 | ENSPSIG00000012565 | HELZ2 | 89 | 60.569 | Pelodiscus_sinensis |
| ENSG00000130589 | HELZ2 | 100 | 71.159 | ENSPEMG00000016538 | Helz2 | 92 | 70.690 | Peromyscus_maniculatus_bairdii |
| ENSG00000130589 | HELZ2 | 99 | 54.328 | ENSPCIG00000017966 | HELZ2 | 99 | 60.044 | Phascolarctos_cinereus |
| ENSG00000130589 | HELZ2 | 100 | 93.394 | ENSPPYG00000011241 | HELZ2 | 100 | 93.394 | Pongo_abelii |
| ENSG00000130589 | HELZ2 | 99 | 66.487 | ENSPCAG00000001068 | HELZ2 | 100 | 66.933 | Procavia_capensis |
| ENSG00000130589 | HELZ2 | 100 | 74.615 | ENSPCOG00000017149 | HELZ2 | 100 | 74.690 | Propithecus_coquereli |
| ENSG00000130589 | HELZ2 | 92 | 82.051 | ENSPVAG00000007183 | HELZ2 | 97 | 82.051 | Pteropus_vampyrus |
| ENSG00000130589 | HELZ2 | 94 | 43.864 | ENSPNAG00000016859 | helz2 | 95 | 39.224 | Pygocentrus_nattereri |
| ENSG00000130589 | HELZ2 | 99 | 67.642 | ENSRNOG00000013267 | Helz2 | 88 | 67.741 | Rattus_norvegicus |
| ENSG00000130589 | HELZ2 | 100 | 94.337 | ENSRBIG00000044653 | HELZ2 | 100 | 94.337 | Rhinopithecus_bieti |
| ENSG00000130589 | HELZ2 | 100 | 94.262 | ENSRROG00000009088 | HELZ2 | 100 | 92.790 | Rhinopithecus_roxellana |
| ENSG00000130589 | HELZ2 | 100 | 87.330 | ENSSBOG00000033345 | HELZ2 | 100 | 87.406 | Saimiri_boliviensis_boliviensis |
| ENSG00000130589 | HELZ2 | 95 | 64.083 | ENSSHAG00000018163 | HELZ2 | 92 | 60.186 | Sarcophilus_harrisii |
| ENSG00000130589 | HELZ2 | 96 | 46.560 | ENSSFOG00015020580 | helz2 | 92 | 43.448 | Scleropages_formosus |
| ENSG00000130589 | HELZ2 | 63 | 75.479 | ENSSARG00000010235 | - | 69 | 75.479 | Sorex_araneus |
| ENSG00000130589 | HELZ2 | 51 | 45.981 | ENSSPUG00000018590 | - | 98 | 45.981 | Sphenodon_punctatus |
| ENSG00000130589 | HELZ2 | 97 | 68.378 | ENSSSCG00000003306 | HELZ2 | 90 | 68.378 | Sus_scrofa |
| ENSG00000130589 | HELZ2 | 95 | 58.140 | ENSTGUG00000006981 | HELZ2 | 99 | 53.826 | Taeniopygia_guttata |
| ENSG00000130589 | HELZ2 | 99 | 70.901 | ENSUAMG00000025224 | - | 94 | 70.160 | Ursus_americanus |
| ENSG00000130589 | HELZ2 | 99 | 71.713 | ENSVVUG00000015158 | HELZ2 | 89 | 71.412 | Vulpes_vulpes |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000184 | nuclear-transcribed mRNA catabolic process, nonsense-mediated decay | 21873635. | IBA | Process |
| GO:0003677 | DNA binding | - | IEA | Function |
| GO:0003723 | RNA binding | 22658674.22681889. | HDA | Function |
| GO:0003723 | RNA binding | 21873635. | IBA | Function |
| GO:0004004 | ATP-dependent RNA helicase activity | 21873635. | IBA | Function |
| GO:0004540 | ribonuclease activity | - | IEA | Function |
| GO:0005515 | protein binding | 16239304. | IPI | Function |
| GO:0005524 | ATP binding | - | IEA | Function |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0005737 | cytoplasm | 21873635. | IBA | Component |
| GO:0016020 | membrane | 19946888. | HDA | Component |
| GO:0019216 | regulation of lipid metabolic process | - | TAS | Process |
| GO:0030374 | nuclear receptor transcription coactivator activity | 16239304. | IDA | Function |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 16239304. | IDA | Process |
| GO:0046872 | metal ion binding | - | IEA | Function |
| GO:0090501 | RNA phosphodiester bond hydrolysis | - | IEA | Process |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| MESO | |||||||
| OV | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| THCA | |||||||
| THYM | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UVM |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| LIHC | |||
| LUAD | |||
| OV | |||
| PRAD | |||
| READ | |||
| SARC | |||
| SKCM |
| Cancer | P-value | Q-value |
|---|---|---|
| THYM | ||
| STAD | ||
| ACC | ||
| SKCM | ||
| PRAD | ||
| LUSC | ||
| TGCT | ||
| KIRP | ||
| LAML | ||
| UCEC | ||
| CHOL | ||
| UVM |