
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000269197 | HARE-HTH | PF05066.13 | 7.5e-18 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000269197 | ASXL3-201 | 11743 | XM_005258356 | ENSP00000269197 | 2248 (aa) | XP_005258413 | Q9C0F0 |
| ENST00000588038 | ASXL3-205 | 572 | - | - | - (aa) | - | - |
| ENST00000593195 | ASXL3-212 | 3968 | - | ENSP00000466073 | 61 (aa) | - | K7ELG8 |
| ENST00000590225 | ASXL3-207 | 546 | - | - | - (aa) | - | - |
| ENST00000590973 | ASXL3-208 | 571 | - | - | - (aa) | - | - |
| ENST00000586948 | ASXL3-204 | 468 | - | - | - (aa) | - | - |
| ENST00000592288 | ASXL3-209 | 3819 | - | ENSP00000465053 | 318 (aa) | - | K7EJ76 |
| ENST00000647014 | ASXL3-215 | 724 | - | - | - (aa) | - | - |
| ENST00000593235 | ASXL3-213 | 493 | - | - | - (aa) | - | - |
| ENST00000642541 | ASXL3-214 | 4216 | XM_011526209 | ENSP00000493665 | 1191 (aa) | XP_011524511 | A0A2R8Y461 |
| ENST00000592349 | ASXL3-210 | 558 | - | - | - (aa) | - | - |
| ENST00000585426 | ASXL3-202 | 653 | - | - | - (aa) | - | - |
| ENST00000586327 | ASXL3-203 | 559 | - | - | - (aa) | - | - |
| ENST00000592541 | ASXL3-211 | 3661 | - | ENSP00000466655 | 85 (aa) | - | K7EMU6 |
| ENST00000590189 | ASXL3-206 | 843 | - | - | - (aa) | - | - |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000141431 | Lipoprotein(a) | 8.6790000E-005 | - |
| ENSG00000141431 | Potassium | 5.6950000E-005 | - |
| ENSG00000141431 | Platelet Function Tests | 2.8051400E-005 | - |
| ENSG00000141431 | Platelet Function Tests | 1.6838100E-005 | - |
| ENSG00000141431 | Platelet Function Tests | 6.4037139E-006 | - |
| ENSG00000141431 | Respiratory Function Tests | 7E-6 | 23932459 |
| ENSG00000141431 | Vital Capacity | 7E-6 | 23932459 |
| ENSG00000141431 | Emotions | 8E-6 | 27089181 |
| ENSG00000141431 | Emotions | 5E-6 | 27089181 |
| ENSG00000141431 | Emotions | 4E-6 | 27089181 |
| ENSG00000141431 | Asthma | 7E-6 | 25918132 |
| ENSG00000141431 | Toluene 2,4-Diisocyanate | 7E-6 | 25918132 |
| ENSG00000141431 | Antidepressive Agents | 4E-6 | 20360315 |
| ENSG00000141431 | Antibodies | 8E-6 | 24324551 |
| ENSG00000141431 | Trypanosoma cruzi | 8E-6 | 24324551 |
| ENSG00000141431 | Asthma | 5E-6 | 25918132 |
| ENSG00000141431 | Toluene 2,4-Diisocyanate | 5E-6 | 25918132 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000141431 | rs55916387 | 18 | 33666280 | ? | Antibody status in Tripanosoma cruzi seropositivity | 24324551 | EFO_0004556|EFO_0005530 | ||
| ENSG00000141431 | rs4799710 | 18 | 33686777 | ? | Pulmonary function | 23932459 | EFO_0003892|EFO_0004312 | ||
| ENSG00000141431 | rs7228141 | 18 | 33634986 | G | Highest math class taken | 30038396 | [0.0092-0.0182] unit increase | 0.0137 | EFO_0004875 |
| ENSG00000141431 | rs12957987 | 18 | 33632245 | A | Educational attainment (MTAG) | 30038396 | [0.0063-0.0113] unit increase | 0.0088 | EFO_0004784 |
| ENSG00000141431 | rs8084619 | 18 | 33628696 | A | Highest math class taken (MTAG) | 30038396 | [0.0084-0.015] unit increase | 0.0117 | EFO_0004875 |
| ENSG00000141431 | rs16964886 | 18 | 33742030 | A | Diisocyanate-induced asthma | 25918132 | [2.62-17.46] | 6.77 | EFO_0006995|EFO_0000270 |
| ENSG00000141431 | rs11081818 | 18 | 33671124 | A | Body mass index | 30108127 | [NR] unit increase | 0.014 | EFO_0004340 |
| ENSG00000141431 | rs12953422 | 18 | 33612565 | A | Educational attainment (years of education) | 30038396 | [0.0053-0.0107] unit decrease | 0.008 | EFO_0004784 |
| ENSG00000141431 | rs7226575 | 18 | 33589018 | T | Systolic blood pressure | 30578418 | [0.21-0.39] mmHg decrease | 0.2999 | EFO_0006335 |
| ENSG00000141431 | rs6507054 | 18 | 33668359 | ? | Body mass index | 30595370 | EFO_0004340 | ||
| ENSG00000141431 | rs10164193 | 18 | 33581462 | T | Diastolic blood pressure | 30224653 | [0.16-0.28] mmHg decrease | 0.2196 | EFO_0006336 |
| ENSG00000141431 | rs1155156 | 18 | 33714297 | A | Life satisfaction | 30643256 | [0.0056-0.0105] unit increase | 0.008061787 | EFO_0007869 |
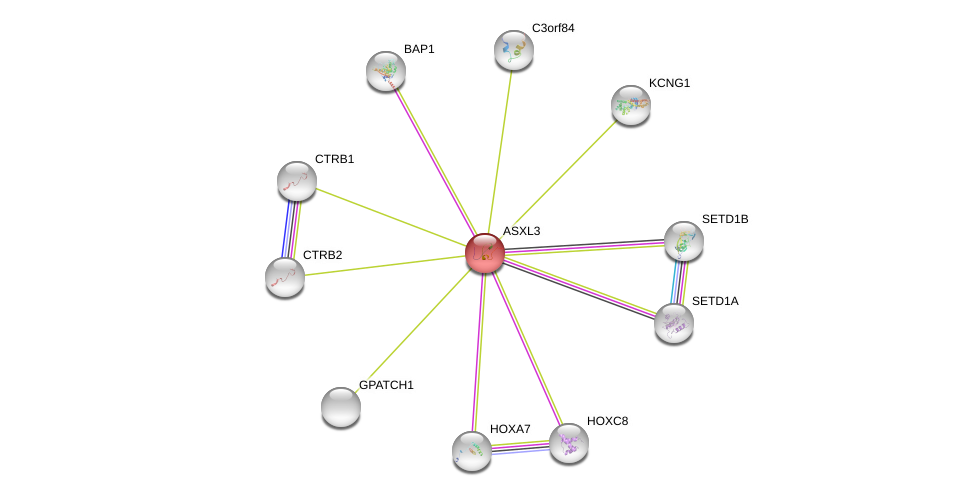
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSAPOG00000016599 | - | 73 | 56.579 | Acanthochromis_polyacanthus |
| ENSG00000141431 | ASXL3 | 75 | 63.043 | ENSACIG00000016887 | - | 85 | 68.056 | Amphilophus_citrinellus |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSACIG00000013802 | - | 60 | 56.579 | Amphilophus_citrinellus |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSAPEG00000014832 | - | 73 | 56.579 | Amphiprion_percula |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSATEG00000000035 | - | 68 | 56.579 | Anabas_testudineus |
| ENSG00000141431 | ASXL3 | 84 | 91.045 | ENSACAG00000017883 | ASXL3 | 100 | 66.310 | Anolis_carolinensis |
| ENSG00000141431 | ASXL3 | 59 | 61.111 | ENSACAG00000012597 | - | 74 | 64.103 | Anolis_carolinensis |
| ENSG00000141431 | ASXL3 | 100 | 96.474 | ENSANAG00000034397 | ASXL3 | 99 | 95.432 | Aotus_nancymaae |
| ENSG00000141431 | ASXL3 | 72 | 71.111 | ENSANAG00000032163 | ASXL1 | 100 | 66.667 | Aotus_nancymaae |
| ENSG00000141431 | ASXL3 | 100 | 87.280 | ENSBTAG00000047003 | ASXL3 | 91 | 96.350 | Bos_taurus |
| ENSG00000141431 | ASXL3 | 72 | 71.111 | ENSCJAG00000020708 | ASXL1 | 100 | 68.421 | Callithrix_jacchus |
| ENSG00000141431 | ASXL3 | 100 | 95.634 | ENSCJAG00000020922 | ASXL3 | 99 | 95.623 | Callithrix_jacchus |
| ENSG00000141431 | ASXL3 | 100 | 90.940 | ENSCAFG00000017980 | ASXL3 | 100 | 89.267 | Canis_familiaris |
| ENSG00000141431 | ASXL3 | 99 | 85.276 | ENSCAFG00020011763 | - | 89 | 90.429 | Canis_lupus_dingo |
| ENSG00000141431 | ASXL3 | 100 | 87.531 | ENSCHIG00000000206 | ASXL3 | 99 | 85.078 | Capra_hircus |
| ENSG00000141431 | ASXL3 | 100 | 91.107 | ENSTSYG00000009121 | ASXL3 | 99 | 91.153 | Carlito_syrichta |
| ENSG00000141431 | ASXL3 | 69 | 50.000 | ENSCAPG00000016451 | - | 56 | 64.615 | Cavia_aperea |
| ENSG00000141431 | ASXL3 | 80 | 64.000 | ENSCPOG00000007343 | ASXL2 | 58 | 48.718 | Cavia_porcellus |
| ENSG00000141431 | ASXL3 | 84 | 65.385 | ENSCCAG00000023224 | ASXL1 | 100 | 66.667 | Cebus_capucinus |
| ENSG00000141431 | ASXL3 | 100 | 95.718 | ENSCCAG00000010303 | ASXL3 | 99 | 95.757 | Cebus_capucinus |
| ENSG00000141431 | ASXL3 | 100 | 96.558 | ENSCATG00000040823 | ASXL3 | 100 | 96.448 | Cercocebus_atys |
| ENSG00000141431 | ASXL3 | 90 | 43.464 | ENSCATG00000034343 | ASXL1 | 100 | 66.667 | Cercocebus_atys |
| ENSG00000141431 | ASXL3 | 80 | 64.000 | ENSCLAG00000011428 | ASXL2 | 58 | 48.974 | Chinchilla_lanigera |
| ENSG00000141431 | ASXL3 | 100 | 96.641 | ENSCANG00000020882 | ASXL3 | 100 | 96.507 | Colobus_angolensis_palliatus |
| ENSG00000141431 | ASXL3 | 86 | 42.034 | ENSCANG00000030372 | ASXL1 | 100 | 66.667 | Colobus_angolensis_palliatus |
| ENSG00000141431 | ASXL3 | 84 | 61.538 | ENSCGRG00000018294 | Asxl2 | 58 | 48.698 | Cricetulus_griseus_crigri |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSCSEG00000004640 | - | 78 | 56.579 | Cynoglossus_semilaevis |
| ENSG00000141431 | ASXL3 | 84 | 63.462 | ENSCVAG00000011364 | - | 68 | 56.579 | Cyprinodon_variegatus |
| ENSG00000141431 | ASXL3 | 52 | 59.375 | ENSDORG00000028887 | - | 82 | 63.235 | Dipodomys_ordii |
| ENSG00000141431 | ASXL3 | 100 | 86.600 | ENSDORG00000026299 | Asxl3 | 99 | 86.250 | Dipodomys_ordii |
| ENSG00000141431 | ASXL3 | 84 | 56.863 | ENSEBUG00000015628 | - | 85 | 43.182 | Eptatretus_burgeri |
| ENSG00000141431 | ASXL3 | 100 | 90.856 | ENSEASG00005016631 | ASXL3 | 99 | 90.645 | Equus_asinus_asinus |
| ENSG00000141431 | ASXL3 | 100 | 90.772 | ENSFCAG00000024545 | ASXL3 | 99 | 89.701 | Felis_catus |
| ENSG00000141431 | ASXL3 | 84 | 91.045 | ENSFALG00000005882 | ASXL3 | 99 | 69.720 | Ficedula_albicollis |
| ENSG00000141431 | ASXL3 | 77 | 61.702 | ENSGMOG00000004155 | - | 92 | 46.076 | Gadus_morhua |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSGMOG00000009096 | - | 57 | 44.444 | Gadus_morhua |
| ENSG00000141431 | ASXL3 | 89 | 91.228 | ENSGALG00000015196 | ASXL3 | 100 | 71.632 | Gallus_gallus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSGAFG00000014909 | - | 82 | 55.696 | Gambusia_affinis |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSGACG00000012822 | asxl1 | 52 | 45.407 | Gasterosteus_aculeatus |
| ENSG00000141431 | ASXL3 | 84 | 92.910 | ENSGAGG00000023753 | ASXL3 | 100 | 71.909 | Gopherus_agassizii |
| ENSG00000141431 | ASXL3 | 79 | 62.500 | ENSGAGG00000020819 | ASXL1 | 50 | 50.133 | Gopherus_agassizii |
| ENSG00000141431 | ASXL3 | 87 | 41.751 | ENSGGOG00000003328 | ASXL1 | 100 | 66.667 | Gorilla_gorilla |
| ENSG00000141431 | ASXL3 | 100 | 99.328 | ENSGGOG00000003118 | ASXL3 | 99 | 99.021 | Gorilla_gorilla |
| ENSG00000141431 | ASXL3 | 84 | 61.538 | ENSHGLG00000006048 | ASXL2 | 60 | 49.373 | Heterocephalus_glaber_female |
| ENSG00000141431 | ASXL3 | 80 | 68.000 | ENSHGLG00000017863 | - | 71 | 68.056 | Heterocephalus_glaber_female |
| ENSG00000141431 | ASXL3 | 84 | 61.538 | ENSHGLG00100010557 | ASXL2 | 60 | 49.373 | Heterocephalus_glaber_male |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSHCOG00000013253 | - | 68 | 56.579 | Hippocampus_comes |
| ENSG00000141431 | ASXL3 | 75 | 43.478 | ENSJJAG00000021569 | - | 71 | 61.194 | Jaculus_jaculus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSKMAG00000013765 | - | 83 | 57.333 | Kryptolebias_marmoratus |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSLBEG00000012396 | - | 86 | 54.762 | Labrus_bergylta |
| ENSG00000141431 | ASXL3 | 80 | 93.878 | ENSLOCG00000006197 | ASXL3 | 57 | 69.777 | Lepisosteus_oculatus |
| ENSG00000141431 | ASXL3 | 100 | 97.061 | ENSMFAG00000032715 | ASXL3 | 100 | 96.801 | Macaca_fascicularis |
| ENSG00000141431 | ASXL3 | 90 | 43.464 | ENSMFAG00000029400 | ASXL1 | 100 | 66.667 | Macaca_fascicularis |
| ENSG00000141431 | ASXL3 | 100 | 96.893 | ENSMMUG00000014451 | ASXL3 | 100 | 96.713 | Macaca_mulatta |
| ENSG00000141431 | ASXL3 | 90 | 43.464 | ENSMMUG00000007117 | ASXL1 | 100 | 66.667 | Macaca_mulatta |
| ENSG00000141431 | ASXL3 | 87 | 41.275 | ENSMNEG00000031201 | ASXL1 | 100 | 66.667 | Macaca_nemestrina |
| ENSG00000141431 | ASXL3 | 100 | 96.641 | ENSMNEG00000041270 | ASXL3 | 100 | 96.490 | Macaca_nemestrina |
| ENSG00000141431 | ASXL3 | 91 | 41.613 | ENSMLEG00000024749 | ASXL1 | 100 | 66.667 | Mandrillus_leucophaeus |
| ENSG00000141431 | ASXL3 | 100 | 96.893 | ENSMLEG00000030306 | ASXL3 | 100 | 95.833 | Mandrillus_leucophaeus |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSMAMG00000008791 | - | 85 | 56.579 | Mastacembelus_armatus |
| ENSG00000141431 | ASXL3 | 84 | 91.045 | ENSMGAG00000010637 | ASXL3 | 100 | 70.701 | Meleagris_gallopavo |
| ENSG00000141431 | ASXL3 | 89 | 94.366 | ENSMAUG00000010440 | Asxl3 | 99 | 81.943 | Mesocricetus_auratus |
| ENSG00000141431 | ASXL3 | 75 | 70.213 | ENSMAUG00000000537 | - | 53 | 68.056 | Mesocricetus_auratus |
| ENSG00000141431 | ASXL3 | 100 | 92.701 | ENSMICG00000031715 | ASXL3 | 99 | 92.194 | Microcebus_murinus |
| ENSG00000141431 | ASXL3 | 100 | 81.925 | ENSMOCG00000020273 | Asxl3 | 99 | 81.453 | Microtus_ochrogaster |
| ENSG00000141431 | ASXL3 | 80 | 68.000 | ENSMOCG00000014066 | - | 85 | 68.056 | Microtus_ochrogaster |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSMMOG00000017515 | - | 80 | 57.333 | Mola_mola |
| ENSG00000141431 | ASXL3 | 89 | 94.737 | ENSMODG00000010795 | ASXL3 | 99 | 76.104 | Monodelphis_domestica |
| ENSG00000141431 | ASXL3 | 72 | 68.889 | ENSMALG00000021361 | - | 81 | 54.762 | Monopterus_albus |
| ENSG00000141431 | ASXL3 | 84 | 59.615 | MGP_CAROLIEiJ_G0017573 | Asxl2 | 93 | 49.734 | Mus_caroli |
| ENSG00000141431 | ASXL3 | 84 | 59.615 | ENSMUSG00000037486 | Asxl2 | 96 | 49.620 | Mus_musculus |
| ENSG00000141431 | ASXL3 | 80 | 64.000 | MGP_SPRETEiJ_G0018417 | Asxl2 | 93 | 49.740 | Mus_spretus |
| ENSG00000141431 | ASXL3 | 100 | 84.396 | ENSNGAG00000016058 | Asxl3 | 99 | 81.551 | Nannospalax_galili |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSNBRG00000021565 | - | 87 | 51.807 | Neolamprologus_brichardi |
| ENSG00000141431 | ASXL3 | 100 | 98.321 | ENSNLEG00000006333 | ASXL3 | 100 | 97.868 | Nomascus_leucogenys |
| ENSG00000141431 | ASXL3 | 86 | 42.712 | ENSNLEG00000009794 | ASXL1 | 100 | 66.667 | Nomascus_leucogenys |
| ENSG00000141431 | ASXL3 | 100 | 87.930 | ENSODEG00000018431 | ASXL3 | 99 | 87.589 | Octodon_degus |
| ENSG00000141431 | ASXL3 | 75 | 70.213 | ENSODEG00000012381 | - | 88 | 59.341 | Octodon_degus |
| ENSG00000141431 | ASXL3 | 84 | 94.030 | ENSOANG00000005610 | - | 98 | 70.945 | Ornithorhynchus_anatinus |
| ENSG00000141431 | ASXL3 | 100 | 88.507 | ENSOCUG00000010832 | ASXL3 | 100 | 88.824 | Oryctolagus_cuniculus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSORLG00000027477 | - | 84 | 57.333 | Oryzias_latipes |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSORLG00020003431 | - | 84 | 57.333 | Oryzias_latipes_hni |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSORLG00015017723 | - | 84 | 57.333 | Oryzias_latipes_hsok |
| ENSG00000141431 | ASXL3 | 72 | 52.273 | ENSORLG00015003122 | - | 74 | 68.254 | Oryzias_latipes_hsok |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSOMEG00000011176 | - | 59 | 57.333 | Oryzias_melastigma |
| ENSG00000141431 | ASXL3 | 100 | 85.356 | ENSOARG00000005872 | ASXL3 | 100 | 83.609 | Ovis_aries |
| ENSG00000141431 | ASXL3 | 86 | 42.373 | ENSPPAG00000028038 | ASXL1 | 100 | 66.667 | Pan_paniscus |
| ENSG00000141431 | ASXL3 | 100 | 99.496 | ENSPPAG00000027991 | ASXL3 | 100 | 99.238 | Pan_paniscus |
| ENSG00000141431 | ASXL3 | 100 | 90.688 | ENSPPRG00000025087 | ASXL3 | 99 | 89.549 | Panthera_pardus |
| ENSG00000141431 | ASXL3 | 100 | 89.513 | ENSPTIG00000010175 | ASXL3 | 100 | 86.705 | Panthera_tigris_altaica |
| ENSG00000141431 | ASXL3 | 54 | 51.515 | ENSPTIG00000008552 | - | 85 | 63.636 | Panthera_tigris_altaica |
| ENSG00000141431 | ASXL3 | 90 | 43.791 | ENSPTRG00000013377 | ASXL1 | 100 | 66.667 | Pan_troglodytes |
| ENSG00000141431 | ASXL3 | 100 | 99.580 | ENSPTRG00000009962 | ASXL3 | 100 | 99.378 | Pan_troglodytes |
| ENSG00000141431 | ASXL3 | 90 | 43.464 | ENSPANG00000025544 | ASXL1 | 100 | 66.667 | Papio_anubis |
| ENSG00000141431 | ASXL3 | 100 | 96.809 | ENSPANG00000007343 | ASXL3 | 100 | 96.490 | Papio_anubis |
| ENSG00000141431 | ASXL3 | 59 | 80.142 | ENSPKIG00000000956 | ASXL3 | 53 | 75.510 | Paramormyrops_kingsleyae |
| ENSG00000141431 | ASXL3 | 75 | 65.217 | ENSPMGG00000024122 | - | 83 | 68.056 | Periophthalmus_magnuspinnatus |
| ENSG00000141431 | ASXL3 | 75 | 70.213 | ENSPMGG00000017948 | - | 74 | 58.667 | Periophthalmus_magnuspinnatus |
| ENSG00000141431 | ASXL3 | 89 | 94.718 | ENSPEMG00000014301 | Asxl3 | 99 | 82.387 | Peromyscus_maniculatus_bairdii |
| ENSG00000141431 | ASXL3 | 89 | 35.331 | ENSPMAG00000000240 | - | 99 | 40.602 | Petromyzon_marinus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSPLAG00000004055 | - | 85 | 51.389 | Poecilia_latipinna |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSPMEG00000000899 | - | 72 | 57.333 | Poecilia_mexicana |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSPREG00000008490 | - | 75 | 57.333 | Poecilia_reticulata |
| ENSG00000141431 | ASXL3 | 75 | 63.043 | ENSPREG00000014267 | - | 85 | 68.056 | Poecilia_reticulata |
| ENSG00000141431 | ASXL3 | 99 | 90.331 | ENSPCOG00000024916 | ASXL3 | 99 | 90.331 | Propithecus_coquereli |
| ENSG00000141431 | ASXL3 | 70 | 60.465 | ENSRBIG00000038437 | - | 100 | 66.667 | Rhinopithecus_bieti |
| ENSG00000141431 | ASXL3 | 100 | 96.809 | ENSRBIG00000029166 | ASXL3 | 100 | 94.744 | Rhinopithecus_bieti |
| ENSG00000141431 | ASXL3 | 87 | 41.414 | ENSRROG00000000172 | ASXL1 | 100 | 66.667 | Rhinopithecus_roxellana |
| ENSG00000141431 | ASXL3 | 100 | 96.809 | ENSRROG00000045627 | ASXL3 | 100 | 96.132 | Rhinopithecus_roxellana |
| ENSG00000141431 | ASXL3 | 87 | 41.892 | ENSSBOG00000023781 | ASXL1 | 100 | 66.667 | Saimiri_boliviensis_boliviensis |
| ENSG00000141431 | ASXL3 | 100 | 95.550 | ENSSBOG00000031872 | ASXL3 | 100 | 95.522 | Saimiri_boliviensis_boliviensis |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSSFOG00015020389 | - | 71 | 51.111 | Scleropages_formosus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSSMAG00000003213 | - | 85 | 51.724 | Scophthalmus_maximus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSSDUG00000000824 | - | 51 | 57.333 | Seriola_dumerili |
| ENSG00000141431 | ASXL3 | 86 | 88.772 | ENSSPUG00000006158 | - | 99 | 88.772 | Sphenodon_punctatus |
| ENSG00000141431 | ASXL3 | 100 | 88.842 | ENSSSCG00000003736 | ASXL3 | 99 | 87.388 | Sus_scrofa |
| ENSG00000141431 | ASXL3 | 51 | 67.742 | ENSTGUG00000014522 | - | 97 | 70.312 | Taeniopygia_guttata |
| ENSG00000141431 | ASXL3 | 87 | 90.614 | ENSTGUG00000010779 | ASXL3 | 100 | 69.635 | Taeniopygia_guttata |
| ENSG00000141431 | ASXL3 | 86 | 40.753 | ENSTGUG00000006483 | ASXL1 | 55 | 48.634 | Taeniopygia_guttata |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSTRUG00000021192 | - | 77 | 57.333 | Takifugu_rubripes |
| ENSG00000141431 | ASXL3 | 66 | 50.000 | ENSUAMG00000023398 | - | 78 | 61.972 | Ursus_americanus |
| ENSG00000141431 | ASXL3 | 80 | 64.000 | ENSUAMG00000027962 | ASXL2 | 58 | 48.953 | Ursus_americanus |
| ENSG00000141431 | ASXL3 | 51 | 64.516 | ENSUMAG00000022345 | ASXL2 | 57 | 48.396 | Ursus_maritimus |
| ENSG00000141431 | ASXL3 | 100 | 89.262 | ENSUMAG00000001778 | ASXL3 | 100 | 86.119 | Ursus_maritimus |
| ENSG00000141431 | ASXL3 | 100 | 91.275 | ENSVVUG00000027494 | ASXL3 | 100 | 89.178 | Vulpes_vulpes |
| ENSG00000141431 | ASXL3 | 89 | 89.510 | ENSXETG00000020547 | asxl3 | 97 | 74.937 | Xenopus_tropicalis |
| ENSG00000141431 | ASXL3 | 75 | 63.043 | ENSXCOG00000001543 | - | 77 | 68.056 | Xiphophorus_couchianus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSXCOG00000008255 | - | 78 | 57.333 | Xiphophorus_couchianus |
| ENSG00000141431 | ASXL3 | 75 | 68.085 | ENSXMAG00000024079 | - | 78 | 57.333 | Xiphophorus_maculatus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000790 | nuclear chromatin | 21873635. | IBA | Component |
| GO:0003677 | DNA binding | - | IEA | Function |
| GO:0003682 | chromatin binding | 21873635. | IBA | Function |
| GO:0005634 | nucleus | 21873635. | IBA | Component |
| GO:0006351 | transcription, DNA-templated | - | IEA | Process |
| GO:0009887 | animal organ morphogenesis | 21873635. | IBA | Process |
| GO:0035517 | PR-DUB complex | 21873635. | IBA | Component |
| GO:0042975 | peroxisome proliferator activated receptor binding | 21873635. | IBA | Function |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 21873635. | IBA | Process |
| GO:0046872 | metal ion binding | - | IEA | Function |
| PID | Title | Article | Time | Author | Doi |
|---|---|---|---|---|---|
| 28935813 |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LAML | |||||||
| LAML | |||||||
| LAML | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| MESO | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UVM |
| Cancer | Type | Freq | Q-value |
|---|
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| ACC | ||
| LUSC | ||
| BRCA | ||
| KIRP | ||
| PAAD | ||
| LAML | ||
| UCEC | ||
| GBM | ||
| LIHC | ||
| LGG | ||
| CHOL | ||
| THCA | ||
| LUAD | ||
| OV |