
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000287538 | zf-C2H2 | PF00096.26 | 6.8e-21 | 1 | 4 |
| ENSP00000287538 | zf-C2H2 | PF00096.26 | 6.8e-21 | 2 | 4 |
| ENSP00000287538 | zf-C2H2 | PF00096.26 | 6.8e-21 | 3 | 4 |
| ENSP00000287538 | zf-C2H2 | PF00096.26 | 6.8e-21 | 4 | 4 |
| ENSP00000359638 | zf-C2H2 | PF00096.26 | 4.2e-20 | 1 | 4 |
| ENSP00000359638 | zf-C2H2 | PF00096.26 | 4.2e-20 | 2 | 4 |
| ENSP00000359638 | zf-C2H2 | PF00096.26 | 4.2e-20 | 3 | 4 |
| ENSP00000359638 | zf-C2H2 | PF00096.26 | 4.2e-20 | 4 | 4 |
| ENSP00000359638 | zf-met | PF12874.7 | 0.0016 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000478471 | ZIC3-203 | 366 | - | - | - (aa) | - | - |
| ENST00000287538 | ZIC3-201 | 3469 | - | ENSP00000287538 | 467 (aa) | - | O60481 |
| ENST00000370606 | ZIC3-202 | 1968 | - | ENSP00000359638 | 457 (aa) | - | O60481 |
| Pathway ID | Pathway Name | Source |
|---|---|---|
| hsa04550 | Signaling pathways regulating pluripotency of stem cells | KEGG |
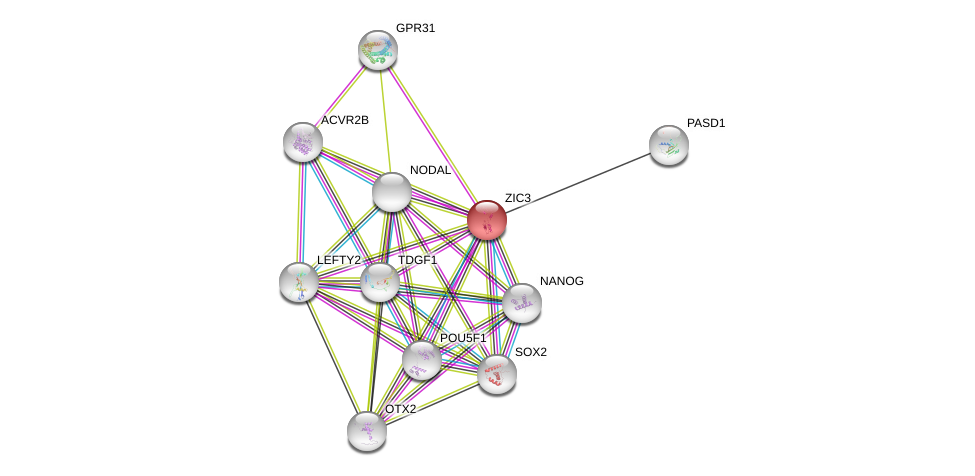
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000156925 | ZIC3 | 100 | 98.929 | ENSANAG00000019614 | ZIC3 | 100 | 98.929 | Aotus_nancymaae |
| ENSG00000156925 | ZIC3 | 100 | 98.501 | ENSCJAG00000013792 | ZIC3 | 100 | 98.501 | Callithrix_jacchus |
| ENSG00000156925 | ZIC3 | 100 | 98.073 | ENSCAFG00000018979 | ZIC3 | 100 | 98.073 | Canis_familiaris |
| ENSG00000156925 | ZIC3 | 100 | 95.503 | ENSTSYG00000003356 | ZIC3 | 100 | 95.503 | Carlito_syrichta |
| ENSG00000156925 | ZIC3 | 53 | 98.780 | ENSCPOG00000002374 | ZIC3 | 100 | 98.780 | Cavia_porcellus |
| ENSG00000156925 | ZIC3 | 100 | 98.715 | ENSCCAG00000025983 | ZIC3 | 100 | 98.715 | Cebus_capucinus |
| ENSG00000156925 | ZIC3 | 100 | 98.715 | ENSCATG00000036569 | ZIC3 | 100 | 98.715 | Cercocebus_atys |
| ENSG00000156925 | ZIC3 | 100 | 98.501 | ENSCLAG00000001934 | ZIC3 | 100 | 98.501 | Chinchilla_lanigera |
| ENSG00000156925 | ZIC3 | 93 | 86.009 | ENSCPBG00000026115 | ZIC3 | 100 | 86.009 | Chrysemys_picta_bellii |
| ENSG00000156925 | ZIC3 | 100 | 98.501 | ENSCANG00000017505 | ZIC3 | 100 | 98.501 | Colobus_angolensis_palliatus |
| ENSG00000156925 | ZIC3 | 100 | 98.287 | ENSCGRG00001024527 | Zic3 | 100 | 98.287 | Cricetulus_griseus_chok1gshd |
| ENSG00000156925 | ZIC3 | 100 | 97.430 | ENSDORG00000025481 | Zic3 | 100 | 97.430 | Dipodomys_ordii |
| ENSG00000156925 | ZIC3 | 100 | 98.073 | ENSFCAG00000025684 | ZIC3 | 100 | 98.073 | Felis_catus |
| ENSG00000156925 | ZIC3 | 79 | 98.113 | ENSFDAG00000014929 | ZIC3 | 100 | 99.593 | Fukomys_damarensis |
| ENSG00000156925 | ZIC3 | 94 | 80.227 | ENSGAGG00000004149 | ZIC3 | 92 | 80.227 | Gopherus_agassizii |
| ENSG00000156925 | ZIC3 | 100 | 99.572 | ENSGGOG00000011914 | ZIC3 | 100 | 99.572 | Gorilla_gorilla |
| ENSG00000156925 | ZIC3 | 100 | 97.430 | ENSHGLG00000006298 | ZIC3 | 100 | 97.430 | Heterocephalus_glaber_female |
| ENSG00000156925 | ZIC3 | 67 | 69.737 | ENSHGLG00100002829 | ZIC3 | 100 | 77.070 | Heterocephalus_glaber_male |
| ENSG00000156925 | ZIC3 | 100 | 98.287 | ENSJJAG00000022714 | Zic3 | 100 | 98.287 | Jaculus_jaculus |
| ENSG00000156925 | ZIC3 | 100 | 76.068 | ENSLACG00000014597 | ZIC3 | 100 | 76.068 | Latimeria_chalumnae |
| ENSG00000156925 | ZIC3 | 88 | 93.917 | ENSLAFG00000007048 | ZIC3 | 99 | 93.917 | Loxodonta_africana |
| ENSG00000156925 | ZIC3 | 100 | 98.715 | ENSMFAG00000027018 | ZIC3 | 100 | 98.715 | Macaca_fascicularis |
| ENSG00000156925 | ZIC3 | 100 | 98.687 | ENSMMUG00000002023 | ZIC3 | 100 | 98.687 | Macaca_mulatta |
| ENSG00000156925 | ZIC3 | 100 | 98.715 | ENSMNEG00000040682 | ZIC3 | 100 | 98.715 | Macaca_nemestrina |
| ENSG00000156925 | ZIC3 | 100 | 98.715 | ENSMLEG00000004378 | ZIC3 | 100 | 98.715 | Mandrillus_leucophaeus |
| ENSG00000156925 | ZIC3 | 100 | 98.073 | ENSMAUG00000009402 | Zic3 | 100 | 98.073 | Mesocricetus_auratus |
| ENSG00000156925 | ZIC3 | 100 | 98.501 | ENSMICG00000042529 | ZIC3 | 100 | 98.501 | Microcebus_murinus |
| ENSG00000156925 | ZIC3 | 100 | 97.859 | ENSMOCG00000020544 | Zic3 | 100 | 97.859 | Microtus_ochrogaster |
| ENSG00000156925 | ZIC3 | 100 | 98.287 | MGP_CAROLIEiJ_G0033101 | Zic3 | 100 | 99.593 | Mus_caroli |
| ENSG00000156925 | ZIC3 | 100 | 98.287 | ENSMUSG00000067860 | Zic3 | 100 | 99.593 | Mus_musculus |
| ENSG00000156925 | ZIC3 | 100 | 98.287 | MGP_PahariEiJ_G0031644 | Zic3 | 100 | 99.593 | Mus_pahari |
| ENSG00000156925 | ZIC3 | 100 | 98.287 | MGP_SPRETEiJ_G0034256 | Zic3 | 100 | 99.593 | Mus_spretus |
| ENSG00000156925 | ZIC3 | 100 | 97.430 | ENSNGAG00000023346 | Zic3 | 100 | 97.430 | Nannospalax_galili |
| ENSG00000156925 | ZIC3 | 78 | 99.262 | ENSNLEG00000003005 | - | 100 | 99.262 | Nomascus_leucogenys |
| ENSG00000156925 | ZIC3 | 100 | 98.287 | ENSODEG00000005556 | ZIC3 | 100 | 98.287 | Octodon_degus |
| ENSG00000156925 | ZIC3 | 100 | 99.572 | ENSPPAG00000030013 | ZIC3 | 100 | 99.572 | Pan_paniscus |
| ENSG00000156925 | ZIC3 | 100 | 98.073 | ENSPPRG00000010839 | ZIC3 | 100 | 98.073 | Panthera_pardus |
| ENSG00000156925 | ZIC3 | 100 | 99.572 | ENSPTRG00000043849 | ZIC3 | 100 | 99.572 | Pan_troglodytes |
| ENSG00000156925 | ZIC3 | 100 | 98.715 | ENSPANG00000011357 | ZIC3 | 100 | 98.715 | Papio_anubis |
| ENSG00000156925 | ZIC3 | 100 | 73.561 | ENSPKIG00000017705 | zic3 | 100 | 73.561 | Paramormyrops_kingsleyae |
| ENSG00000156925 | ZIC3 | 62 | 90.068 | ENSPSIG00000011896 | ZIC3 | 99 | 90.068 | Pelodiscus_sinensis |
| ENSG00000156925 | ZIC3 | 100 | 98.073 | ENSPEMG00000022168 | Zic3 | 100 | 98.073 | Peromyscus_maniculatus_bairdii |
| ENSG00000156925 | ZIC3 | 100 | 98.073 | ENSPCOG00000021557 | ZIC3 | 100 | 98.073 | Propithecus_coquereli |
| ENSG00000156925 | ZIC3 | 100 | 97.859 | ENSRNOG00000000861 | Zic3 | 100 | 97.859 | Rattus_norvegicus |
| ENSG00000156925 | ZIC3 | 100 | 98.501 | ENSRBIG00000030660 | ZIC3 | 100 | 98.501 | Rhinopithecus_bieti |
| ENSG00000156925 | ZIC3 | 100 | 98.501 | ENSRROG00000028410 | ZIC3 | 100 | 98.501 | Rhinopithecus_roxellana |
| ENSG00000156925 | ZIC3 | 100 | 98.715 | ENSSBOG00000024684 | ZIC3 | 100 | 98.715 | Saimiri_boliviensis_boliviensis |
| ENSG00000156925 | ZIC3 | 99 | 74.304 | ENSSFOG00015011731 | zic3 | 100 | 74.304 | Scleropages_formosus |
| ENSG00000156925 | ZIC3 | 99 | 68.522 | ENSSFOG00015008079 | zic3 | 100 | 68.522 | Scleropages_formosus |
| ENSG00000156925 | ZIC3 | 84 | 83.038 | ENSTGUG00000002155 | ZIC3 | 100 | 83.038 | Taeniopygia_guttata |
| ENSG00000156925 | ZIC3 | 100 | 98.073 | ENSVVUG00000021378 | ZIC3 | 100 | 98.073 | Vulpes_vulpes |
| ENSG00000156925 | ZIC3 | 100 | 76.383 | ENSXETG00000024458 | zic3 | 100 | 76.383 | Xenopus_tropicalis |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000977 | RNA polymerase II regulatory region sequence-specific DNA binding | 21873635. | IBA | Function |
| GO:0000978 | RNA polymerase II proximal promoter sequence-specific DNA binding | 17764085. | IDA | Function |
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | 21873635. | IBA | Function |
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | - | ISA | Function |
| GO:0001228 | DNA-binding transcription activator activity, RNA polymerase II-specific | 17764085. | IDA | Function |
| GO:0001947 | heart looping | 9354794. | IMP | Process |
| GO:0003700 | DNA-binding transcription factor activity | 17764085. | IDA | Function |
| GO:0005515 | protein binding | 17764085.18716025. | IPI | Function |
| GO:0005634 | nucleus | 21873635. | IBA | Component |
| GO:0005634 | nucleus | - | ISS | Component |
| GO:0005654 | nucleoplasm | - | IDA | Component |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0005737 | cytoplasm | - | ISS | Component |
| GO:0007368 | determination of left/right symmetry | 9354794. | IMP | Process |
| GO:0007417 | central nervous system development | 21873635. | IBA | Process |
| GO:0009952 | anterior/posterior pattern specification | - | IEA | Process |
| GO:0030154 | cell differentiation | - | IEA | Process |
| GO:0030324 | lung development | 9354794. | IMP | Process |
| GO:0035019 | somatic stem cell population maintenance | - | TAS | Process |
| GO:0035469 | determination of pancreatic left/right asymmetry | 9354794. | IMP | Process |
| GO:0035545 | determination of left/right asymmetry in nervous system | - | IEA | Process |
| GO:0043565 | sequence-specific DNA binding | 17764085. | IDA | Function |
| GO:0045893 | positive regulation of transcription, DNA-templated | - | ISS | Process |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 21873635. | IBA | Process |
| GO:0045944 | positive regulation of transcription by RNA polymerase II | 17764085. | IDA | Process |
| GO:0046872 | metal ion binding | - | IEA | Function |
| GO:0071907 | determination of digestive tract left/right asymmetry | 9354794. | IMP | Process |
| GO:0071910 | determination of liver left/right asymmetry | 9354794. | IMP | Process |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| DLBC | |||
| KIRC | |||
| READ | |||
| TGCT | |||
| THCA | |||
| UCS |
| Cancer | P-value | Q-value |
|---|---|---|
| MESO | ||
| GBM | ||
| LGG |