
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000359454 | ResIII | PF04851.15 | 2.8e-11 | 1 | 1 |
| ENSP00000359454 | DEAD | PF00270.29 | 7.9e-25 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000455133 | HFM1-205 | 596 | - | ENSP00000409827 | 138 (aa) | - | C9JQP7 |
| ENST00000427444 | HFM1-202 | 672 | - | ENSP00000388900 | 196 (aa) | - | C9JQ07 |
| ENST00000488023 | HFM1-208 | 1699 | - | - | - (aa) | - | - |
| ENST00000430465 | HFM1-203 | 1928 | XM_017000493 | ENSP00000387661 | 625 (aa) | XP_016855982 | H0Y3X7 |
| ENST00000497520 | HFM1-209 | 383 | - | - | - (aa) | - | - |
| ENST00000481900 | HFM1-207 | 2020 | - | - | - (aa) | - | - |
| ENST00000462405 | HFM1-206 | 2667 | - | - | - (aa) | - | - |
| ENST00000448819 | HFM1-204 | 540 | - | ENSP00000397369 | 151 (aa) | - | C9JA44 |
| ENST00000370425 | HFM1-201 | 4931 | XM_011540849 | ENSP00000359454 | 1435 (aa) | XP_011539151 | A2PYH4 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000162669 | rs10801851 | 1 | 91281449 | ? | Red cell distribution width | 30595370 | EFO_0005192 |
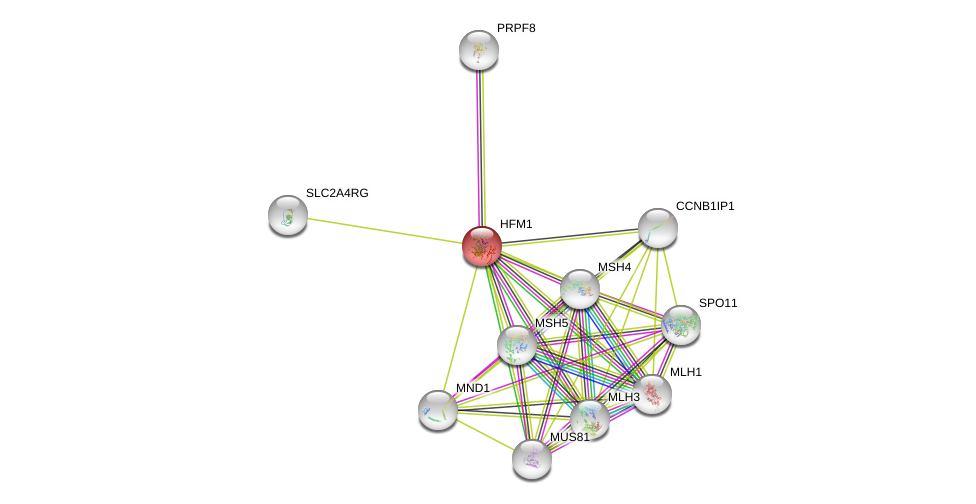
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000162669 | HFM1 | 64 | 65.192 | ENSAPOG00000005304 | hfm1 | 100 | 65.192 | Acanthochromis_polyacanthus |
| ENSG00000162669 | HFM1 | 100 | 86.518 | ENSAMEG00000000432 | HFM1 | 100 | 86.518 | Ailuropoda_melanoleuca |
| ENSG00000162669 | HFM1 | 70 | 60.662 | ENSACIG00000021553 | hfm1 | 91 | 60.662 | Amphilophus_citrinellus |
| ENSG00000162669 | HFM1 | 64 | 65.811 | ENSAOCG00000022839 | hfm1 | 100 | 65.811 | Amphiprion_ocellaris |
| ENSG00000162669 | HFM1 | 64 | 65.461 | ENSAPEG00000014316 | hfm1 | 96 | 69.532 | Amphiprion_percula |
| ENSG00000162669 | HFM1 | 67 | 64.396 | ENSATEG00000019181 | hfm1 | 80 | 63.537 | Anabas_testudineus |
| ENSG00000162669 | HFM1 | 100 | 60.301 | ENSAPLG00000013639 | HFM1 | 100 | 60.301 | Anas_platyrhynchos |
| ENSG00000162669 | HFM1 | 100 | 91.997 | ENSANAG00000029513 | HFM1 | 100 | 91.997 | Aotus_nancymaae |
| ENSG00000162669 | HFM1 | 65 | 63.734 | ENSACLG00000009033 | hfm1 | 97 | 65.316 | Astatotilapia_calliptera |
| ENSG00000162669 | HFM1 | 93 | 51.909 | ENSAMXG00000006108 | hfm1 | 90 | 52.053 | Astyanax_mexicanus |
| ENSG00000162669 | HFM1 | 100 | 85.278 | ENSBTAG00000020856 | HFM1 | 100 | 85.278 | Bos_taurus |
| ENSG00000162669 | HFM1 | 100 | 93.868 | ENSCJAG00000001843 | HFM1 | 100 | 93.868 | Callithrix_jacchus |
| ENSG00000162669 | HFM1 | 100 | 86.032 | ENSCAFG00000020187 | HFM1 | 100 | 86.032 | Canis_familiaris |
| ENSG00000162669 | HFM1 | 100 | 79.710 | ENSCAFG00020013595 | - | 100 | 84.009 | Canis_lupus_dingo |
| ENSG00000162669 | HFM1 | 95 | 71.970 | ENSCHIG00000018623 | - | 95 | 74.565 | Capra_hircus |
| ENSG00000162669 | HFM1 | 100 | 87.352 | ENSTSYG00000014250 | HFM1 | 100 | 87.352 | Carlito_syrichta |
| ENSG00000162669 | HFM1 | 99 | 78.984 | ENSCPOG00000007421 | HFM1 | 99 | 78.984 | Cavia_porcellus |
| ENSG00000162669 | HFM1 | 100 | 93.798 | ENSCCAG00000033206 | HFM1 | 100 | 93.798 | Cebus_capucinus |
| ENSG00000162669 | HFM1 | 100 | 96.864 | ENSCATG00000030987 | HFM1 | 100 | 96.864 | Cercocebus_atys |
| ENSG00000162669 | HFM1 | 100 | 81.242 | ENSCLAG00000005173 | HFM1 | 99 | 81.242 | Chinchilla_lanigera |
| ENSG00000162669 | HFM1 | 68 | 96.053 | ENSCHOG00000011824 | - | 77 | 96.053 | Choloepus_hoffmanni |
| ENSG00000162669 | HFM1 | 100 | 94.928 | ENSCANG00000034052 | - | 99 | 96.360 | Colobus_angolensis_palliatus |
| ENSG00000162669 | HFM1 | 100 | 73.946 | ENSCGRG00001016995 | Hfm1 | 100 | 73.946 | Cricetulus_griseus_chok1gshd |
| ENSG00000162669 | HFM1 | 100 | 78.179 | ENSCGRG00000017181 | Hfm1 | 100 | 78.179 | Cricetulus_griseus_crigri |
| ENSG00000162669 | HFM1 | 70 | 60.621 | ENSCSEG00000017659 | hfm1 | 93 | 60.621 | Cynoglossus_semilaevis |
| ENSG00000162669 | HFM1 | 50 | 69.101 | ENSCVAG00000005075 | hfm1 | 86 | 69.101 | Cyprinodon_variegatus |
| ENSG00000162669 | HFM1 | 60 | 66.238 | ENSDARG00000104288 | hfm1 | 77 | 66.238 | Danio_rerio |
| ENSG00000162669 | HFM1 | 100 | 86.957 | ENSDNOG00000004776 | HFM1 | 100 | 81.402 | Dasypus_novemcinctus |
| ENSG00000162669 | HFM1 | 100 | 78.709 | ENSDORG00000014661 | Hfm1 | 100 | 78.709 | Dipodomys_ordii |
| ENSG00000162669 | HFM1 | 100 | 84.892 | ENSEASG00005015424 | HFM1 | 98 | 85.435 | Equus_asinus_asinus |
| ENSG00000162669 | HFM1 | 100 | 84.983 | ENSECAG00000024039 | HFM1 | 100 | 84.983 | Equus_caballus |
| ENSG00000162669 | HFM1 | 64 | 66.744 | ENSELUG00000018944 | hfm1 | 99 | 66.744 | Esox_lucius |
| ENSG00000162669 | HFM1 | 100 | 86.319 | ENSFCAG00000029116 | HFM1 | 100 | 86.319 | Felis_catus |
| ENSG00000162669 | HFM1 | 100 | 60.014 | ENSFALG00000001781 | HFM1 | 100 | 60.428 | Ficedula_albicollis |
| ENSG00000162669 | HFM1 | 100 | 79.785 | ENSFDAG00000020816 | HFM1 | 100 | 79.785 | Fukomys_damarensis |
| ENSG00000162669 | HFM1 | 66 | 60.729 | ENSGMOG00000017436 | hfm1 | 100 | 60.729 | Gadus_morhua |
| ENSG00000162669 | HFM1 | 71 | 62.002 | ENSGAFG00000018093 | hfm1 | 93 | 67.150 | Gambusia_affinis |
| ENSG00000162669 | HFM1 | 66 | 62.319 | ENSGACG00000015686 | hfm1 | 100 | 62.319 | Gasterosteus_aculeatus |
| ENSG00000162669 | HFM1 | 100 | 100.000 | ENSGGOG00000038524 | HFM1 | 100 | 98.955 | Gorilla_gorilla |
| ENSG00000162669 | HFM1 | 65 | 64.807 | ENSHBUG00000007309 | hfm1 | 96 | 59.962 | Haplochromis_burtoni |
| ENSG00000162669 | HFM1 | 100 | 71.223 | ENSHGLG00000007780 | - | 100 | 80.384 | Heterocephalus_glaber_female |
| ENSG00000162669 | HFM1 | 100 | 71.223 | ENSHGLG00100019217 | - | 100 | 78.692 | Heterocephalus_glaber_male |
| ENSG00000162669 | HFM1 | 57 | 64.216 | ENSHCOG00000019632 | hfm1 | 97 | 64.216 | Hippocampus_comes |
| ENSG00000162669 | HFM1 | 66 | 64.632 | ENSIPUG00000017020 | hfm1 | 92 | 65.714 | Ictalurus_punctatus |
| ENSG00000162669 | HFM1 | 100 | 76.259 | ENSSTOG00000008477 | - | 100 | 81.023 | Ictidomys_tridecemlineatus |
| ENSG00000162669 | HFM1 | 100 | 78.219 | ENSJJAG00000017198 | Hfm1 | 100 | 78.219 | Jaculus_jaculus |
| ENSG00000162669 | HFM1 | 62 | 63.636 | ENSKMAG00000002282 | hfm1 | 90 | 63.707 | Kryptolebias_marmoratus |
| ENSG00000162669 | HFM1 | 70 | 60.707 | ENSLBEG00000006759 | hfm1 | 98 | 65.299 | Labrus_bergylta |
| ENSG00000162669 | HFM1 | 66 | 70.868 | ENSLACG00000010698 | HFM1 | 99 | 67.014 | Latimeria_chalumnae |
| ENSG00000162669 | HFM1 | 72 | 64.661 | ENSLOCG00000004931 | hfm1 | 96 | 64.756 | Lepisosteus_oculatus |
| ENSG00000162669 | HFM1 | 52 | 90.310 | ENSLAFG00000015903 | - | 99 | 90.310 | Loxodonta_africana |
| ENSG00000162669 | HFM1 | 100 | 95.652 | ENSMFAG00000003649 | HFM1 | 100 | 93.407 | Macaca_fascicularis |
| ENSG00000162669 | HFM1 | 100 | 96.376 | ENSMMUG00000006819 | HFM1 | 100 | 96.376 | Macaca_mulatta |
| ENSG00000162669 | HFM1 | 100 | 95.652 | ENSMNEG00000039833 | - | 99 | 94.647 | Macaca_nemestrina |
| ENSG00000162669 | HFM1 | 100 | 95.652 | ENSMLEG00000027571 | - | 99 | 96.146 | Mandrillus_leucophaeus |
| ENSG00000162669 | HFM1 | 54 | 70.641 | ENSMAMG00000004623 | hfm1 | 97 | 66.908 | Mastacembelus_armatus |
| ENSG00000162669 | HFM1 | 65 | 63.734 | ENSMZEG00005004679 | hfm1 | 97 | 65.316 | Maylandia_zebra |
| ENSG00000162669 | HFM1 | 99 | 37.671 | ENSMGAG00000008437 | HFM1 | 98 | 77.423 | Meleagris_gallopavo |
| ENSG00000162669 | HFM1 | 100 | 78.125 | ENSMAUG00000018858 | Hfm1 | 100 | 78.125 | Mesocricetus_auratus |
| ENSG00000162669 | HFM1 | 100 | 88.673 | ENSMICG00000037935 | HFM1 | 100 | 88.673 | Microcebus_murinus |
| ENSG00000162669 | HFM1 | 100 | 76.319 | ENSMOCG00000014812 | Hfm1 | 100 | 76.319 | Microtus_ochrogaster |
| ENSG00000162669 | HFM1 | 62 | 64.350 | ENSMMOG00000006148 | hfm1 | 96 | 64.426 | Mola_mola |
| ENSG00000162669 | HFM1 | 65 | 64.354 | ENSMALG00000002401 | hfm1 | 96 | 65.618 | Monopterus_albus |
| ENSG00000162669 | HFM1 | 98 | 68.382 | MGP_CAROLIEiJ_G0027496 | Hfm1 | 100 | 71.964 | Mus_caroli |
| ENSG00000162669 | HFM1 | 100 | 76.773 | ENSMUSG00000043410 | Hfm1 | 100 | 76.773 | Mus_musculus |
| ENSG00000162669 | HFM1 | 100 | 76.982 | MGP_PahariEiJ_G0017268 | Hfm1 | 100 | 76.982 | Mus_pahari |
| ENSG00000162669 | HFM1 | 100 | 76.426 | MGP_SPRETEiJ_G0028495 | Hfm1 | 100 | 76.426 | Mus_spretus |
| ENSG00000162669 | HFM1 | 100 | 82.222 | ENSMPUG00000004594 | HFM1 | 100 | 82.222 | Mustela_putorius_furo |
| ENSG00000162669 | HFM1 | 100 | 83.761 | ENSMLUG00000010200 | HFM1 | 100 | 83.761 | Myotis_lucifugus |
| ENSG00000162669 | HFM1 | 65 | 60.557 | ENSNBRG00000002910 | hfm1 | 97 | 65.697 | Neolamprologus_brichardi |
| ENSG00000162669 | HFM1 | 100 | 97.674 | ENSNLEG00000010285 | HFM1 | 100 | 93.946 | Nomascus_leucogenys |
| ENSG00000162669 | HFM1 | 73 | 86.087 | ENSMEUG00000015788 | HFM1 | 84 | 66.954 | Notamacropus_eugenii |
| ENSG00000162669 | HFM1 | 84 | 78.675 | ENSOPRG00000013916 | HFM1 | 84 | 78.675 | Ochotona_princeps |
| ENSG00000162669 | HFM1 | 100 | 70.504 | ENSODEG00000006243 | - | 100 | 79.318 | Octodon_degus |
| ENSG00000162669 | HFM1 | 71 | 62.500 | ENSONIG00000010590 | hfm1 | 99 | 62.452 | Oreochromis_niloticus |
| ENSG00000162669 | HFM1 | 100 | 75.362 | ENSOCUG00000010974 | - | 95 | 77.519 | Oryctolagus_cuniculus |
| ENSG00000162669 | HFM1 | 57 | 66.052 | ENSORLG00000026844 | hfm1 | 99 | 66.052 | Oryzias_latipes |
| ENSG00000162669 | HFM1 | 85 | 49.274 | ENSORLG00020002951 | hfm1 | 96 | 49.355 | Oryzias_latipes_hni |
| ENSG00000162669 | HFM1 | 89 | 52.261 | ENSOMEG00000016474 | hfm1 | 90 | 52.261 | Oryzias_melastigma |
| ENSG00000162669 | HFM1 | 100 | 91.304 | ENSOGAG00000032369 | HFM1 | 100 | 88.762 | Otolemur_garnettii |
| ENSG00000162669 | HFM1 | 100 | 85.357 | ENSOARG00000015812 | HFM1 | 100 | 85.357 | Ovis_aries |
| ENSG00000162669 | HFM1 | 100 | 100.000 | ENSPPAG00000024582 | HFM1 | 100 | 99.698 | Pan_paniscus |
| ENSG00000162669 | HFM1 | 100 | 86.250 | ENSPPRG00000003270 | HFM1 | 100 | 86.250 | Panthera_pardus |
| ENSG00000162669 | HFM1 | 100 | 86.319 | ENSPTIG00000018881 | HFM1 | 100 | 86.319 | Panthera_tigris_altaica |
| ENSG00000162669 | HFM1 | 100 | 100.000 | ENSPTRG00000000948 | HFM1 | 100 | 99.303 | Pan_troglodytes |
| ENSG00000162669 | HFM1 | 100 | 96.725 | ENSPANG00000009838 | HFM1 | 100 | 96.725 | Papio_anubis |
| ENSG00000162669 | HFM1 | 62 | 67.416 | ENSPKIG00000003810 | hfm1 | 95 | 67.754 | Paramormyrops_kingsleyae |
| ENSG00000162669 | HFM1 | 58 | 66.264 | ENSPMGG00000011059 | hfm1 | 100 | 66.264 | Periophthalmus_magnuspinnatus |
| ENSG00000162669 | HFM1 | 100 | 80.320 | ENSPEMG00000022852 | Hfm1 | 100 | 80.320 | Peromyscus_maniculatus_bairdii |
| ENSG00000162669 | HFM1 | 100 | 66.979 | ENSPCIG00000014233 | HFM1 | 100 | 66.979 | Phascolarctos_cinereus |
| ENSG00000162669 | HFM1 | 70 | 62.642 | ENSPFOG00000017194 | hfm1 | 99 | 62.642 | Poecilia_formosa |
| ENSG00000162669 | HFM1 | 71 | 64.654 | ENSPLAG00000000571 | hfm1 | 92 | 64.654 | Poecilia_latipinna |
| ENSG00000162669 | HFM1 | 71 | 64.306 | ENSPMEG00000019475 | hfm1 | 92 | 64.306 | Poecilia_mexicana |
| ENSG00000162669 | HFM1 | 70 | 63.744 | ENSPREG00000007803 | hfm1 | 93 | 66.868 | Poecilia_reticulata |
| ENSG00000162669 | HFM1 | 100 | 98.328 | ENSPPYG00000001163 | HFM1 | 100 | 98.328 | Pongo_abelii |
| ENSG00000162669 | HFM1 | 84 | 73.438 | ENSPCAG00000004289 | - | 74 | 82.883 | Procavia_capensis |
| ENSG00000162669 | HFM1 | 100 | 86.957 | ENSPCOG00000026252 | - | 100 | 75.053 | Propithecus_coquereli |
| ENSG00000162669 | HFM1 | 100 | 80.435 | ENSPVAG00000009713 | HFM1 | 100 | 78.079 | Pteropus_vampyrus |
| ENSG00000162669 | HFM1 | 65 | 63.519 | ENSPNYG00000001795 | hfm1 | 97 | 65.197 | Pundamilia_nyererei |
| ENSG00000162669 | HFM1 | 59 | 67.494 | ENSPNAG00000010865 | hfm1 | 84 | 67.494 | Pygocentrus_nattereri |
| ENSG00000162669 | HFM1 | 100 | 76.356 | ENSRNOG00000023299 | Hfm1 | 100 | 76.356 | Rattus_norvegicus |
| ENSG00000162669 | HFM1 | 100 | 93.478 | ENSRBIG00000033899 | - | 99 | 95.075 | Rhinopithecus_bieti |
| ENSG00000162669 | HFM1 | 100 | 96.655 | ENSRROG00000045569 | HFM1 | 100 | 96.655 | Rhinopithecus_roxellana |
| ENSG00000162669 | HFM1 | 100 | 91.304 | ENSSBOG00000027456 | HFM1 | 100 | 91.220 | Saimiri_boliviensis_boliviensis |
| ENSG00000162669 | HFM1 | 93 | 46.154 | ENSSHAG00000014616 | - | 98 | 71.792 | Sarcophilus_harrisii |
| ENSG00000162669 | HFM1 | 86 | 56.701 | ENSSFOG00015020129 | hfm1 | 96 | 56.701 | Scleropages_formosus |
| ENSG00000162669 | HFM1 | 62 | 64.916 | ENSSMAG00000006907 | hfm1 | 87 | 64.916 | Scophthalmus_maximus |
| ENSG00000162669 | HFM1 | 64 | 64.527 | ENSSDUG00000011424 | hfm1 | 100 | 64.527 | Seriola_dumerili |
| ENSG00000162669 | HFM1 | 65 | 64.808 | ENSSLDG00000016386 | hfm1 | 100 | 64.808 | Seriola_lalandi_dorsalis |
| ENSG00000162669 | HFM1 | 99 | 63.768 | ENSSARG00000009598 | - | 99 | 67.609 | Sorex_araneus |
| ENSG00000162669 | HFM1 | 97 | 37.410 | ENSSPUG00000003380 | - | 90 | 88.325 | Sphenodon_punctatus |
| ENSG00000162669 | HFM1 | 62 | 66.787 | ENSSPAG00000001023 | hfm1 | 100 | 66.787 | Stegastes_partitus |
| ENSG00000162669 | HFM1 | 100 | 82.155 | ENSSSCG00000006912 | HFM1 | 100 | 82.155 | Sus_scrofa |
| ENSG00000162669 | HFM1 | 66 | 75.131 | ENSTGUG00000006172 | HFM1 | 100 | 75.131 | Taeniopygia_guttata |
| ENSG00000162669 | HFM1 | 100 | 76.978 | ENSTBEG00000017533 | - | 99 | 79.381 | Tupaia_belangeri |
| ENSG00000162669 | HFM1 | 100 | 82.639 | ENSTTRG00000013933 | HFM1 | 100 | 82.639 | Tursiops_truncatus |
| ENSG00000162669 | HFM1 | 100 | 79.856 | ENSUAMG00000008754 | - | 99 | 78.994 | Ursus_americanus |
| ENSG00000162669 | HFM1 | 100 | 79.856 | ENSUMAG00000001345 | - | 100 | 82.766 | Ursus_maritimus |
| ENSG00000162669 | HFM1 | 93 | 84.235 | ENSVPAG00000011331 | HFM1 | 93 | 84.235 | Vicugna_pacos |
| ENSG00000162669 | HFM1 | 100 | 77.536 | ENSVVUG00000020760 | HFM1 | 99 | 82.865 | Vulpes_vulpes |
| ENSG00000162669 | HFM1 | 58 | 66.945 | ENSXMAG00000004178 | hfm1 | 92 | 66.945 | Xiphophorus_maculatus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000712 | resolution of meiotic recombination intermediates | - | IEA | Process |
| GO:0003676 | nucleic acid binding | - | IEA | Function |
| GO:0004386 | helicase activity | - | IEA | Function |
| GO:0005524 | ATP binding | - | IEA | Function |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PCPG | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| BRCA | |||
| CESC | |||
| COAD | |||
| MESO | |||
| PRAD | |||
| SKCM | |||
| STAD | |||
| TGCT |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| STAD | ||
| SARC | ||
| MESO | ||
| UCS | ||
| SKCM | ||
| BRCA | ||
| PAAD | ||
| UCEC | ||
| GBM | ||
| LIHC | ||
| THCA |