
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000304078 | FAM83 | PF07894.12 | 5.2e-104 | 1 | 1 |
| PID | Title | Article | Time | Author | Doi |
|---|---|---|---|---|---|
| 29915327 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000306858 | FAM83B-201 | 3167 | XM_006715022 | ENSP00000304078 | 1011 (aa) | XP_006715085 | Q5T0W9 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000168143 | rs1155750 | 6 | 54865546 | ? | Colorectal cancer | 29228715 | [NR] | 1.4334862 | EFO_0005842 |
| ENSG00000168143 | rs988913 | 6 | 54891510 | C | Menarche (age at onset) | 25231870 | [0.03-0.05] unit increase | 0.04 | EFO_0004703 |
| ENSG00000168143 | rs4715491 | 6 | 54899522 | ? | Morning vs. evening chronotype | 26835600 | EFO_0004354 | ||
| ENSG00000168143 | rs4715491 | 6 | 54899522 | ? | Blood urea nitrogen levels | 29403010 | [0.023-0.04] unit increase novel | 0.03139 | EFO_0004741 |
| ENSG00000168143 | rs4715491 | 6 | 54899522 | ? | Creatinine levels | 29403010 | [0.023-0.041] unit increase novel | 0.03202 | EFO_0004518 |
| ENSG00000168143 | rs4715491 | 6 | 54899522 | ? | Glomerular filtration rate | 29403010 | [0.025-0.043] unit decrease novel | 0.03373 | EFO_0005208 |
| ENSG00000168143 | rs1021836 | 6 | 54859047 | ? | Lung function (FEV1/FVC) | 30595370 | EFO_0004713 | ||
| ENSG00000168143 | rs924712 | 6 | 54862053 | G | Breast cancer | 29059683 | [0.017-0.041] unit increase | 0.0291 | EFO_0000305 |
| ENSG00000168143 | rs4715491 | 6 | 54899522 | G | Morning person | 30696823 | 1.0332713 | EFO_0008328 |
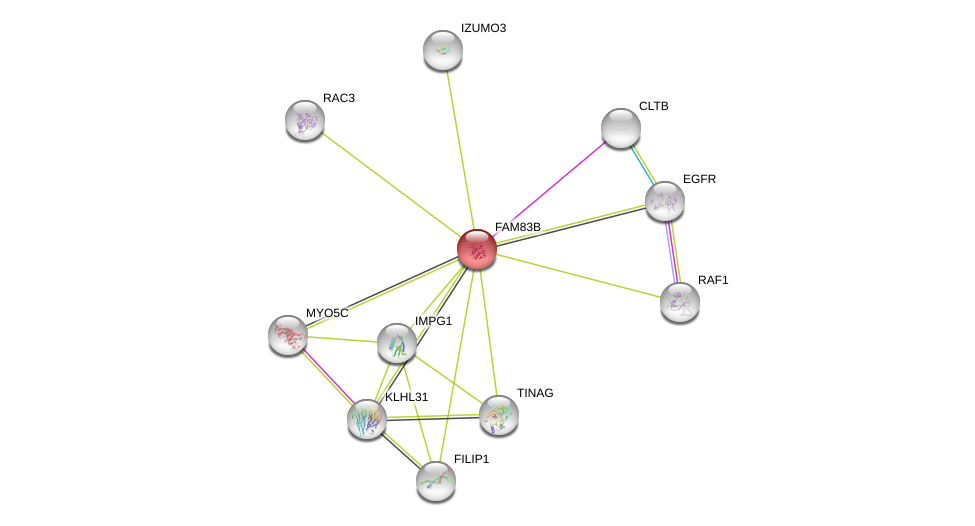
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000168143 | FAM83B | 99 | 36.184 | ENSAPOG00000020960 | fam83b | 99 | 36.808 | Acanthochromis_polyacanthus |
| ENSG00000168143 | FAM83B | 100 | 87.673 | ENSAMEG00000017444 | FAM83B | 100 | 87.673 | Ailuropoda_melanoleuca |
| ENSG00000168143 | FAM83B | 99 | 35.380 | ENSACIG00000019530 | fam83b | 99 | 34.942 | Amphilophus_citrinellus |
| ENSG00000168143 | FAM83B | 99 | 35.566 | ENSAOCG00000003874 | fam83b | 99 | 36.049 | Amphiprion_ocellaris |
| ENSG00000168143 | FAM83B | 99 | 36.038 | ENSAPEG00000017607 | fam83b | 99 | 36.056 | Amphiprion_percula |
| ENSG00000168143 | FAM83B | 99 | 35.387 | ENSATEG00000021450 | fam83b | 99 | 35.201 | Anabas_testudineus |
| ENSG00000168143 | FAM83B | 100 | 65.222 | ENSAPLG00000015482 | FAM83B | 100 | 65.318 | Anas_platyrhynchos |
| ENSG00000168143 | FAM83B | 85 | 60.633 | ENSACAG00000016759 | FAM83B | 100 | 60.747 | Anolis_carolinensis |
| ENSG00000168143 | FAM83B | 100 | 94.263 | ENSANAG00000029837 | FAM83B | 100 | 94.263 | Aotus_nancymaae |
| ENSG00000168143 | FAM83B | 99 | 34.516 | ENSACLG00000003681 | fam83b | 99 | 34.895 | Astatotilapia_calliptera |
| ENSG00000168143 | FAM83B | 99 | 35.549 | ENSAMXG00000035047 | fam83b | 99 | 35.558 | Astyanax_mexicanus |
| ENSG00000168143 | FAM83B | 99 | 83.598 | ENSBTAG00000016058 | FAM83B | 100 | 83.858 | Bos_taurus |
| ENSG00000168143 | FAM83B | 100 | 94.461 | ENSCJAG00000045233 | FAM83B | 99 | 94.461 | Callithrix_jacchus |
| ENSG00000168143 | FAM83B | 100 | 88.834 | ENSCAFG00000002327 | FAM83B | 99 | 88.834 | Canis_familiaris |
| ENSG00000168143 | FAM83B | 100 | 88.834 | ENSCAFG00020013411 | FAM83B | 100 | 88.834 | Canis_lupus_dingo |
| ENSG00000168143 | FAM83B | 99 | 83.797 | ENSCHIG00000019707 | FAM83B | 100 | 84.055 | Capra_hircus |
| ENSG00000168143 | FAM83B | 100 | 89.120 | ENSTSYG00000033366 | FAM83B | 100 | 89.120 | Carlito_syrichta |
| ENSG00000168143 | FAM83B | 100 | 80.118 | ENSCAPG00000010174 | FAM83B | 100 | 80.118 | Cavia_aperea |
| ENSG00000168143 | FAM83B | 100 | 80.020 | ENSCPOG00000030647 | FAM83B | 100 | 80.020 | Cavia_porcellus |
| ENSG00000168143 | FAM83B | 100 | 93.274 | ENSCCAG00000035242 | FAM83B | 100 | 93.274 | Cebus_capucinus |
| ENSG00000168143 | FAM83B | 100 | 97.527 | ENSCATG00000039759 | FAM83B | 100 | 97.527 | Cercocebus_atys |
| ENSG00000168143 | FAM83B | 100 | 80.610 | ENSCLAG00000010709 | FAM83B | 100 | 80.709 | Chinchilla_lanigera |
| ENSG00000168143 | FAM83B | 85 | 97.203 | ENSCSAG00000013206 | FAM83B | 100 | 97.203 | Chlorocebus_sabaeus |
| ENSG00000168143 | FAM83B | 95 | 86.618 | ENSCHOG00000007740 | FAM83B | 100 | 86.618 | Choloepus_hoffmanni |
| ENSG00000168143 | FAM83B | 89 | 63.627 | ENSCPBG00000022063 | FAM83B | 100 | 63.841 | Chrysemys_picta_bellii |
| ENSG00000168143 | FAM83B | 100 | 97.527 | ENSCANG00000004219 | FAM83B | 100 | 97.527 | Colobus_angolensis_palliatus |
| ENSG00000168143 | FAM83B | 100 | 82.115 | ENSCGRG00001020454 | Fam83b | 100 | 82.115 | Cricetulus_griseus_chok1gshd |
| ENSG00000168143 | FAM83B | 100 | 82.115 | ENSCGRG00000014543 | Fam83b | 100 | 82.115 | Cricetulus_griseus_crigri |
| ENSG00000168143 | FAM83B | 99 | 33.786 | ENSCSEG00000010249 | fam83b | 99 | 33.430 | Cynoglossus_semilaevis |
| ENSG00000168143 | FAM83B | 99 | 36.965 | ENSDARG00000078309 | fam83b | 99 | 36.673 | Danio_rerio |
| ENSG00000168143 | FAM83B | 100 | 82.510 | ENSETEG00000009535 | FAM83B | 100 | 82.510 | Echinops_telfairi |
| ENSG00000168143 | FAM83B | 100 | 87.352 | ENSEASG00005019743 | FAM83B | 100 | 87.352 | Equus_asinus_asinus |
| ENSG00000168143 | FAM83B | 100 | 87.648 | ENSECAG00000024109 | FAM83B | 100 | 87.648 | Equus_caballus |
| ENSG00000168143 | FAM83B | 77 | 85.811 | ENSEEUG00000009452 | FAM83B | 76 | 85.811 | Erinaceus_europaeus |
| ENSG00000168143 | FAM83B | 99 | 36.555 | ENSELUG00000020142 | fam83b | 99 | 36.711 | Esox_lucius |
| ENSG00000168143 | FAM83B | 100 | 88.538 | ENSFCAG00000013437 | FAM83B | 100 | 88.538 | Felis_catus |
| ENSG00000168143 | FAM83B | 100 | 64.740 | ENSFALG00000001838 | FAM83B | 100 | 65.125 | Ficedula_albicollis |
| ENSG00000168143 | FAM83B | 100 | 83.054 | ENSFDAG00000006302 | FAM83B | 100 | 83.153 | Fukomys_damarensis |
| ENSG00000168143 | FAM83B | 55 | 42.226 | ENSFHEG00000008806 | fam83b | 56 | 41.947 | Fundulus_heteroclitus |
| ENSG00000168143 | FAM83B | 55 | 40.773 | ENSGMOG00000005524 | fam83b | 94 | 55.636 | Gadus_morhua |
| ENSG00000168143 | FAM83B | 100 | 64.933 | ENSGALG00000016299 | FAM83B | 100 | 65.029 | Gallus_gallus |
| ENSG00000168143 | FAM83B | 79 | 36.663 | ENSGAFG00000007831 | fam83b | 96 | 33.756 | Gambusia_affinis |
| ENSG00000168143 | FAM83B | 100 | 63.567 | ENSGAGG00000015120 | FAM83B | 100 | 63.663 | Gopherus_agassizii |
| ENSG00000168143 | FAM83B | 100 | 99.011 | ENSGGOG00000002212 | FAM83B | 100 | 99.011 | Gorilla_gorilla |
| ENSG00000168143 | FAM83B | 99 | 34.833 | ENSHBUG00000006835 | fam83b | 99 | 34.766 | Haplochromis_burtoni |
| ENSG00000168143 | FAM83B | 100 | 83.416 | ENSHGLG00000001791 | FAM83B | 100 | 83.416 | Heterocephalus_glaber_female |
| ENSG00000168143 | FAM83B | 100 | 83.317 | ENSHGLG00100004617 | FAM83B | 100 | 83.317 | Heterocephalus_glaber_male |
| ENSG00000168143 | FAM83B | 99 | 32.853 | ENSHCOG00000015629 | fam83b | 99 | 32.981 | Hippocampus_comes |
| ENSG00000168143 | FAM83B | 99 | 36.555 | ENSIPUG00000015937 | fam83b | 99 | 36.242 | Ictalurus_punctatus |
| ENSG00000168143 | FAM83B | 100 | 88.659 | ENSSTOG00000004736 | FAM83B | 100 | 88.659 | Ictidomys_tridecemlineatus |
| ENSG00000168143 | FAM83B | 100 | 84.980 | ENSJJAG00000010325 | Fam83b | 100 | 84.980 | Jaculus_jaculus |
| ENSG00000168143 | FAM83B | 99 | 33.141 | ENSKMAG00000019582 | fam83b | 96 | 33.044 | Kryptolebias_marmoratus |
| ENSG00000168143 | FAM83B | 100 | 35.640 | ENSLBEG00000025047 | fam83b | 100 | 35.450 | Labrus_bergylta |
| ENSG00000168143 | FAM83B | 100 | 43.898 | ENSLACG00000010492 | FAM83B | 100 | 43.425 | Latimeria_chalumnae |
| ENSG00000168143 | FAM83B | 100 | 41.370 | ENSLOCG00000016902 | fam83b | 100 | 40.845 | Lepisosteus_oculatus |
| ENSG00000168143 | FAM83B | 100 | 87.154 | ENSLAFG00000011864 | FAM83B | 100 | 87.154 | Loxodonta_africana |
| ENSG00000168143 | FAM83B | 100 | 97.428 | ENSMFAG00000039244 | FAM83B | 100 | 97.428 | Macaca_fascicularis |
| ENSG00000168143 | FAM83B | 100 | 97.428 | ENSMMUG00000000815 | FAM83B | 100 | 97.428 | Macaca_mulatta |
| ENSG00000168143 | FAM83B | 100 | 97.329 | ENSMNEG00000035498 | FAM83B | 100 | 97.329 | Macaca_nemestrina |
| ENSG00000168143 | FAM83B | 100 | 97.725 | ENSMLEG00000033866 | FAM83B | 100 | 97.725 | Mandrillus_leucophaeus |
| ENSG00000168143 | FAM83B | 99 | 34.899 | ENSMAMG00000009194 | fam83b | 99 | 34.770 | Mastacembelus_armatus |
| ENSG00000168143 | FAM83B | 80 | 37.664 | ENSMZEG00005004845 | fam83b | 99 | 34.700 | Maylandia_zebra |
| ENSG00000168143 | FAM83B | 100 | 64.485 | ENSMGAG00000013914 | FAM83B | 100 | 64.581 | Meleagris_gallopavo |
| ENSG00000168143 | FAM83B | 100 | 81.522 | ENSMAUG00000021764 | Fam83b | 100 | 81.522 | Mesocricetus_auratus |
| ENSG00000168143 | FAM83B | 100 | 89.229 | ENSMICG00000036577 | FAM83B | 99 | 89.328 | Microcebus_murinus |
| ENSG00000168143 | FAM83B | 100 | 79.249 | ENSMOCG00000022341 | Fam83b | 100 | 79.249 | Microtus_ochrogaster |
| ENSG00000168143 | FAM83B | 80 | 34.450 | ENSMMOG00000013560 | fam83b | 84 | 34.450 | Mola_mola |
| ENSG00000168143 | FAM83B | 100 | 77.264 | ENSMODG00000018788 | FAM83B | 100 | 77.264 | Monodelphis_domestica |
| ENSG00000168143 | FAM83B | 99 | 34.674 | ENSMALG00000000850 | fam83b | 99 | 34.663 | Monopterus_albus |
| ENSG00000168143 | FAM83B | 100 | 81.836 | MGP_CAROLIEiJ_G0032451 | Fam83b | 100 | 81.836 | Mus_caroli |
| ENSG00000168143 | FAM83B | 100 | 81.423 | ENSMUSG00000032358 | Fam83b | 100 | 81.423 | Mus_musculus |
| ENSG00000168143 | FAM83B | 100 | 81.953 | MGP_PahariEiJ_G0015316 | Fam83b | 100 | 82.150 | Mus_pahari |
| ENSG00000168143 | FAM83B | 100 | 81.701 | MGP_SPRETEiJ_G0033590 | Fam83b | 100 | 81.701 | Mus_spretus |
| ENSG00000168143 | FAM83B | 100 | 86.957 | ENSMPUG00000002830 | FAM83B | 100 | 86.957 | Mustela_putorius_furo |
| ENSG00000168143 | FAM83B | 100 | 84.403 | ENSMLUG00000006727 | FAM83B | 100 | 84.403 | Myotis_lucifugus |
| ENSG00000168143 | FAM83B | 100 | 83.893 | ENSNGAG00000017355 | Fam83b | 100 | 83.893 | Nannospalax_galili |
| ENSG00000168143 | FAM83B | 99 | 34.582 | ENSNBRG00000012329 | fam83b | 99 | 34.962 | Neolamprologus_brichardi |
| ENSG00000168143 | FAM83B | 100 | 98.121 | ENSNLEG00000003315 | FAM83B | 100 | 98.121 | Nomascus_leucogenys |
| ENSG00000168143 | FAM83B | 88 | 84.134 | ENSOPRG00000002938 | FAM83B | 100 | 84.246 | Ochotona_princeps |
| ENSG00000168143 | FAM83B | 85 | 70.289 | ENSODEG00000001468 | FAM83B | 100 | 70.520 | Octodon_degus |
| ENSG00000168143 | FAM83B | 85 | 74.453 | ENSOANG00000013832 | FAM83B | 100 | 75.029 | Ornithorhynchus_anatinus |
| ENSG00000168143 | FAM83B | 100 | 86.166 | ENSOCUG00000003822 | FAM83B | 100 | 86.166 | Oryctolagus_cuniculus |
| ENSG00000168143 | FAM83B | 100 | 33.430 | ENSORLG00000009856 | fam83b | 100 | 33.333 | Oryzias_latipes |
| ENSG00000168143 | FAM83B | 100 | 33.333 | ENSORLG00020020592 | fam83b | 100 | 33.140 | Oryzias_latipes_hni |
| ENSG00000168143 | FAM83B | 99 | 33.138 | ENSORLG00015004455 | fam83b | 99 | 32.945 | Oryzias_latipes_hsok |
| ENSG00000168143 | FAM83B | 99 | 32.438 | ENSOMEG00000001954 | fam83b | 99 | 32.630 | Oryzias_melastigma |
| ENSG00000168143 | FAM83B | 100 | 87.068 | ENSOGAG00000013014 | FAM83B | 100 | 87.068 | Otolemur_garnettii |
| ENSG00000168143 | FAM83B | 99 | 83.897 | ENSOARG00000006650 | FAM83B | 99 | 84.154 | Ovis_aries |
| ENSG00000168143 | FAM83B | 100 | 99.209 | ENSPPAG00000028547 | FAM83B | 100 | 99.209 | Pan_paniscus |
| ENSG00000168143 | FAM83B | 100 | 88.834 | ENSPPRG00000005908 | FAM83B | 100 | 88.834 | Panthera_pardus |
| ENSG00000168143 | FAM83B | 100 | 89.032 | ENSPTIG00000007339 | FAM83B | 100 | 89.032 | Panthera_tigris_altaica |
| ENSG00000168143 | FAM83B | 100 | 99.209 | ENSPTRG00000018296 | FAM83B | 100 | 99.209 | Pan_troglodytes |
| ENSG00000168143 | FAM83B | 100 | 97.329 | ENSPANG00000024397 | FAM83B | 100 | 97.329 | Papio_anubis |
| ENSG00000168143 | FAM83B | 70 | 47.938 | ENSPKIG00000015977 | fam83b | 99 | 36.632 | Paramormyrops_kingsleyae |
| ENSG00000168143 | FAM83B | 100 | 63.860 | ENSPSIG00000011489 | FAM83B | 100 | 64.489 | Pelodiscus_sinensis |
| ENSG00000168143 | FAM83B | 99 | 32.039 | ENSPMGG00000023381 | fam83b | 99 | 31.897 | Periophthalmus_magnuspinnatus |
| ENSG00000168143 | FAM83B | 100 | 82.708 | ENSPEMG00000024281 | Fam83b | 100 | 82.708 | Peromyscus_maniculatus_bairdii |
| ENSG00000168143 | FAM83B | 100 | 78.994 | ENSPCIG00000017994 | FAM83B | 100 | 78.973 | Phascolarctos_cinereus |
| ENSG00000168143 | FAM83B | 99 | 34.236 | ENSPFOG00000009755 | fam83b | 96 | 33.815 | Poecilia_formosa |
| ENSG00000168143 | FAM83B | 55 | 43.531 | ENSPLAG00000012096 | fam83b | 59 | 43.158 | Poecilia_latipinna |
| ENSG00000168143 | FAM83B | 99 | 34.302 | ENSPMEG00000017967 | fam83b | 99 | 33.849 | Poecilia_mexicana |
| ENSG00000168143 | FAM83B | 80 | 35.511 | ENSPREG00000022212 | fam83b | 99 | 33.493 | Poecilia_reticulata |
| ENSG00000168143 | FAM83B | 100 | 98.417 | ENSPPYG00000016729 | FAM83B | 100 | 98.417 | Pongo_abelii |
| ENSG00000168143 | FAM83B | 97 | 72.533 | ENSPCAG00000016525 | FAM83B | 100 | 72.533 | Procavia_capensis |
| ENSG00000168143 | FAM83B | 100 | 83.992 | ENSPCOG00000014825 | FAM83B | 100 | 84.190 | Propithecus_coquereli |
| ENSG00000168143 | FAM83B | 100 | 86.319 | ENSPVAG00000011513 | FAM83B | 100 | 86.319 | Pteropus_vampyrus |
| ENSG00000168143 | FAM83B | 99 | 34.239 | ENSPNYG00000020645 | fam83b | 99 | 34.623 | Pundamilia_nyererei |
| ENSG00000168143 | FAM83B | 99 | 35.130 | ENSPNAG00000023843 | fam83b | 99 | 35.468 | Pygocentrus_nattereri |
| ENSG00000168143 | FAM83B | 100 | 81.818 | ENSRNOG00000011925 | Fam83b | 100 | 81.818 | Rattus_norvegicus |
| ENSG00000168143 | FAM83B | 100 | 97.626 | ENSRBIG00000043341 | FAM83B | 100 | 97.626 | Rhinopithecus_bieti |
| ENSG00000168143 | FAM83B | 100 | 97.725 | ENSRROG00000032277 | FAM83B | 100 | 97.725 | Rhinopithecus_roxellana |
| ENSG00000168143 | FAM83B | 100 | 94.065 | ENSSBOG00000024939 | FAM83B | 100 | 94.065 | Saimiri_boliviensis_boliviensis |
| ENSG00000168143 | FAM83B | 100 | 78.085 | ENSSHAG00000002718 | FAM83B | 100 | 78.085 | Sarcophilus_harrisii |
| ENSG00000168143 | FAM83B | 99 | 36.095 | ENSSFOG00015013191 | fam83b | 99 | 36.095 | Scleropages_formosus |
| ENSG00000168143 | FAM83B | 100 | 34.749 | ENSSMAG00000005786 | fam83b | 100 | 34.623 | Scophthalmus_maximus |
| ENSG00000168143 | FAM83B | 100 | 35.310 | ENSSDUG00000023285 | fam83b | 100 | 35.370 | Seriola_dumerili |
| ENSG00000168143 | FAM83B | 100 | 35.245 | ENSSLDG00000000986 | fam83b | 100 | 35.278 | Seriola_lalandi_dorsalis |
| ENSG00000168143 | FAM83B | 99 | 78.295 | ENSSARG00000003511 | FAM83B | 99 | 78.295 | Sorex_araneus |
| ENSG00000168143 | FAM83B | 100 | 64.516 | ENSSPUG00000006653 | FAM83B | 100 | 64.809 | Sphenodon_punctatus |
| ENSG00000168143 | FAM83B | 99 | 36.190 | ENSSPAG00000006245 | fam83b | 99 | 36.019 | Stegastes_partitus |
| ENSG00000168143 | FAM83B | 100 | 85.474 | ENSSSCG00000001483 | FAM83B | 100 | 85.474 | Sus_scrofa |
| ENSG00000168143 | FAM83B | 100 | 64.644 | ENSTGUG00000012844 | FAM83B | 100 | 64.836 | Taeniopygia_guttata |
| ENSG00000168143 | FAM83B | 58 | 38.564 | ENSTRUG00000025049 | fam83b | 68 | 56.643 | Takifugu_rubripes |
| ENSG00000168143 | FAM83B | 96 | 88.157 | ENSTBEG00000011451 | FAM83B | 100 | 88.157 | Tupaia_belangeri |
| ENSG00000168143 | FAM83B | 85 | 84.930 | ENSTTRG00000000745 | FAM83B | 85 | 84.930 | Tursiops_truncatus |
| ENSG00000168143 | FAM83B | 100 | 88.340 | ENSUAMG00000017718 | FAM83B | 100 | 88.340 | Ursus_americanus |
| ENSG00000168143 | FAM83B | 100 | 88.340 | ENSUMAG00000004057 | FAM83B | 100 | 88.340 | Ursus_maritimus |
| ENSG00000168143 | FAM83B | 85 | 87.131 | ENSVPAG00000010871 | FAM83B | 85 | 87.131 | Vicugna_pacos |
| ENSG00000168143 | FAM83B | 100 | 88.241 | ENSVVUG00000001201 | FAM83B | 100 | 88.241 | Vulpes_vulpes |
| ENSG00000168143 | FAM83B | 100 | 53.385 | ENSXETG00000001621 | fam83b | 100 | 53.385 | Xenopus_tropicalis |
| ENSG00000168143 | FAM83B | 99 | 33.591 | ENSXCOG00000011894 | fam83b | 99 | 33.106 | Xiphophorus_couchianus |
| ENSG00000168143 | FAM83B | 99 | 33.782 | ENSXMAG00000010212 | fam83b | 96 | 33.301 | Xiphophorus_maculatus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0004630 | phospholipase D activity | 22886302. | IDA | Function |
| GO:0005154 | epidermal growth factor receptor binding | 23912460. | IPI | Function |
| GO:0005737 | cytoplasm | 22886302. | IDA | Component |
| GO:0007173 | epidermal growth factor receptor signaling pathway | 23676467. | IDA | Process |
| GO:0007173 | epidermal growth factor receptor signaling pathway | 22886302.23912460. | IMP | Process |
| GO:0008283 | cell proliferation | 23912460. | IMP | Process |
| GO:0016020 | membrane | 22886302. | IDA | Component |
| GO:0019901 | protein kinase binding | 23676467. | IDA | Function |
| GO:0019901 | protein kinase binding | 22886302.23676467. | IPI | Function |
| GO:0036312 | phosphatidylinositol 3-kinase regulatory subunit binding | 23676467. | IPI | Function |
| GO:0036313 | phosphatidylinositol 3-kinase catalytic subunit binding | 23676467. | IPI | Function |
| PID | Title | Article | Time | Author | Doi |
|---|---|---|---|---|---|
| 22886302 |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| KIRP | |||
| LUSC |
| Cancer | P-value | Q-value |
|---|---|---|
| SKCM | ||
| KIRP | ||
| PAAD | ||
| BLCA | ||
| READ | ||
| LAML | ||
| UCEC | ||
| CHOL | ||
| LUAD | ||
| OV |