
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000329638 | zf-C2H2_jaz | PF12171.8 | 5.9e-06 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000611114 | ZNF804B-202 | 3968 | - | ENSP00000478506 | 1266 (aa) | - | A0A087WUA7 |
| ENST00000333190 | ZNF804B-201 | 4659 | - | ENSP00000329638 | 1349 (aa) | - | A4D1E1 |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000182348 | Cholesterol, LDL | 2.06263949146306E-5 | 17903299 |
| ENSG00000182348 | Cholesterol, LDL | 1.85852551080244E-6 | 17903299 |
| ENSG00000182348 | Cholesterol | 4.25827720586365E-5 | 17903299 |
| ENSG00000182348 | Cholesterol | 2.01306711045579E-7 | 17903299 |
| ENSG00000182348 | gamma-Glutamylcyclotransferase | 4.99202591892622E-5 | 17903293 |
| ENSG00000182348 | gamma-Glutamylcyclotransferase | 1.71116536366247E-6 | 17903293 |
| ENSG00000182348 | Vitamin D | 4.01745388133465E-6 | 17903293 |
| ENSG00000182348 | Stroke | 3.3069960E-005 | - |
| ENSG00000182348 | Body Weights and Measures | 8.961e-005 | 17658951 |
| ENSG00000182348 | Insulin | 7.931e-005 | - |
| ENSG00000182348 | Insulin | 5.721e-005 | - |
| ENSG00000182348 | Leukoaraiosis | 2.0223687E-005 | - |
| ENSG00000182348 | Child Development Disorders, Pervasive | 4.1000000E-005 | - |
| ENSG00000182348 | Auditory Cortex | 4E-6 | 25130324 |
| ENSG00000182348 | Hypothyroidism | 7E-6 | 22493691 |
| ENSG00000182348 | Immunoglobulins | 5E-6 | 23382691 |
| ENSG00000182348 | Body Mass Index | 9E-6 | 20966902 |
| ENSG00000182348 | Anorexia Nervosa | 2E-6 | 21079607 |
| ENSG00000182348 | Uterine Cervical Neoplasms | 9E-6 | 24700089 |
| ENSG00000182348 | Immunoglobulins | 7E-6 | 23382691 |
| ENSG00000182348 | Immunoglobulins | 6E-6 | 23382691 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000182348 | rs17301259 | 7 | 88922813 | A | Heschl's gyrus morphology | 25130324 | unit increase | 6.93 | EFO_0005852 |
| ENSG00000182348 | rs10236237 | 7 | 89065756 | T | IgG glycosylation | 23382691 | [0.092-0.23] unit decrease | 0.1613 | EFO_0005193 |
| ENSG00000182348 | rs10236237 | 7 | 89065756 | T | IgG glycosylation | 23382691 | [0.089-0.228] unit decrease | 0.1584 | EFO_0005193 |
| ENSG00000182348 | rs10236237 | 7 | 89065756 | T | IgG glycosylation | 23382691 | [0.091-0.229] unit increase | 0.16 | EFO_0005193 |
| ENSG00000182348 | rs3899697 | 7 | 88970471 | A | Cervical cancer | 24700089 | [1.449-2.621] | 1.949 | EFO_0001061 |
| ENSG00000182348 | rs6959888 | 7 | 88967071 | ? | Anorexia nervosa | 21079607 | EFO_0004215 | ||
| ENSG00000182348 | rs1406503 | 7 | 88931564 | C | Body mass index | 20966902 | [0.04-0.10] unit increase | 0.07 | EFO_0004340 |
| ENSG00000182348 | rs10248351 | 7 | 88852128 | C | Hypothyroidism | 22493691 | [1.43-2.37] | 1.843 | EFO_0004705 |
| ENSG00000182348 | rs73705514 | 7 | 88777238 | C | Logical memory (immediate recall) in mild cognitive impairment | 29274321 | [0.41-0.99] unit decrease | 0.7 | EFO_0007998|EFO_0004874 |
| ENSG00000182348 | rs73705514 | 7 | 88777238 | C | Logical memory (delayed recall) in mild cognitive impairment | 29274321 | [0.57-1.11] unit decrease | 0.84 | EFO_0007998|EFO_0004874 |
| ENSG00000182348 | rs4727189 | 7 | 88813254 | C | Smoking initiation (ever regular vs never regular) (MTAG) | 30643251 | [0.0048-0.0092] unit increase | 0.00700144 | EFO_0006527 |
| ENSG00000182348 | rs4727189 | 7 | 88813254 | C | Smoking initiation (ever regular vs never regular) | 30643251 | [0.0096-0.0201] unit increase | 0.014860439 | EFO_0006527 |
| ENSG00000182348 | rs12535041 | 7 | 88944157 | A | Breast milk fatty acid composition (maternal genotype effect) | 29514873 | [-0.8288-3.2088] unit increase | 1.19 | EFO_0005110|EFO_0009092|EFO_0005939 |
| ENSG00000182348 | rs12535041 | 7 | 88944157 | A | Breast milk fatty acid composition (maternal genotype effect) | 29514873 | [-0.8388-3.1988] unit increase | 1.18 | EFO_0005110|EFO_0009092|EFO_0005939 |
| ENSG00000182348 | rs12535041 | 7 | 88944157 | A | Breast milk fatty acid composition (infant genotype effect) | 29514873 | EFO_0005110|EFO_0007959|EFO_0009092 |
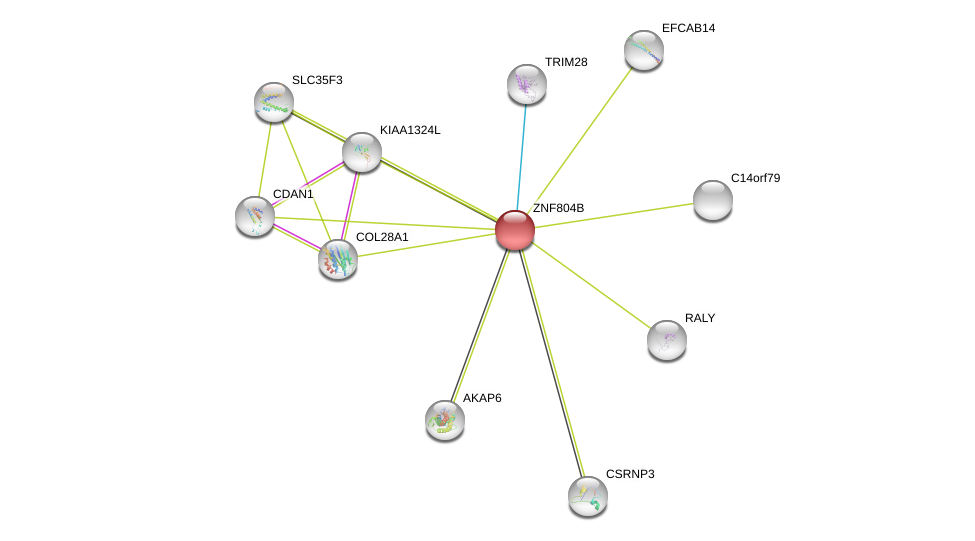
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000182348 | ZNF804B | 100 | 42.824 | ENSAPLG00000005972 | ZNF804B | 100 | 44.925 | Anas_platyrhynchos |
| ENSG00000182348 | ZNF804B | 97 | 39.605 | ENSACAG00000015927 | ZNF804B | 100 | 47.768 | Anolis_carolinensis |
| ENSG00000182348 | ZNF804B | 100 | 90.148 | ENSANAG00000035191 | ZNF804B | 100 | 90.148 | Aotus_nancymaae |
| ENSG00000182348 | ZNF804B | 100 | 73.776 | ENSBTAG00000046430 | ZNF804B | 100 | 74.581 | Bos_taurus |
| ENSG00000182348 | ZNF804B | 99 | 90.215 | ENSCJAG00000014282 | ZNF804B | 99 | 90.215 | Callithrix_jacchus |
| ENSG00000182348 | ZNF804B | 100 | 74.369 | ENSCAFG00000001862 | ZNF804B | 100 | 75.152 | Canis_familiaris |
| ENSG00000182348 | ZNF804B | 100 | 74.250 | ENSCHIG00000015623 | ZNF804B | 99 | 75.038 | Capra_hircus |
| ENSG00000182348 | ZNF804B | 100 | 80.444 | ENSTSYG00000027772 | ZNF804B | 100 | 80.444 | Carlito_syrichta |
| ENSG00000182348 | ZNF804B | 100 | 67.694 | ENSCPOG00000010946 | ZNF804B | 99 | 68.469 | Cavia_porcellus |
| ENSG00000182348 | ZNF804B | 100 | 89.704 | ENSCCAG00000019667 | ZNF804B | 100 | 89.704 | Cebus_capucinus |
| ENSG00000182348 | ZNF804B | 100 | 93.852 | ENSCATG00000021949 | ZNF804B | 100 | 93.852 | Cercocebus_atys |
| ENSG00000182348 | ZNF804B | 100 | 71.820 | ENSCLAG00000006080 | ZNF804B | 100 | 71.820 | Chinchilla_lanigera |
| ENSG00000182348 | ZNF804B | 97 | 46.627 | ENSCPBG00000021243 | ZNF804B | 98 | 47.451 | Chrysemys_picta_bellii |
| ENSG00000182348 | ZNF804B | 100 | 93.444 | ENSCANG00000031910 | ZNF804B | 100 | 93.531 | Colobus_angolensis_palliatus |
| ENSG00000182348 | ZNF804B | 100 | 67.185 | ENSCGRG00001000316 | Zfp804b | 100 | 67.185 | Cricetulus_griseus_chok1gshd |
| ENSG00000182348 | ZNF804B | 100 | 67.111 | ENSCGRG00000000160 | Zfp804b | 100 | 67.111 | Cricetulus_griseus_crigri |
| ENSG00000182348 | ZNF804B | 100 | 68.720 | ENSDORG00000025087 | Zfp804b | 100 | 69.635 | Dipodomys_ordii |
| ENSG00000182348 | ZNF804B | 77 | 100.000 | ENSETEG00000002393 | - | 76 | 96.703 | Echinops_telfairi |
| ENSG00000182348 | ZNF804B | 100 | 77.111 | ENSFCAG00000008141 | ZNF804B | 100 | 77.111 | Felis_catus |
| ENSG00000182348 | ZNF804B | 98 | 41.149 | ENSFALG00000007891 | ZNF804B | 99 | 43.452 | Ficedula_albicollis |
| ENSG00000182348 | ZNF804B | 100 | 44.444 | ENSGALG00000009004 | ZNF804B | 100 | 45.166 | Gallus_gallus |
| ENSG00000182348 | ZNF804B | 100 | 97.850 | ENSGGOG00000027270 | ZNF804B | 100 | 97.850 | Gorilla_gorilla |
| ENSG00000182348 | ZNF804B | 100 | 69.446 | ENSJJAG00000015297 | Zfp804b | 100 | 69.446 | Jaculus_jaculus |
| ENSG00000182348 | ZNF804B | 100 | 93.407 | ENSMFAG00000044325 | ZNF804B | 100 | 93.407 | Macaca_fascicularis |
| ENSG00000182348 | ZNF804B | 100 | 93.185 | ENSMNEG00000044734 | ZNF804B | 100 | 93.185 | Macaca_nemestrina |
| ENSG00000182348 | ZNF804B | 100 | 93.778 | ENSMLEG00000029354 | ZNF804B | 100 | 93.778 | Mandrillus_leucophaeus |
| ENSG00000182348 | ZNF804B | 99 | 41.436 | ENSMGAG00000008467 | ZNF804B | 99 | 43.313 | Meleagris_gallopavo |
| ENSG00000182348 | ZNF804B | 100 | 67.481 | ENSMAUG00000013056 | Zfp804b | 100 | 67.481 | Mesocricetus_auratus |
| ENSG00000182348 | ZNF804B | 100 | 80.695 | ENSMICG00000031570 | ZNF804B | 100 | 80.695 | Microcebus_murinus |
| ENSG00000182348 | ZNF804B | 100 | 66.519 | ENSMOCG00000019182 | Zfp804b | 100 | 66.519 | Microtus_ochrogaster |
| ENSG00000182348 | ZNF804B | 100 | 67.704 | MGP_CAROLIEiJ_G0026951 | Zfp804b | 100 | 67.704 | Mus_caroli |
| ENSG00000182348 | ZNF804B | 100 | 67.704 | ENSMUSG00000092094 | Zfp804b | 100 | 67.704 | Mus_musculus |
| ENSG00000182348 | ZNF804B | 100 | 66.889 | MGP_PahariEiJ_G0021724 | Zfp804b | 100 | 66.889 | Mus_pahari |
| ENSG00000182348 | ZNF804B | 100 | 66.815 | MGP_SPRETEiJ_G0027946 | Zfp804b | 100 | 66.815 | Mus_spretus |
| ENSG00000182348 | ZNF804B | 100 | 69.333 | ENSNGAG00000016523 | Zfp804b | 100 | 69.333 | Nannospalax_galili |
| ENSG00000182348 | ZNF804B | 100 | 96.444 | ENSNLEG00000015122 | ZNF804B | 100 | 96.444 | Nomascus_leucogenys |
| ENSG00000182348 | ZNF804B | 82 | 47.368 | ENSMEUG00000012422 | - | 84 | 47.368 | Notamacropus_eugenii |
| ENSG00000182348 | ZNF804B | 100 | 62.889 | ENSOPRG00000011287 | ZNF804B | 99 | 62.889 | Ochotona_princeps |
| ENSG00000182348 | ZNF804B | 100 | 74.013 | ENSOARG00000011886 | ZNF804B | 98 | 74.810 | Ovis_aries |
| ENSG00000182348 | ZNF804B | 100 | 96.998 | ENSPPAG00000030964 | ZNF804B | 100 | 97.106 | Pan_paniscus |
| ENSG00000182348 | ZNF804B | 100 | 76.963 | ENSPPRG00000009796 | ZNF804B | 99 | 76.963 | Panthera_pardus |
| ENSG00000182348 | ZNF804B | 100 | 76.667 | ENSPTIG00000016340 | ZNF804B | 99 | 76.667 | Panthera_tigris_altaica |
| ENSG00000182348 | ZNF804B | 100 | 97.628 | ENSPTRG00000019378 | ZNF804B | 100 | 97.628 | Pan_troglodytes |
| ENSG00000182348 | ZNF804B | 100 | 93.926 | ENSPANG00000017284 | ZNF804B | 100 | 93.926 | Papio_anubis |
| ENSG00000182348 | ZNF804B | 98 | 44.287 | ENSPSIG00000013424 | ZNF804B | 99 | 46.996 | Pelodiscus_sinensis |
| ENSG00000182348 | ZNF804B | 100 | 68.148 | ENSPEMG00000010520 | Zfp804b | 100 | 68.148 | Peromyscus_maniculatus_bairdii |
| ENSG00000182348 | ZNF804B | 65 | 82.692 | ENSPCAG00000010152 | - | 65 | 82.692 | Procavia_capensis |
| ENSG00000182348 | ZNF804B | 76 | 77.132 | ENSPCOG00000021437 | ZNF804B | 100 | 77.132 | Propithecus_coquereli |
| ENSG00000182348 | ZNF804B | 100 | 72.498 | ENSPVAG00000009275 | ZNF804B | 100 | 73.349 | Pteropus_vampyrus |
| ENSG00000182348 | ZNF804B | 100 | 93.602 | ENSRROG00000031123 | ZNF804B | 100 | 93.760 | Rhinopithecus_roxellana |
| ENSG00000182348 | ZNF804B | 100 | 90.296 | ENSSBOG00000018086 | ZNF804B | 100 | 90.296 | Saimiri_boliviensis_boliviensis |
| ENSG00000182348 | ZNF804B | 100 | 43.782 | ENSTGUG00000001424 | ZNF804B | 100 | 44.283 | Taeniopygia_guttata |
| ENSG00000182348 | ZNF804B | 100 | 76.593 | ENSTBEG00000007509 | ZNF804B | 100 | 76.593 | Tupaia_belangeri |
| ENSG00000182348 | ZNF804B | 100 | 79.556 | ENSTTRG00000004391 | ZNF804B | 100 | 79.556 | Tursiops_truncatus |
| ENSG00000182348 | ZNF804B | 100 | 74.074 | ENSVPAG00000009902 | ZNF804B | 100 | 74.074 | Vicugna_pacos |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0003676 | nucleic acid binding | - | IEA | Function |
| GO:0046872 | metal ion binding | - | IEA | Function |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| DLBC | |||
| PAAD | |||
| PRAD | |||
| TGCT | |||
| THCA |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| LGG | ||
| THCA |