
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000450596 | ResIII | PF04851.15 | 2.4e-18 | 1 | 1 |
| ENSP00000267430 | ResIII | PF04851.15 | 9.4e-17 | 1 | 1 |
| ENSP00000442493 | ResIII | PF04851.15 | 9.2e-13 | 1 | 1 |
| ENSP00000450596 | DEAD | PF00270.29 | 1.4e-17 | 1 | 1 |
| ENSP00000267430 | DEAD | PF00270.29 | 7.8e-17 | 1 | 1 |
| ENSP00000442493 | DEAD | PF00270.29 | 2.9e-14 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000556250 | FANCM-209 | 5577 | XM_011537037 | ENSP00000452033 | 1564 (aa) | XP_011535339 | H0YJS3 |
| ENST00000553551 | FANCM-203 | 603 | - | - | - (aa) | - | - |
| ENST00000542564 | FANCM-202 | 6167 | XM_011537035 | ENSP00000442493 | 2022 (aa) | XP_011535337 | Q8IYD8 |
| ENST00000267430 | FANCM-201 | 7111 | XM_011537034 | ENSP00000267430 | 2048 (aa) | XP_011535336 | Q8IYD8 |
| ENST00000554809 | FANCM-205 | 3112 | - | ENSP00000450632 | 1016 (aa) | - | H0YJ14 |
| ENST00000557110 | FANCM-210 | 638 | - | ENSP00000451846 | 135 (aa) | - | H0YJN7 |
| ENST00000554030 | FANCM-204 | 917 | - | - | - (aa) | - | - |
| ENST00000555013 | FANCM-206 | 573 | - | - | - (aa) | - | - |
| ENST00000555484 | FANCM-207 | 448 | - | ENSP00000450797 | 106 (aa) | - | H0YJ45 |
| ENST00000556036 | FANCM-208 | 2354 | - | ENSP00000450596 | 669 (aa) | - | Q8IYD8 |
| Pathway ID | Pathway Name | Source |
|---|---|---|
| hsa03460 | Fanconi anemia pathway | KEGG |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000187790 | Platelet Function Tests | 1.9154700E-005 | - |
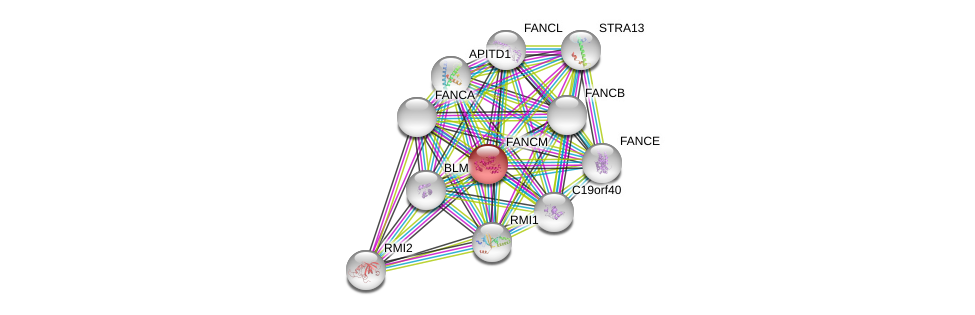
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000187790 | FANCM | 55 | 55.035 | ENSAPOG00000014274 | - | 96 | 55.035 | Acanthochromis_polyacanthus |
| ENSG00000187790 | FANCM | 99 | 90.462 | ENSAMEG00000002114 | FANCM | 99 | 79.825 | Ailuropoda_melanoleuca |
| ENSG00000187790 | FANCM | 97 | 64.977 | ENSACIG00000005444 | - | 96 | 64.688 | Amphilophus_citrinellus |
| ENSG00000187790 | FANCM | 96 | 58.873 | ENSATEG00000012412 | - | 77 | 54.734 | Anabas_testudineus |
| ENSG00000187790 | FANCM | 99 | 95.359 | ENSANAG00000025075 | FANCM | 99 | 91.752 | Aotus_nancymaae |
| ENSG00000187790 | FANCM | 97 | 58.520 | ENSACLG00000016008 | - | 70 | 54.566 | Astatotilapia_calliptera |
| ENSG00000187790 | FANCM | 97 | 58.832 | ENSAMXG00000020275 | - | 89 | 54.142 | Astyanax_mexicanus |
| ENSG00000187790 | FANCM | 99 | 89.021 | ENSBTAG00000002612 | FANCM | 95 | 89.888 | Bos_taurus |
| ENSG00000187790 | FANCM | 99 | 95.060 | ENSCJAG00000015945 | FANCM | 99 | 90.386 | Callithrix_jacchus |
| ENSG00000187790 | FANCM | 99 | 89.671 | ENSCAFG00000014062 | FANCM | 99 | 79.309 | Canis_familiaris |
| ENSG00000187790 | FANCM | 100 | 89.088 | ENSCAFG00020022069 | - | 100 | 89.088 | Canis_lupus_dingo |
| ENSG00000187790 | FANCM | 99 | 88.427 | ENSCHIG00000015176 | FANCM | 99 | 75.948 | Capra_hircus |
| ENSG00000187790 | FANCM | 88 | 93.581 | ENSTSYG00000036497 | - | 88 | 93.581 | Carlito_syrichta |
| ENSG00000187790 | FANCM | 100 | 84.604 | ENSCPOG00000001446 | FANCM | 99 | 71.373 | Cavia_porcellus |
| ENSG00000187790 | FANCM | 99 | 95.509 | ENSCCAG00000026593 | FANCM | 99 | 83.650 | Cebus_capucinus |
| ENSG00000187790 | FANCM | 99 | 97.156 | ENSCATG00000031379 | FANCM | 99 | 94.632 | Cercocebus_atys |
| ENSG00000187790 | FANCM | 99 | 97.754 | ENSCSAG00000015308 | FANCM | 99 | 94.924 | Chlorocebus_sabaeus |
| ENSG00000187790 | FANCM | 89 | 92.553 | ENSCHOG00000000190 | FANCM | 81 | 85.799 | Choloepus_hoffmanni |
| ENSG00000187790 | FANCM | 99 | 72.100 | ENSCPBG00000015089 | FANCM | 100 | 50.327 | Chrysemys_picta_bellii |
| ENSG00000187790 | FANCM | 99 | 97.754 | ENSCANG00000029498 | FANCM | 99 | 94.046 | Colobus_angolensis_palliatus |
| ENSG00000187790 | FANCM | 99 | 84.871 | ENSCGRG00001023573 | Fancm | 99 | 65.938 | Cricetulus_griseus_chok1gshd |
| ENSG00000187790 | FANCM | 97 | 58.403 | ENSCSEG00000002313 | - | 73 | 52.626 | Cynoglossus_semilaevis |
| ENSG00000187790 | FANCM | 86 | 65.972 | ENSCVAG00000015579 | - | 68 | 60.494 | Cyprinodon_variegatus |
| ENSG00000187790 | FANCM | 99 | 88.244 | ENSDNOG00000007697 | FANCM | 99 | 76.246 | Dasypus_novemcinctus |
| ENSG00000187790 | FANCM | 98 | 83.891 | ENSDORG00000010095 | Fancm | 99 | 67.591 | Dipodomys_ordii |
| ENSG00000187790 | FANCM | 82 | 85.500 | ENSETEG00000003360 | FANCM | 81 | 84.091 | Echinops_telfairi |
| ENSG00000187790 | FANCM | 99 | 86.140 | ENSEASG00005007781 | FANCM | 99 | 85.606 | Equus_asinus_asinus |
| ENSG00000187790 | FANCM | 99 | 86.438 | ENSECAG00000018694 | FANCM | 87 | 76.591 | Equus_caballus |
| ENSG00000187790 | FANCM | 88 | 78.571 | ENSEEUG00000005607 | - | 90 | 75.510 | Erinaceus_europaeus |
| ENSG00000187790 | FANCM | 91 | 64.204 | ENSELUG00000015761 | - | 72 | 59.921 | Esox_lucius |
| ENSG00000187790 | FANCM | 100 | 89.583 | ENSFCAG00000022146 | - | 99 | 89.717 | Felis_catus |
| ENSG00000187790 | FANCM | 89 | 67.608 | ENSFALG00000001703 | FANCM | 78 | 64.335 | Ficedula_albicollis |
| ENSG00000187790 | FANCM | 99 | 87.145 | ENSFDAG00000009043 | FANCM | 99 | 72.736 | Fukomys_damarensis |
| ENSG00000187790 | FANCM | 82 | 72.868 | ENSFHEG00000006371 | - | 90 | 71.111 | Fundulus_heteroclitus |
| ENSG00000187790 | FANCM | 96 | 62.346 | ENSGMOG00000002019 | - | 75 | 56.159 | Gadus_morhua |
| ENSG00000187790 | FANCM | 87 | 72.483 | ENSGALG00000031182 | FANCM | 91 | 54.329 | Gallus_gallus |
| ENSG00000187790 | FANCM | 96 | 60.823 | ENSGACG00000009448 | - | 81 | 48.148 | Gasterosteus_aculeatus |
| ENSG00000187790 | FANCM | 52 | 62.117 | ENSGAGG00000007068 | - | 93 | 63.989 | Gopherus_agassizii |
| ENSG00000187790 | FANCM | 100 | 98.730 | ENSGGOG00000008546 | FANCM | 100 | 98.730 | Gorilla_gorilla |
| ENSG00000187790 | FANCM | 97 | 58.380 | ENSHBUG00000007085 | - | 84 | 54.452 | Haplochromis_burtoni |
| ENSG00000187790 | FANCM | 90 | 97.895 | ENSHGLG00000013787 | FANCM | 99 | 74.951 | Heterocephalus_glaber_female |
| ENSG00000187790 | FANCM | 90 | 97.895 | ENSHGLG00100006377 | FANCM | 99 | 74.903 | Heterocephalus_glaber_male |
| ENSG00000187790 | FANCM | 97 | 61.256 | ENSHCOG00000013769 | - | 97 | 60.811 | Hippocampus_comes |
| ENSG00000187790 | FANCM | 98 | 57.969 | ENSIPUG00000014629 | fancm | 88 | 56.742 | Ictalurus_punctatus |
| ENSG00000187790 | FANCM | 52 | 56.174 | ENSKMAG00000009391 | - | 99 | 56.174 | Kryptolebias_marmoratus |
| ENSG00000187790 | FANCM | 97 | 58.956 | ENSLBEG00000004982 | - | 69 | 55.569 | Labrus_bergylta |
| ENSG00000187790 | FANCM | 99 | 69.507 | ENSLACG00000007739 | FANCM | 99 | 46.516 | Latimeria_chalumnae |
| ENSG00000187790 | FANCM | 99 | 64.758 | ENSLOCG00000011318 | FANCM | 91 | 58.480 | Lepisosteus_oculatus |
| ENSG00000187790 | FANCM | 99 | 87.073 | ENSLAFG00000001136 | FANCM | 100 | 77.024 | Loxodonta_africana |
| ENSG00000187790 | FANCM | 99 | 97.305 | ENSMFAG00000000383 | FANCM | 99 | 94.632 | Macaca_fascicularis |
| ENSG00000187790 | FANCM | 99 | 97.305 | ENSMMUG00000016513 | FANCM | 99 | 94.583 | Macaca_mulatta |
| ENSG00000187790 | FANCM | 99 | 97.305 | ENSMNEG00000038659 | FANCM | 99 | 94.680 | Macaca_nemestrina |
| ENSG00000187790 | FANCM | 97 | 93.939 | ENSMLEG00000035743 | FANCM | 99 | 93.750 | Mandrillus_leucophaeus |
| ENSG00000187790 | FANCM | 97 | 58.832 | ENSMAMG00000007087 | - | 77 | 55.774 | Mastacembelus_armatus |
| ENSG00000187790 | FANCM | 97 | 58.520 | ENSMZEG00005004644 | - | 70 | 54.566 | Maylandia_zebra |
| ENSG00000187790 | FANCM | 99 | 77.610 | ENSMAUG00000015450 | Fancm | 99 | 62.938 | Mesocricetus_auratus |
| ENSG00000187790 | FANCM | 99 | 91.467 | ENSMICG00000005811 | FANCM | 99 | 82.708 | Microcebus_murinus |
| ENSG00000187790 | FANCM | 99 | 81.392 | ENSMOCG00000008775 | Fancm | 99 | 62.458 | Microtus_ochrogaster |
| ENSG00000187790 | FANCM | 87 | 63.481 | ENSMMOG00000010215 | - | 68 | 59.178 | Mola_mola |
| ENSG00000187790 | FANCM | 98 | 75.187 | ENSMODG00000007334 | FANCM | 98 | 55.469 | Monodelphis_domestica |
| ENSG00000187790 | FANCM | 52 | 55.610 | ENSMALG00000013187 | - | 94 | 55.610 | Monopterus_albus |
| ENSG00000187790 | FANCM | 99 | 82.934 | MGP_CAROLIEiJ_G0017791 | Fancm | 99 | 64.286 | Mus_caroli |
| ENSG00000187790 | FANCM | 99 | 82.335 | ENSMUSG00000055884 | Fancm | 98 | 82.335 | Mus_musculus |
| ENSG00000187790 | FANCM | 99 | 78.838 | MGP_PahariEiJ_G0029547 | Fancm | 99 | 63.387 | Mus_pahari |
| ENSG00000187790 | FANCM | 99 | 82.335 | MGP_SPRETEiJ_G0018636 | Fancm | 99 | 64.303 | Mus_spretus |
| ENSG00000187790 | FANCM | 99 | 90.611 | ENSMPUG00000004849 | FANCM | 99 | 78.184 | Mustela_putorius_furo |
| ENSG00000187790 | FANCM | 99 | 86.607 | ENSMLUG00000006671 | FANCM | 100 | 77.279 | Myotis_lucifugus |
| ENSG00000187790 | FANCM | 99 | 82.934 | ENSNGAG00000017199 | Fancm | 99 | 69.238 | Nannospalax_galili |
| ENSG00000187790 | FANCM | 99 | 98.653 | ENSNLEG00000004432 | FANCM | 99 | 96.096 | Nomascus_leucogenys |
| ENSG00000187790 | FANCM | 90 | 72.632 | ENSMEUG00000004977 | - | 67 | 73.729 | Notamacropus_eugenii |
| ENSG00000187790 | FANCM | 97 | 64.427 | ENSONIG00000003531 | - | 95 | 51.691 | Oreochromis_niloticus |
| ENSG00000187790 | FANCM | 90 | 78.947 | ENSOANG00000013997 | FANCM | 99 | 53.166 | Ornithorhynchus_anatinus |
| ENSG00000187790 | FANCM | 99 | 90.719 | ENSOCUG00000007539 | FANCM | 99 | 77.257 | Oryctolagus_cuniculus |
| ENSG00000187790 | FANCM | 97 | 58.873 | ENSORLG00020013516 | - | 73 | 54.798 | Oryzias_latipes_hni |
| ENSG00000187790 | FANCM | 97 | 58.815 | ENSORLG00015012100 | - | 73 | 54.630 | Oryzias_latipes_hsok |
| ENSG00000187790 | FANCM | 97 | 60.545 | ENSOMEG00000010717 | - | 75 | 56.280 | Oryzias_melastigma |
| ENSG00000187790 | FANCM | 98 | 90.137 | ENSOGAG00000003015 | FANCM | 100 | 77.178 | Otolemur_garnettii |
| ENSG00000187790 | FANCM | 99 | 88.576 | ENSOARG00000009429 | FANCM | 99 | 76.142 | Ovis_aries |
| ENSG00000187790 | FANCM | 100 | 98.926 | ENSPPAG00000028944 | FANCM | 100 | 98.926 | Pan_paniscus |
| ENSG00000187790 | FANCM | 100 | 88.988 | ENSPPRG00000011952 | - | 99 | 89.121 | Panthera_pardus |
| ENSG00000187790 | FANCM | 100 | 88.839 | ENSPTIG00000018621 | - | 99 | 88.972 | Panthera_tigris_altaica |
| ENSG00000187790 | FANCM | 100 | 98.863 | ENSPTRG00000006307 | FANCM | 100 | 98.863 | Pan_troglodytes |
| ENSG00000187790 | FANCM | 99 | 97.605 | ENSPANG00000023200 | FANCM | 99 | 94.632 | Papio_anubis |
| ENSG00000187790 | FANCM | 52 | 59.398 | ENSPKIG00000000861 | - | 92 | 59.148 | Paramormyrops_kingsleyae |
| ENSG00000187790 | FANCM | 99 | 83.735 | ENSPEMG00000005619 | Fancm | 99 | 64.210 | Peromyscus_maniculatus_bairdii |
| ENSG00000187790 | FANCM | 100 | 74.891 | ENSPCIG00000005354 | - | 99 | 75.036 | Phascolarctos_cinereus |
| ENSG00000187790 | FANCM | 97 | 62.481 | ENSPFOG00000002008 | - | 77 | 63.333 | Poecilia_formosa |
| ENSG00000187790 | FANCM | 97 | 59.944 | ENSPLAG00000014164 | - | 76 | 56.083 | Poecilia_latipinna |
| ENSG00000187790 | FANCM | 97 | 59.212 | ENSPMEG00000010746 | - | 76 | 55.954 | Poecilia_mexicana |
| ENSG00000187790 | FANCM | 97 | 59.379 | ENSPREG00000019849 | - | 83 | 55.504 | Poecilia_reticulata |
| ENSG00000187790 | FANCM | 99 | 98.204 | ENSPPYG00000005781 | FANCM | 99 | 97.387 | Pongo_abelii |
| ENSG00000187790 | FANCM | 90 | 85.263 | ENSPCAG00000011363 | - | 64 | 84.127 | Procavia_capensis |
| ENSG00000187790 | FANCM | 90 | 92.632 | ENSPCOG00000014388 | FANCM | 99 | 81.647 | Propithecus_coquereli |
| ENSG00000187790 | FANCM | 88 | 90.043 | ENSPVAG00000015802 | FANCM | 71 | 90.043 | Pteropus_vampyrus |
| ENSG00000187790 | FANCM | 97 | 54.597 | ENSPNAG00000013558 | - | 80 | 50.408 | Pygocentrus_nattereri |
| ENSG00000187790 | FANCM | 99 | 81.764 | ENSRNOG00000056721 | Fancm | 100 | 71.914 | Rattus_norvegicus |
| ENSG00000187790 | FANCM | 99 | 95.970 | ENSRBIG00000011451 | FANCM | 99 | 93.857 | Rhinopithecus_bieti |
| ENSG00000187790 | FANCM | 99 | 97.305 | ENSRROG00000028917 | FANCM | 99 | 94.632 | Rhinopithecus_roxellana |
| ENSG00000187790 | FANCM | 85 | 31.220 | YIR002C | - | 60 | 31.270 | Saccharomyces_cerevisiae |
| ENSG00000187790 | FANCM | 99 | 95.060 | ENSSBOG00000030882 | FANCM | 99 | 90.874 | Saimiri_boliviensis_boliviensis |
| ENSG00000187790 | FANCM | 99 | 73.977 | ENSSHAG00000000507 | FANCM | 100 | 54.531 | Sarcophilus_harrisii |
| ENSG00000187790 | FANCM | 96 | 58.449 | ENSSMAG00000019903 | - | 99 | 55.990 | Scophthalmus_maximus |
| ENSG00000187790 | FANCM | 96 | 62.481 | ENSSDUG00000016682 | - | 95 | 62.519 | Seriola_dumerili |
| ENSG00000187790 | FANCM | 96 | 59.212 | ENSSLDG00000003408 | - | 77 | 48.749 | Seriola_lalandi_dorsalis |
| ENSG00000187790 | FANCM | 89 | 84.783 | ENSSARG00000002618 | FANCM | 82 | 84.950 | Sorex_araneus |
| ENSG00000187790 | FANCM | 99 | 87.592 | ENSSSCG00000005000 | FANCM | 99 | 77.762 | Sus_scrofa |
| ENSG00000187790 | FANCM | 89 | 70.957 | ENSTGUG00000013226 | - | 100 | 68.501 | Taeniopygia_guttata |
| ENSG00000187790 | FANCM | 96 | 62.597 | ENSTRUG00000009756 | - | 95 | 62.328 | Takifugu_rubripes |
| ENSG00000187790 | FANCM | 98 | 63.459 | ENSTNIG00000017277 | - | 100 | 39.401 | Tetraodon_nigroviridis |
| ENSG00000187790 | FANCM | 99 | 89.072 | ENSTTRG00000006669 | FANCM | 99 | 79.737 | Tursiops_truncatus |
| ENSG00000187790 | FANCM | 99 | 89.104 | ENSUMAG00000007704 | - | 97 | 89.104 | Ursus_maritimus |
| ENSG00000187790 | FANCM | 90 | 96.842 | ENSVPAG00000005763 | FANCM | 73 | 90.571 | Vicugna_pacos |
| ENSG00000187790 | FANCM | 99 | 89.222 | ENSVVUG00000000357 | FANCM | 99 | 79.346 | Vulpes_vulpes |
| ENSG00000187790 | FANCM | 70 | 68.590 | ENSXETG00000003046 | fancm | 100 | 68.710 | Xenopus_tropicalis |
| ENSG00000187790 | FANCM | 98 | 59.384 | ENSXMAG00000007702 | - | 76 | 55.000 | Xiphophorus_maculatus |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000712 | resolution of meiotic recombination intermediates | 20347428. | IMP | Process |
| GO:0003677 | DNA binding | - | IEA | Function |
| GO:0003682 | chromatin binding | 20347429. | IDA | Function |
| GO:0004518 | nuclease activity | - | IEA | Function |
| GO:0005515 | protein binding | 17289582.20347429.25416956. | IPI | Function |
| GO:0005524 | ATP binding | - | IEA | Function |
| GO:0005654 | nucleoplasm | - | IDA | Component |
| GO:0005654 | nucleoplasm | - | TAS | Component |
| GO:0031297 | replication fork processing | 20347428. | IMP | Process |
| GO:0032508 | DNA duplex unwinding | - | IEA | Process |
| GO:0036297 | interstrand cross-link repair | - | TAS | Process |
| GO:0043140 | ATP-dependent 3'-5' DNA helicase activity | - | IEA | Function |
| GO:0043240 | Fanconi anaemia nuclear complex | 20347428.20347429. | IDA | Component |
| GO:0071821 | FANCM-MHF complex | 20347428. | IDA | Component |
| GO:0090305 | nucleic acid phosphodiester bond hydrolysis | - | IEA | Process |
| GO:1902527 | positive regulation of protein monoubiquitination | 29231814. | IMP | Process |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| ACC | |||||||
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LAML | |||||||
| LAML | |||||||
| LAML | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PCPG | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| TGCT | |||||||
| TGCT | |||||||
| THCA | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UCS | |||||||
| UVM |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| ACC | |||
| CHOL | |||
| KIRP | |||
| PAAD |
| Cancer | P-value | Q-value |
|---|---|---|
| THYM | ||
| KIRC | ||
| SARC | ||
| ACC | ||
| SKCM | ||
| PRAD | ||
| LUSC | ||
| ESCA | ||
| PCPG | ||
| KICH | ||
| LIHC | ||
| LGG |