
| Protein ID | Domain | Pfam ID | E-value | Domain number | Total number |
|---|---|---|---|---|---|
| ENSP00000354794 | zf-C2H2 | PF00096.26 | 6.7e-51 | 1 | 4 |
| ENSP00000354794 | zf-C2H2 | PF00096.26 | 6.7e-51 | 2 | 4 |
| ENSP00000354794 | zf-C2H2 | PF00096.26 | 6.7e-51 | 3 | 4 |
| ENSP00000354794 | zf-C2H2 | PF00096.26 | 6.7e-51 | 4 | 4 |
| ENSP00000440768 | zf-C2H2 | PF00096.26 | 6.7e-51 | 1 | 4 |
| ENSP00000440768 | zf-C2H2 | PF00096.26 | 6.7e-51 | 2 | 4 |
| ENSP00000440768 | zf-C2H2 | PF00096.26 | 6.7e-51 | 3 | 4 |
| ENSP00000440768 | zf-C2H2 | PF00096.26 | 6.7e-51 | 4 | 4 |
| ENSP00000463000 | zf-C2H2 | PF00096.26 | 2.5e-43 | 1 | 2 |
| ENSP00000463000 | zf-C2H2 | PF00096.26 | 2.5e-43 | 2 | 2 |
| ENSP00000462724 | zf-C2H2 | PF00096.26 | 1.5e-13 | 1 | 2 |
| ENSP00000462724 | zf-C2H2 | PF00096.26 | 1.5e-13 | 2 | 2 |
| ENSP00000463748 | zf-C2H2 | PF00096.26 | 5e-06 | 1 | 1 |
| ENSP00000463000 | zf-met | PF12874.7 | 0.00098 | 1 | 3 |
| ENSP00000463000 | zf-met | PF12874.7 | 0.00098 | 2 | 3 |
| ENSP00000463000 | zf-met | PF12874.7 | 0.00098 | 3 | 3 |
| ENSP00000463748 | zf-met | PF12874.7 | 0.0014 | 1 | 1 |
| Transcript ID | Name | Length | RefSeq ID | Protein ID | Length | RefSeq ID | UniportKB ID |
|---|---|---|---|---|---|---|---|
| ENST00000538137 | ZNF521-203 | 4253 | - | ENSP00000440768 | 1311 (aa) | - | Q96K83 |
| ENST00000580488 | ZNF521-209 | 547 | - | ENSP00000464415 | 144 (aa) | - | J3QRW6 |
| ENST00000577775 | ZNF521-206 | 552 | - | ENSP00000463748 | 184 (aa) | - | J3QQI2 |
| ENST00000577461 | ZNF521-204 | 338 | - | ENSP00000462746 | 30 (aa) | - | J3KT07 |
| ENST00000584787 | ZNF521-214 | 4327 | XM_011525911 | ENSP00000463000 | 1091 (aa) | XP_011524213 | J3KTI4 |
| ENST00000583005 | ZNF521-212 | 541 | - | - | - (aa) | - | - |
| ENST00000399425 | ZNF521-202 | 4345 | XM_011525910 | ENSP00000382352 | 1244 (aa) | XP_011524212 | H7BYU6 |
| ENST00000581869 | ZNF521-210 | 531 | - | - | - (aa) | - | - |
| ENST00000577720 | ZNF521-205 | 555 | - | - | - (aa) | - | - |
| ENST00000583398 | ZNF521-213 | 406 | - | - | - (aa) | - | - |
| ENST00000361524 | ZNF521-201 | 4871 | XM_011525909 | ENSP00000354794 | 1311 (aa) | XP_011524211 | Q96K83 |
| ENST00000582584 | ZNF521-211 | 590 | - | - | - (aa) | - | - |
| ENST00000577801 | ZNF521-207 | 694 | - | ENSP00000462724 | 224 (aa) | - | J3KSZ4 |
| ENST00000579111 | ZNF521-208 | 594 | - | - | - (aa) | - | - |
| ensgID | Trait | pValue | Pubmed ID |
|---|---|---|---|
| ENSG00000198795 | Hip | 1.18922840174945E-11 | 17903296 |
| ENSG00000198795 | Hip | 9.642024058532E-7 | 17903296 |
| ENSG00000198795 | Personality Inventory | 4.226e-005 | - |
| ENSG00000198795 | Personality | 6.213e-005 | - |
| ENSG00000198795 | Personality | 6.213e-005 | - |
| ENSG00000198795 | Waist-Hip Ratio | 6.7520000E-005 | - |
| ENSG00000198795 | Waist-Hip Ratio | 6.8680000E-005 | - |
| ENSG00000198795 | Leukoaraiosis | 4.2911674E-005 | - |
| ENSG00000198795 | Leukoaraiosis | 5.9559630E-005 | - |
| ENSG00000198795 | Platelet Function Tests | 4.5500000E-006 | - |
| ENSG00000198795 | Platelet Function Tests | 8.5100000E-007 | - |
| ENSG00000198795 | Platelet Function Tests | 4.5500000E-006 | - |
| ENSG00000198795 | Platelet Function Tests | 3.3800000E-006 | - |
| ENSG00000198795 | Child Development Disorders, Pervasive | 1.8000000E-005 | - |
| ENSG00000198795 | Receptors, Interleukin-6 | 3.5470000E-006 | - |
| ENSG00000198795 | Cholesterol, LDL | 7.9510000E-005 | - |
| ENSG00000198795 | Periodontitis | 5E-6 | 24024966 |
| ENSG00000198795 | DNA, Mitochondrial | 3E-6 | 25240745 |
| ENSG00000198795 | Polychlorinated Biphenyls | 9E-7 | 25839716 |
| ENSG00000198795 | Urinary Incontinence | 2E-7 | 25524241 |
| ENSG00000198795 | Selenium | 8E-6 | 25343990 |
| ENSG00000198795 | Motor Activity | 3E-6 | 23251661 |
| ENSG00000198795 | Motor Activity | 5E-6 | 23251661 |
| ENSG00000198795 | Motor Activity | 2E-6 | 23251661 |
| ENSG00000198795 | Anticonvulsants | 6E-6 | 22379998 |
| ENSG00000198795 | Arthritis, Juvenile | 2E-6 | 27927641 |
| ENSG00000198795 | Schizophrenia | 4E-6 | 26198764 |
| ENSG00000198795 | Electrocardiography | 2E-8 | 27958378 |
| ENSG00000198795 | Sulfonylurea Compounds | 2E-8 | 27958378 |
| ENSG00000198795 | Body Weight | 3E-7 | 19851299 |
| ensgID | SNP | Chromosome | Position | SNP-risk | Trait | PubmedID | 95% CI | Or or BEAT | EFO ID |
|---|---|---|---|---|---|---|---|---|---|
| ENSG00000198795 | rs4133168 | 18 | 25232544 | ? | Mitochondrial DNA levels | 25240745 | [NR] | EFO_0006312 | |
| ENSG00000198795 | rs72881251 | 18 | 25094696 | ? | Urgency urinary incontinence | 25524241 | [1.29-1.75] | 1.5 | EFO_0006865 |
| ENSG00000198795 | rs9957365 | 18 | 25072853 | A | Highest math class taken | 30038396 | [0.0086-0.0184] unit increase | 0.0135 | EFO_0004875 |
| ENSG00000198795 | rs9957365 | 18 | 25072853 | A | Self-reported math ability (MTAG) | 30038396 | [0.0085-0.0163] unit increase | 0.0124 | EFO_0004875 |
| ENSG00000198795 | rs9957365 | 18 | 25072853 | A | Highest math class taken (MTAG) | 30038396 | [0.011-0.018] unit increase | 0.0141 | EFO_0004875 |
| ENSG00000198795 | rs8083432 | 18 | 25151396 | ? | Adverse response to lamotrigine and phenytoin | 22379998 | GO_0036277 | ||
| ENSG00000198795 | rs188885834 | 18 | 25187295 | ? | Reaction time | 29844566 | [0.0047-0.0116] unit increase | 0.0081264 | EFO_0008393 |
| ENSG00000198795 | rs150021505 | 18 | 25331015 | ? | Reaction time | 29844566 | [0.0048-0.0117] unit increase | 0.0082287 | EFO_0008393 |
| ENSG00000198795 | rs12962845 | 18 | 25074138 | C | Educational attainment (years of education) | 30038396 | [0.0082-0.0164] unit decrease | 0.0123 | EFO_0004784 |
| ENSG00000198795 | rs12961565 | 18 | 25282547 | ? | Balding type 1 | 30595370 | EFO_0007825 | ||
| ENSG00000198795 | rs11663772 | 18 | 25280882 | C | Male-pattern baldness | 30573740 | [0.031-0.052] unit decrease | 0.041154 | EFO_0007825 |
| ENSG00000198795 | rs8089996 | 18 | 25068541 | A | Educational attainment (years of education) | 30038396 | [0.0095-0.0149] unit decrease | 0.0122 | EFO_0004784 |
| ENSG00000198795 | rs62082230 | 18 | 25096107 | ? | Systolic blood pressure | 30595370 | EFO_0006335 | ||
| ENSG00000198795 | rs72881254 | 18 | 25099226 | A | Smoking initiation (ever regular vs never regular) (MTAG) | 30643251 | [0.0056-0.0116] unit increase | 0.0085785 | EFO_0006527 |
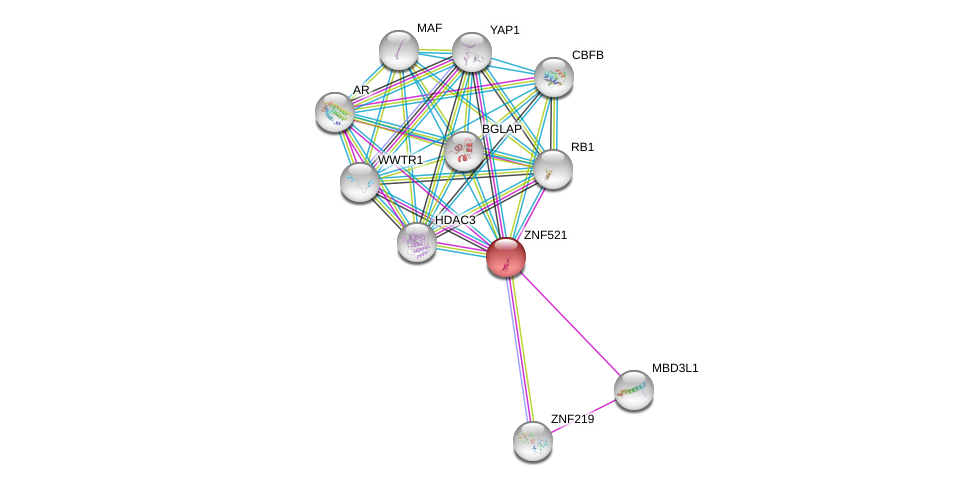
| Ensembl ID | Gene Symbol | Coverage | Identiy | Ortholog | Gene Symbol | Coverage | Identiy | Species |
|---|---|---|---|---|---|---|---|---|
| ENSG00000198795 | ZNF521 | 100 | 100.000 | ENSAMEG00000014151 | ZNF521 | 100 | 99.085 | Ailuropoda_melanoleuca |
| ENSG00000198795 | ZNF521 | 100 | 95.796 | ENSAPLG00000003518 | - | 100 | 96.167 | Anas_platyrhynchos |
| ENSG00000198795 | ZNF521 | 100 | 91.831 | ENSACAG00000001799 | ZNF521 | 100 | 91.523 | Anolis_carolinensis |
| ENSG00000198795 | ZNF521 | 100 | 100.000 | ENSCJAG00000020691 | ZNF521 | 100 | 99.619 | Callithrix_jacchus |
| ENSG00000198795 | ZNF521 | 100 | 99.107 | ENSCLAG00000010565 | ZNF521 | 100 | 98.780 | Chinchilla_lanigera |
| ENSG00000198795 | ZNF521 | 98 | 96.072 | ENSCPBG00000027365 | - | 100 | 96.072 | Chrysemys_picta_bellii |
| ENSG00000198795 | ZNF521 | 99 | 68.267 | ENSDARG00000116769 | ZNF521 | 97 | 69.529 | Danio_rerio |
| ENSG00000198795 | ZNF521 | 100 | 99.083 | ENSEASG00005005129 | ZNF521 | 100 | 99.083 | Equus_asinus_asinus |
| ENSG00000198795 | ZNF521 | 100 | 95.967 | ENSFALG00000006065 | ZNF521 | 100 | 93.195 | Ficedula_albicollis |
| ENSG00000198795 | ZNF521 | 100 | 98.167 | ENSFDAG00000016560 | ZNF521 | 100 | 98.150 | Fukomys_damarensis |
| ENSG00000198795 | ZNF521 | 100 | 97.768 | ENSGALG00000015112 | ZNF521 | 100 | 93.491 | Gallus_gallus |
| ENSG00000198795 | ZNF521 | 100 | 96.875 | ENSGAGG00000018451 | ZNF521 | 100 | 95.314 | Gopherus_agassizii |
| ENSG00000198795 | ZNF521 | 100 | 86.917 | ENSLACG00000007021 | ZNF521 | 100 | 87.893 | Latimeria_chalumnae |
| ENSG00000198795 | ZNF521 | 100 | 98.992 | ENSLAFG00000013445 | ZNF521 | 100 | 98.924 | Loxodonta_africana |
| ENSG00000198795 | ZNF521 | 100 | 99.725 | ENSMMUG00000008600 | ZNF521 | 100 | 99.756 | Macaca_mulatta |
| ENSG00000198795 | ZNF521 | 100 | 94.358 | ENSMGAG00000010352 | ZNF521 | 99 | 94.358 | Meleagris_gallopavo |
| ENSG00000198795 | ZNF521 | 100 | 96.975 | ENSMODG00000021509 | ZNF521 | 100 | 95.868 | Monodelphis_domestica |
| ENSG00000198795 | ZNF521 | 100 | 90.758 | ENSMLUG00000009484 | ZNF521 | 100 | 91.960 | Myotis_lucifugus |
| ENSG00000198795 | ZNF521 | 100 | 98.214 | ENSOANG00000009055 | ZNF521 | 99 | 92.295 | Ornithorhynchus_anatinus |
| ENSG00000198795 | ZNF521 | 99 | 97.043 | ENSOARG00000007246 | ZNF521 | 100 | 96.025 | Ovis_aries |
| ENSG00000198795 | ZNF521 | 100 | 99.633 | ENSPANG00000024017 | ZNF521 | 100 | 99.633 | Papio_anubis |
| ENSG00000198795 | ZNF521 | 100 | 95.967 | ENSPSIG00000002538 | ZNF521 | 100 | 94.591 | Pelodiscus_sinensis |
| ENSG00000198795 | ZNF521 | 100 | 99.107 | ENSPCIG00000020692 | ZNF521 | 100 | 96.820 | Phascolarctos_cinereus |
| ENSG00000198795 | ZNF521 | 99 | 98.754 | ENSPVAG00000015426 | ZNF521 | 100 | 98.907 | Pteropus_vampyrus |
| ENSG00000198795 | ZNF521 | 100 | 97.344 | ENSRNOG00000016874 | Zfp521 | 100 | 97.344 | Rattus_norvegicus |
| ENSG00000198795 | ZNF521 | 100 | 97.067 | ENSSHAG00000018217 | ZNF521 | 100 | 97.067 | Sarcophilus_harrisii |
| ENSG00000198795 | ZNF521 | 99 | 76.697 | ENSSFOG00015007599 | ZNF521 | 96 | 76.567 | Scleropages_formosus |
| ENSG00000198795 | ZNF521 | 100 | 81.086 | ENSSFOG00015010128 | ZNF521 | 99 | 82.381 | Scleropages_formosus |
| ENSG00000198795 | ZNF521 | 100 | 96.875 | ENSTGUG00000010575 | ZNF521 | 100 | 94.086 | Taeniopygia_guttata |
| Go ID | Go_term | PubmedID | Evidence | Category |
|---|---|---|---|---|
| GO:0000981 | DNA-binding transcription factor activity, RNA polymerase II-specific | - | ISA | Function |
| GO:0003677 | DNA binding | 21873635. | IBA | Function |
| GO:0005634 | nucleus | 21873635. | IBA | Component |
| GO:0005634 | nucleus | 12393497. | IDA | Component |
| GO:0006357 | regulation of transcription by RNA polymerase II | - | IEA | Process |
| GO:0019904 | protein domain specific binding | 11984006. | IPI | Function |
| GO:0046872 | metal ion binding | - | IEA | Function |
| GO:0048663 | neuron fate commitment | - | IEA | Process |
| Cancer | Chr | Position | Mutation Type | dbSNP | Protein-change | Allele Freq | RBD |
|---|---|---|---|---|---|---|---|
| ACC | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BLCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| BRCA | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CESC | |||||||
| CHOL | |||||||
| CHOL | |||||||
| CHOL | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| COAD | |||||||
| DLBC | |||||||
| DLBC | |||||||
| DLBC | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| ESCA | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| GBM | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| HNSC | |||||||
| KICH | |||||||
| KICH | |||||||
| KICH | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRC | |||||||
| KIRP | |||||||
| KIRP | |||||||
| KIRP | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LGG | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LIHC | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUAD | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| LUSC | |||||||
| MESO | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| OV | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PAAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| PRAD | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| READ | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SARC | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| SKCM | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| STAD | |||||||
| THCA | |||||||
| THCA | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC | |||||||
| UCEC |
| Cancer | Type | Freq | Q-value |
|---|---|---|---|
| LUAD |
| Cancer | P-value | Q-value |
|---|---|---|
| KIRC | ||
| STAD | ||
| SARC | ||
| ACC | ||
| UCS | ||
| HNSC | ||
| KIRP | ||
| PAAD | ||
| BLCA | ||
| LIHC | ||
| DLBC | ||
| LGG | ||
| THCA |